+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | ATP and DNA bound SMC5/6 core complex | |||||||||
 マップデータ マップデータ | Primary map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Nse1 / Nse3 / Nse4 / Smc5 / Smc6 / Nse2 / ATP / DNA BINDING PROTEIN-DNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Smc5-Smc6 complex / resolution of DNA recombination intermediates / chromosome separation / DNA double-strand break attachment to nuclear envelope / Platelet degranulation / SUMOylation of DNA damage response and repair proteins / chromatin looping / regulation of telomere maintenance / recombinational repair / double-strand break repair via homologous recombination ...Smc5-Smc6 complex / resolution of DNA recombination intermediates / chromosome separation / DNA double-strand break attachment to nuclear envelope / Platelet degranulation / SUMOylation of DNA damage response and repair proteins / chromatin looping / regulation of telomere maintenance / recombinational repair / double-strand break repair via homologous recombination / single-stranded DNA binding / site of double-strand break / damaged DNA binding / chromosome, telomeric region / DNA repair / ATP hydrolysis activity / mitochondrion / ATP binding / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.8 Å | |||||||||
 データ登録者 データ登録者 | Yu Y / Patel DJ | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2022 ジャーナル: Proc Natl Acad Sci U S A / 年: 2022タイトル: Cryo-EM structure of DNA-bound Smc5/6 reveals DNA clamping enabled by multi-subunit conformational changes. 著者: You Yu / Shibai Li / Zheng Ser / Huihui Kuang / Thane Than / Danying Guan / Xiaolan Zhao / Dinshaw J Patel /   要旨: Structural maintenance of chromosomes (SMC) complexes are essential for chromatin organization and functions throughout the cell cycle. The cohesin and condensin SMCs fold and tether DNA, while ...Structural maintenance of chromosomes (SMC) complexes are essential for chromatin organization and functions throughout the cell cycle. The cohesin and condensin SMCs fold and tether DNA, while Smc5/6 directly promotes DNA replication and repair. The functions of SMCs rely on their abilities to engage DNA, but how Smc5/6 binds and translocates on DNA remains largely unknown. Here, we present a 3.8 Å cryogenic electron microscopy (cryo-EM) structure of DNA-bound Saccharomyces cerevisiae Smc5/6 complex containing five of its core subunits, including Smc5, Smc6, and the Nse1-3-4 subcomplex. Intricate interactions among these subunits support the formation of a clamp that encircles the DNA double helix. The positively charged inner surface of the clamp contacts DNA in a nonsequence-specific manner involving numerous DNA binding residues from four subunits. The DNA duplex is held up by Smc5 and 6 head regions and positioned between their coiled-coil arm regions, reflecting an engaged-head and open-arm configuration. The Nse3 subunit secures the DNA from above, while the hook-shaped Nse4 kleisin forms a scaffold connecting DNA and all other subunits. The Smc5/6 DNA clamp shares similarities with DNA-clamps formed by other SMCs but also exhibits differences that reflect its unique functions. Mapping cross-linking mass spectrometry data derived from DNA-free Smc5/6 to the DNA-bound Smc5/6 structure identifies multi-subunit conformational changes that enable DNA capture. Finally, mutational data from cells reveal distinct DNA binding contributions from each subunit to Smc5/6 chromatin association and cell fitness. In summary, our integrative study illuminates how a unique SMC complex engages DNA in supporting genome regulation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26140.map.gz emd_26140.map.gz | 6.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26140-v30.xml emd-26140-v30.xml emd-26140.xml emd-26140.xml | 21 KB 21 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_26140.png emd_26140.png | 50.9 KB | ||
| Filedesc metadata |  emd-26140.cif.gz emd-26140.cif.gz | 8.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26140 http://ftp.pdbj.org/pub/emdb/structures/EMD-26140 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26140 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26140 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7tveMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26140.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26140.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Primary map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.069 Å | ||||||||||||||||||||||||||||||||||||
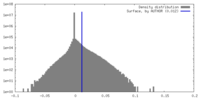
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Hexamer complex of Smc5-Smc6-Nse1-Nse3-Nse4-Nse2 with ATP and DNA
| 全体 | 名称: Hexamer complex of Smc5-Smc6-Nse1-Nse3-Nse4-Nse2 with ATP and DNA |
|---|---|
| 要素 |
|
-超分子 #1: Hexamer complex of Smc5-Smc6-Nse1-Nse3-Nse4-Nse2 with ATP and DNA
| 超分子 | 名称: Hexamer complex of Smc5-Smc6-Nse1-Nse3-Nse4-Nse2 with ATP and DNA タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#7 / 詳細: Smc5 E1015Q mutation and Smc6 E1048Q mutation |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 410 KDa |
-分子 #1: DNA (68-MER)
| 分子 | 名称: DNA (68-MER) / タイプ: dna / ID: 1 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 21.253111 KDa |
| 配列 | 文字列: (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA) (DA)(DA)(DA)(DA)(DA) ...文字列: (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA)(DA) (DA)(DA)(DA)(DA)(DA)(DA)(DA) (DA) |
-分子 #2: DNA (78-MER)
| 分子 | 名称: DNA (78-MER) / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 23.682055 KDa |
| 配列 | 文字列: (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT) (DT)(DT)(DT)(DT)(DT) ...文字列: (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT)(DT) (DT) |
-分子 #3: Non-structural maintenance of chromosomes element 1
| 分子 | 名称: Non-structural maintenance of chromosomes element 1 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO / EC番号: RING-type E3 ubiquitin transferase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 38.437395 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MEVHEEHVSA PVTGDATAKY LLQYILSARG ICHENALILA LMRLETDAST LNTEWSIQQW VDKLNDYINA INVKLNLLGY KIIRINHGI GRNAVTLKAK QNFESFEDNT AIRAHDNDYA VLQSIVLPES NRFFVYVNLA STEETKLATR FNQNEIEFIK W AIEQFMIS ...文字列: MEVHEEHVSA PVTGDATAKY LLQYILSARG ICHENALILA LMRLETDAST LNTEWSIQQW VDKLNDYINA INVKLNLLGY KIIRINHGI GRNAVTLKAK QNFESFEDNT AIRAHDNDYA VLQSIVLPES NRFFVYVNLA STEETKLATR FNQNEIEFIK W AIEQFMIS GETIVEGPAL DTSIIVREVN RILVAATGDS NLAKWRKFST FTVGSTNLFQ FQELTATDIE DLLLRLCELK WF YRTQEGK FGIDLRCIAE LEEYLTSMYN LNTCQNCHKL AIQGVRCGNE SCREENEETG ENSLSQIWHV DCFKHYITHV SKN CDRCGS SLITEGVYVI G UniProtKB: UNIPROTKB: A0A7I9FFW3 |
-分子 #4: Structural maintenance of chromosomes protein 6
| 分子 | 名称: Structural maintenance of chromosomes protein 6 / タイプ: protein_or_peptide / ID: 4 / 詳細: Smc6(E1048Q)-2XStrep / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 132.445078 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MISTTISGKR PIEQVDDELL SLTAQQENEE QQQQRKRRRH QFAPMTQFNS NTLDEDSGFR SSSDVATADQ DNFLEESPSG YIKKVILRN FMCHEHFELE LGSRLNFIVG NNGSGKSAIL TAITIGLGAK ASETNRGSSL KDLIREGCYS AKIILHLDNS K YGAYQQGI ...文字列: MISTTISGKR PIEQVDDELL SLTAQQENEE QQQQRKRRRH QFAPMTQFNS NTLDEDSGFR SSSDVATADQ DNFLEESPSG YIKKVILRN FMCHEHFELE LGSRLNFIVG NNGSGKSAIL TAITIGLGAK ASETNRGSSL KDLIREGCYS AKIILHLDNS K YGAYQQGI FGNEIIVERI IKRDGPASFS LRSENGKEIS NKKKDIQTVV DYFSVPVSNP MCFLSQDAAR SFLTASTSQD KY SHFMKGT LLQEITENLL YASAIHDSAQ ENMALHLENL KSLKAEYEDA KKLLRELNQT SDLNERKMLL QAKSLWIDVA HNT DACKNL ENEISGIQQK VDEVTEKIRN RQEKIERYTS DGTTIEAQID AKVIYVNEKD SEHQNARELL RDVKSRFEKE KSNQ AEAQS NIDQGRKKVD ALNKTIAHLE EELTKEMGGD KDQMRQELEQ LEKANEKLRE VNNSLVVSLQ DVKNEERDIQ HERES ELRT ISRSIQNKKV ELQNIAKGND TFLMNFDRNM DRLLRTIEQR KNEFETPAIG PLGSLVTIRK GFEKWTRSIQ RAISSS LNA FVVSNPKDNR LFRDIMRSCG IRSNIPIVTY CLSQFDYSKG RAHGNYPTIV DALEFSKPEI ECLFVDLSRI ERIVLIE DK NEARNFLQRN PVNVNMALSL RDRRSGFQLS GGYRLDTVTY QDKIRLKVNS SSDNGTQYLK DLIEQETKEL QNIRDRYE E KLSEVRSRLK EIDGRLKSTK NEMRKTNFRM TELKMNVGKV VDTGILNSKI NERKNQEQAI ASYEAAKEEL GLKIEQIAQ EAQPIKEQYD STKLALVEAQ DELQQLKEDI NSRQSKIQKY KDDTIYYEDK KKVYLENIKK IEVNVAALKE GIQRQIQNAC AFCSKERIE NVDLPDTQEE IKRELDKVSR MIQKAEKSLG LSQEEVIALF EKCRNKYKEG QKKYMEIDEA LNRLHNSLKA R DQNYKNAE KGTCFDADMD FRASLKVRKF SGNLSFIKDT KSLEIYILTT NDEKARNVDT LSGGEKSFSQ MALLLATWKP MR SRIIALD QFDVFMDQVN RKIGTTLIVK KLKDIARTQT IIITPQDIGK IADIDSSGVS IHRMRDPERQ NNSNFYNGSL EVL FQGPGG SSAWSHPQFE KGGGSGGGSG GGSWSHPQFE K UniProtKB: Structural maintenance of chromosomes protein 6 |
-分子 #5: Structural maintenance of chromosomes protein 5
| 分子 | 名称: Structural maintenance of chromosomes protein 5 / タイプ: protein_or_peptide / ID: 5 / 詳細: Smc5 (E1015Q) / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 126.293234 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTSLIDLGRY VERTHHGEDT EPRSKRVKIA KPDLSSFQPG SIIKIRLQDF VTYTLTEFNL SPSLNMIIGP NGSGKSTFVC AVCLGLAGK PEYIGRSKKV EDFIKNGQDV SKIEITLKNS PNVTDIEYID ARDETIKITR IITRSKRRSD YLINDYQVSE S VVKTLVAQ ...文字列: MTSLIDLGRY VERTHHGEDT EPRSKRVKIA KPDLSSFQPG SIIKIRLQDF VTYTLTEFNL SPSLNMIIGP NGSGKSTFVC AVCLGLAGK PEYIGRSKKV EDFIKNGQDV SKIEITLKNS PNVTDIEYID ARDETIKITR IITRSKRRSD YLINDYQVSE S VVKTLVAQ LNIQLDNLCQ FLSQERVEEF ARLKSVKLLV ETIRSIDASL LDVLDELREL QGNEQSLQKD LDFKKAKIVH LR QESDKLR KSVESLRDFQ NKKGEIELHS QLLPYVKVKD HKEKLNIYKE EYERAKANLR AILKDKKPFA NTKKTLENQV EEL TEKCSL KTDEFLKAKE KINEIFEKLN TIRDEVIKKK NQNEYYRGRT KKLQATIIST KEDFLRSQEI LAQTHLPEKS VFED IDIKR KEIINKEGEI RDLISEIDAK ANAINHEMRS IQRQAESKTK SLTTTDKIGI LNQDQDLKEV RDAVLMVREH PEMKD KILE PPIMTVSAIN AQFAAYLAQC VDYNTSKALT VVDSDSYKLF ANPILDKFKV NLRELSSADT TPPVPAETVR DLGFEG YLS DFITGDKRVM KMLCQTSKIH TIPVSRRELT PAQIKKLITP RPNGKILFKR IIHGNRLVDI KQSAYGSKQV FPTDVSI KQ TNFYQGSIMS NEQKIRIENE IINLKNEYND RKSTLDALSN QKSGYRHELS ELASKNDDIN REAHQLNEIR KKYTMRKS T IETLREKLDQ LKREARKDVS QKIKDIDDQI QQLLLKQRHL LSKMASSMKS LKNCQKELIS TQILQFEAQN MDVSMNDVI GFFNEREADL KSQYEDKKKF VKEMRDTPEF QSWMREIRSY DQDTKEKLNK VAEKYEEEGN FNLSFVQDVL DKLESEIAMV NHDESAVTI LDQVTAELRE LEHTVPQQSK DLETIKAKLK EDHAVLEPKL DDIVSKISAR FARLFNNVGS AGAVRLEKPK D YAEWKIEI MVKFRDNAPL KKLDSHTQSG GERAVSTVLY MIALQEFTSA PFRVVDQINQ GMDSRNERIV HKAMVENACA EN TSQYFLI TPKLLTGLHY HEKMRIHCVM AGSWIPNPSE DPKMIHFGET SNYSFDG UniProtKB: Structural maintenance of chromosomes protein 5 |
-分子 #6: Non-structural maintenance of chromosome element 3
| 分子 | 名称: Non-structural maintenance of chromosome element 3 / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 34.193777 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MMSSIDNDSD VDLTEDLAVA KIVKENPVAR KMVRYILSRG ESQNSIITRN KLQSVIHEAA REENIAKPSF SKMFMDINAI LYNVYGFEL QGLPSKNNMN AGGNGSNSNT NKSMPEPLGH RAQKFILLNN VPHSKNFDDF KILQSAHTYE ELIVTGEYIG D DIASGTSN ...文字列: MMSSIDNDSD VDLTEDLAVA KIVKENPVAR KMVRYILSRG ESQNSIITRN KLQSVIHEAA REENIAKPSF SKMFMDINAI LYNVYGFEL QGLPSKNNMN AGGNGSNSNT NKSMPEPLGH RAQKFILLNN VPHSKNFDDF KILQSAHTYE ELIVTGEYIG D DIASGTSN TLESKLSTDR DLVYKGVLSV ILCIVFFSKN NILHQELIKF LETFGIPSDG SKIAILNITI EDLIKSLEKR EY IVRLEEK SDTDGEVISY RIGRRTQAEL GLESLEKLVQ EIMGLEKEQT KSLHDDIIKS IGDSYSIG UniProtKB: Non-structural maintenance of chromosome element 3 |
-分子 #7: Non-structural maintenance of chromosome element 4
| 分子 | 名称: Non-structural maintenance of chromosome element 4 / タイプ: protein_or_peptide / ID: 7 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 46.252996 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSSTVISRKR RNSTVTEPDS SGETRKQKKS RSDEKSSSSK DGDPQLEFKV LQGYRDLESE MHKGRAQVTR TGDIGVAMDN LNAVDSLFN KVIGIKNNGL FAHDARAMVS ISELAQISVR NLKFDDSRSM VNLENIVNSL KRYMLKEHFK LNNIAENRND L TLAADEQS ...文字列: MSSTVISRKR RNSTVTEPDS SGETRKQKKS RSDEKSSSSK DGDPQLEFKV LQGYRDLESE MHKGRAQVTR TGDIGVAMDN LNAVDSLFN KVIGIKNNGL FAHDARAMVS ISELAQISVR NLKFDDSRSM VNLENIVNSL KRYMLKEHFK LNNIAENRND L TLAADEQS AADQQEESDG DIDRTPDDNH TDKATSSFKA TSMRHSYLQQ FSHYNEFSQF NWFRIGALYN TISKNAPITD HL MGPLSIE KKPRVLTQRR RNNDQVGEKI TAEKITQHSL NSTQQETTPE QVKKCFKKLS KKLGPEGSIN LFKFIIDPNS FSR SIENLF YTSFLIKEGK LLMEHDEEGL PTIKIKQSIS HTDSRSKEIE RQRRRAAHQN HIIFQMDMPT WRKLIKKYNI TSPF LDG UniProtKB: Non-structural maintenance of chromosome element 4 |
-分子 #8: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 8 / コピー数: 1 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 53.55 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)