+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cyanide dihydratase from Bacillus pumilus C1 E155R variant with altered helical twist. | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Left-handed helix. / HYDROLASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.8 Å | |||||||||
 データ登録者 データ登録者 | Dlamini LS / Woodward JD / Sewell BT | |||||||||
| 資金援助 |  南アフリカ, 1件 南アフリカ, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Cyanide dihydratase from Bacillus pumilus C1 E155R variant with altered helical twist 著者: Dlamini LS / Woodward JD / Sewell BT | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_19910.map.gz emd_19910.map.gz | 166.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-19910-v30.xml emd-19910-v30.xml emd-19910.xml emd-19910.xml | 16.2 KB 16.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_19910_fsc.xml emd_19910_fsc.xml | 12.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_19910.png emd_19910.png | 48.4 KB | ||
| Filedesc metadata |  emd-19910.cif.gz emd-19910.cif.gz | 6 KB | ||
| その他 |  emd_19910_half_map_1.map.gz emd_19910_half_map_1.map.gz emd_19910_half_map_2.map.gz emd_19910_half_map_2.map.gz | 139.6 MB 139.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-19910 http://ftp.pdbj.org/pub/emdb/structures/EMD-19910 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19910 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19910 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_19910_validation.pdf.gz emd_19910_validation.pdf.gz | 1.2 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_19910_full_validation.pdf.gz emd_19910_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  emd_19910_validation.xml.gz emd_19910_validation.xml.gz | 20.1 KB | 表示 | |
| CIF形式データ |  emd_19910_validation.cif.gz emd_19910_validation.cif.gz | 26.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19910 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19910 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19910 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-19910 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9er3MC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_19910.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_19910.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.825 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_19910_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
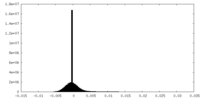
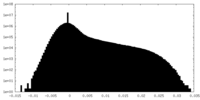
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_19910_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
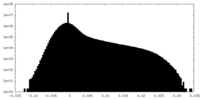
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cyanide dihydratase from Bacillus pumilus C1 E155R variant with a...
| 全体 | 名称: Cyanide dihydratase from Bacillus pumilus C1 E155R variant with altered helical twist. |
|---|---|
| 要素 |
|
-超分子 #1: Cyanide dihydratase from Bacillus pumilus C1 E155R variant with a...
| 超分子 | 名称: Cyanide dihydratase from Bacillus pumilus C1 E155R variant with altered helical twist. タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 703 KDa |
-分子 #1: Cyanide dihydratase
| 分子 | 名称: Cyanide dihydratase / タイプ: protein_or_peptide / ID: 1 / コピー数: 19 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 36.19873 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: TSIYPKFRAA AVQAAPIYLN LEASVEKSCE LIDEAASNGA KLVAFPEAFL PGYPWFAFIG HPEYTRKFYH ELYKNAVEIP SLAIQKISE AAKRNETYVC ISCSEKDGGS LYLAQLWFNP NGDLIGKHRK MRASVAERLI WGDGSGSMMP VFQTRIGNLG G LMCWEHQV ...文字列: TSIYPKFRAA AVQAAPIYLN LEASVEKSCE LIDEAASNGA KLVAFPEAFL PGYPWFAFIG HPEYTRKFYH ELYKNAVEIP SLAIQKISE AAKRNETYVC ISCSEKDGGS LYLAQLWFNP NGDLIGKHRK MRASVAERLI WGDGSGSMMP VFQTRIGNLG G LMCWEHQV PLDLMAMNAQ NEQVHVASWP GYFDDEISSR YYAIATQTFV LMTSSIYTEE MKEMICLTQE QRDYFETFKS GH TCIYGPD GEPISDMVPA ETEGIAYAEI DVERVIDYKY YIDPAGHYSN QSLSMNFNQQ PTPVVKHLNH QKNEVFTYED IQ UniProtKB: Cyanide dihydratase |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 1.8 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 濃度: 50.0 mM / 構成要素 - 式: Tris-HCl / 構成要素 - 名称: Tris-(hydroxymethyl) aminomethane / 詳細: 50 mM NaCL, 50 mM Tris-HCl |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 30 sec. / 前処理 - 雰囲気: OTHER / 前処理 - 気圧: 2.0 kPa |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK I |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 31418 / 平均露光時間: 2.04 sec. / 平均電子線量: 1.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | Chain - Source name: Other / Chain - Initial model type: other 詳細: The initial model was built ab initio using the map and amino acid sequence. |
|---|---|
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 101.248 当てはまり具合の基準: Cross-correlation coefficient |
| 得られたモデル |  PDB-9er3: |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)