+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM of Hantaan virus polymerase in hexameric state | |||||||||
 マップデータ マップデータ | HTNV-L Hexamer Apo | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Bunyavirus / Hantaan virus / polymerase / dimer / VIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA-templated viral transcription / negative stranded viral RNA replication / cap snatching / endonuclease activity / 加水分解酵素; エステル加水分解酵素 / host cell perinuclear region of cytoplasm / RNA-directed RNA polymerase / nucleotide binding / hydrolase activity / RNA-directed RNA polymerase activity ...RNA-templated viral transcription / negative stranded viral RNA replication / cap snatching / endonuclease activity / 加水分解酵素; エステル加水分解酵素 / host cell perinuclear region of cytoplasm / RNA-directed RNA polymerase / nucleotide binding / hydrolase activity / RNA-directed RNA polymerase activity / DNA-templated transcription / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Hantaan virus 76-118 (ウイルス) Hantaan virus 76-118 (ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.24 Å | |||||||||
 データ登録者 データ登録者 | Durieux Trouilleton Q / Arragain B / Malet H | |||||||||
| 資金援助 |  フランス, 1件 フランス, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Structural characterization of the oligomerization of full-length Hantaan virus polymerase into symmetric dimers and hexamers. 著者: Quentin Durieux Trouilleton / Dominique Housset / Paco Tarillon / Benoît Arragain / Hélène Malet /  要旨: Hantaan virus is a dangerous human pathogen whose segmented negative-stranded RNA genome is replicated and transcribed by a virally-encoded multi-functional polymerase. Here we describe the complete ...Hantaan virus is a dangerous human pathogen whose segmented negative-stranded RNA genome is replicated and transcribed by a virally-encoded multi-functional polymerase. Here we describe the complete cryo-electron microscopy structure of Hantaan virus polymerase in several oligomeric forms. Apo polymerase protomers can adopt two drastically different conformations, which assemble into two distinct symmetric homodimers, that can themselves gather to form hexamers. Polymerase dimerization induces the stabilization of most polymerase domains, including the C-terminal domain that contributes the most to dimer's interface, along with a lariat region that participates to the polymerase steadying. Binding to viral RNA induces significant conformational changes resulting in symmetric oligomer disruption and polymerase activation, suggesting the possible involvement of apo multimers as protecting systems that would stabilize the otherwise flexible C-terminal domains. Overall, these results provide insights into the multimerization capability of Hantavirus polymerase and may help to define antiviral compounds to counteract these life-threatening viruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_18406.map.gz emd_18406.map.gz | 651.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-18406-v30.xml emd-18406-v30.xml emd-18406.xml emd-18406.xml | 20.2 KB 20.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_18406_fsc.xml emd_18406_fsc.xml | 23.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_18406.png emd_18406.png | 71.3 KB | ||
| Filedesc metadata |  emd-18406.cif.gz emd-18406.cif.gz | 6.9 KB | ||
| その他 |  emd_18406_half_map_1.map.gz emd_18406_half_map_1.map.gz emd_18406_half_map_2.map.gz emd_18406_half_map_2.map.gz | 1.2 GB 1.2 GB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-18406 http://ftp.pdbj.org/pub/emdb/structures/EMD-18406 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18406 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18406 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_18406.map.gz / 形式: CCP4 / 大きさ: 1.3 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_18406.map.gz / 形式: CCP4 / 大きさ: 1.3 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HTNV-L Hexamer Apo | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.839 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: HTNV-L Hexamer Apo half map A
| ファイル | emd_18406_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HTNV-L Hexamer Apo half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
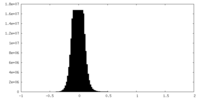
| 密度ヒストグラム |
-ハーフマップ: HTNV-L Hexamer Apo half map b
| ファイル | emd_18406_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HTNV-L Hexamer Apo half map b | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Hantaan virus polymerase
| 全体 | 名称: Hantaan virus polymerase |
|---|---|
| 要素 |
|
-超分子 #1: Hantaan virus polymerase
| 超分子 | 名称: Hantaan virus polymerase / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Hantaan virus 76-118 (ウイルス) Hantaan virus 76-118 (ウイルス) |
| 分子量 | 理論値: 1.5 MDa |
-分子 #1: Hantaan virus polymerase
| 分子 | 名称: Hantaan virus polymerase / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Hantaan virus 76-118 (ウイルス) Hantaan virus 76-118 (ウイルス) |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MGHHHHHHDY DIPTTENLYF QGMDKYREIH NKLKEFSPGT LTAVECIDYL DRLYAVRHDI VDQMIKHDWS DNKDSEEAIG KVLLFAGVPS NIITALEKKI IPNHPTGKSL KAFFKMTPDN YKISGTTIEF VEVTVTADVD KGIREKKLKY EAGLTYIEQE LHKFFLKGEI ...文字列: MGHHHHHHDY DIPTTENLYF QGMDKYREIH NKLKEFSPGT LTAVECIDYL DRLYAVRHDI VDQMIKHDWS DNKDSEEAIG KVLLFAGVPS NIITALEKKI IPNHPTGKSL KAFFKMTPDN YKISGTTIEF VEVTVTADVD KGIREKKLKY EAGLTYIEQE LHKFFLKGEI PQPYKITFNV VAVRTDGSNI TTQWPSRRND GVVQYMRLVQ AEISYVREHL IKTEERAALE AMFNLKFNIS THKSQPYYIP DYKGMEPIGA NIEDLVDYSK DWLSRARNFS FFEVKGTAVF ECFNSNEANH CQRYPMSRKP RNFLLIQCSL ITSYKPATTL SDQIDSRRAC SYILNLIPDT PASYLIHDMA YRYINLTRED MINYYAPRIQ FKQTQNVREP GTFKLTSSML RAESKAMLDL LNNHKSGEKH GAQIESLNIA SHIVQSESVS LITKILSDLE LNITEPSTQE YSTTKHTYVD TVLDKFFQNE TQKYLIDVLK KTTAWHIGHL IRDITESLIA HSGLKRSKYW SLHSYNNGNV ILFILPSKSL EVAGSFIRFI TVFRIGPGLV DKDNLDTILI DGDSQWGVSK VMSIDLNRLL ALNIAFEKAL IATATWFQYY TEDQGQFPLQ YAIRSVFANH FLLAICQKMK LCAIFDNLRY LIPAVTSLYS GFPSLIEKLF ERPFKSSLEV YIYYNIKSLL VALAQNNKAR FYSKVKLLGL TVDQSTVGAS GVYPSFMSRI VYKHYRSLIS EVTTCFFLFE KGLHGNMNEE AKIHLETVEW ALKFREKEEK YGESLVENGY MMWELRANAE LAEQQLYCQD AIELAAIELN KVLATKSSVV ANSILSKNWE EPYFSQTRNI SLKGMSGQVQ EDGHLSSSVT IIEAIRYLSN SRHNPSLLKL YEETREQKAM ARIVRKYQRT EADRGFFITT LPTRCRLEII EDYYDAIAKN ISEEYISYGG EKKILAIQGA LEKALRWASG ESFIELSNHK FIRMKRKLMY VSADATKWSP GDNSAKFRRF TSMLHNGLPN NKLKNCVIDA LKQVYKTDFF MSRKLRNYID SMESLDPHIK QFLDFFPDGH HGEVKGNWLQ GNLNKCSSLF GVAMSLLFKQ VWTNLFPELD CFFEFAHHSD DALFIYGYLE PVDDGTDWFL FVSQQIQAGH LHWFSVNTEM WKSMFNLHEH ILLLGSIKIS PKKTTVSPTN AEFLSTFFEG CAVSIPFVKI LLGSLSDLPG LGYFDDLAAA QSRCVKALDL GASPQVAQLA VALCTSKVER LYGTAPGMVN HPAAYLQVKH TDTPIPLGGN GAMSIMELAT AGIGMSDKNL LKRALLGYSH KRQKSMLYIL GLFKFLMKLS DETFQHERLG QFSFIGKVQW KIFTPKSEFE FADMYTSKFL ELWSSQHVTY DYIIPKGRDN LLIYLVRKLN DPSIVTAMTM QSPLQLRFRM QAKQHMKVCR LDGEWVTFRE VLAAANSFAE NYSATSQDMD LFQTLTSCTF SKEYAWKDFL NGIHCDVIPT KQVQRAKVAR TFTVREKDQI IQNSIPAVIG YKFAVTVEEM SDVLDTAKFP DSLSVDLKTM KDGVYRELGL DISLPDVMKR IAPMLYKSSK SRVVIVQGNV EGTAEAICRY WLKSMSLVKT IRVKPHKEVL QAVSIFNRKE DIGQQKDLAA LKLCIEVWRW CKANSAPYRD WFQALWFEDK TFSEWLDRFC RVGVPPIDPE IQCAALMIAD IKGDYSVLQL QANRRAYSGK QYDAYCVQTY NEVTKLYEGD LRVTFNFGLD CARLEIFWDK KAYILETSIT QKHVLKIMMD EVSKELIKCG MRFNTEQVQG VRHMVLFKTE SGFEWGKPNI PCIVYKNCVL RTSLRTTQAI NHKFMITIKD DGLRAIAQHD EDSPRFLLAH AFHTIRDIRY QAVDAVSNVW FIHKGVKLYL NPIISSGLLE NFMKNLPAAI PPAAYSLIMN RAKISVDLFM FNDLLKLINP RNTLDLSGLE TTGDEFSTVS SMSSRLWSEE MSLVDDDEEL DDEFTIDLQD VDFENIDIEA DIEHFLQDES SYTGDLLIST EETESKKMRG IVKILEPVRL IKSWVSRGLS IEKVYSPVNI ILMSRYISKT FNLSTKQVSL LDPYDLTELE SIVRGWGECV IDQFESLDRE AQNMVVNKGI CPEDVIPDSL FSFRHTMVLL RRLFPQDSIS SFY UniProtKB: RNA-directed RNA polymerase L |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.25 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 50 sec. / 前処理 - 雰囲気: AIR / 詳細: 25mA | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 77 K / 装置: FEI VITROBOT MARK IV / 詳細: blot force 1 3s. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum LS / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 1 / 実像数: 14650 / 平均露光時間: 1.45 sec. / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 最大 デフォーカス(補正後): 2.0 µm / 最小 デフォーカス(補正後): 0.8 µm / 倍率(補正後): 105000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A / Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL |
 ムービー
ムービー コントローラー
コントローラー


















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)