+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the SARS-CoV-2 spike glycoprotein in complex with the 87G7 antibody Fab fragment (local refinement) | ||||||||||||
 マップデータ マップデータ | DeepEMhancer sharpened map | ||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Coronavirus / Spike / Antibody / Complex / VIRAL PROTEIN | ||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
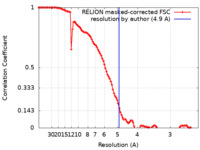
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.9 Å | ||||||||||||
 データ登録者 データ登録者 | Hurdiss DL / Drulyte I | ||||||||||||
| 資金援助 | European Union,  ドイツ, 3件 ドイツ, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Sci Immunol / 年: 2022 ジャーナル: Sci Immunol / 年: 2022タイトル: An ACE2-blocking antibody confers broad neutralization and protection against Omicron and other SARS-CoV-2 variants of concern. 著者: Wenjuan Du / Daniel L Hurdiss / Dubravka Drabek / Anna Z Mykytyn / Franziska K Kaiser / Mariana González-Hernández / Diego Muñoz-Santos / Mart M Lamers / Rien van Haperen / Wentao Li / ...著者: Wenjuan Du / Daniel L Hurdiss / Dubravka Drabek / Anna Z Mykytyn / Franziska K Kaiser / Mariana González-Hernández / Diego Muñoz-Santos / Mart M Lamers / Rien van Haperen / Wentao Li / Ieva Drulyte / Chunyan Wang / Isabel Sola / Federico Armando / Georg Beythien / Malgorzata Ciurkiewicz / Wolfgang Baumgärtner / Kate Guilfoyle / Tony Smits / Joline van der Lee / Frank J M van Kuppeveld / Geert van Amerongen / Bart L Haagmans / Luis Enjuanes / Albert D M E Osterhaus / Frank Grosveld / Berend-Jan Bosch /     要旨: The ongoing evolution of SARS-CoV-2 has resulted in the emergence of Omicron, which displays notable immune escape potential through mutations at key antigenic sites on the spike protein. Many of ...The ongoing evolution of SARS-CoV-2 has resulted in the emergence of Omicron, which displays notable immune escape potential through mutations at key antigenic sites on the spike protein. Many of these mutations localize to the spike protein ACE2 receptor binding domain, annulling the neutralizing activity of therapeutic antibodies that were effective against other variants of concern (VOCs) earlier in the pandemic. Here, we identified a receptor-blocking human monoclonal antibody, 87G7, that retained potent in vitro neutralizing activity against SARS-CoV-2 variants including the Alpha, Beta, Gamma, Delta, and Omicron (BA.1/BA.2) VOCs. Using cryo-electron microscopy and site-directed mutagenesis experiments, we showed that 87G7 targets a patch of hydrophobic residues in the ACE2-binding site that are highly conserved in SARS-CoV-2 variants, explaining its broad neutralization capacity. 87G7 protected mice and hamsters prophylactically against challenge with all current SARS-CoV-2 VOCs and showed therapeutic activity against SARS-CoV-2 challenge in both animal models. Our findings demonstrate that 87G7 holds promise as a prophylactic or therapeutic agent for COVID-19 that is more resilient to SARS-CoV-2 antigenic diversity. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14271.map.gz emd_14271.map.gz | 92.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14271-v30.xml emd-14271-v30.xml emd-14271.xml emd-14271.xml | 29.2 KB 29.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14271_fsc.xml emd_14271_fsc.xml | 10.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14271.png emd_14271.png | 70.2 KB | ||
| マスクデータ |  emd_14271_msk_1.map emd_14271_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-14271.cif.gz emd-14271.cif.gz | 7.3 KB | ||
| その他 |  emd_14271_additional_1.map.gz emd_14271_additional_1.map.gz emd_14271_additional_2.map.gz emd_14271_additional_2.map.gz emd_14271_additional_3.map.gz emd_14271_additional_3.map.gz emd_14271_half_map_1.map.gz emd_14271_half_map_1.map.gz emd_14271_half_map_2.map.gz emd_14271_half_map_2.map.gz | 60.9 MB 50.4 MB 97 MB 95.6 MB 95.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14271 http://ftp.pdbj.org/pub/emdb/structures/EMD-14271 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14271 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14271 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_14271_validation.pdf.gz emd_14271_validation.pdf.gz | 675.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_14271_full_validation.pdf.gz emd_14271_full_validation.pdf.gz | 675.4 KB | 表示 | |
| XML形式データ |  emd_14271_validation.xml.gz emd_14271_validation.xml.gz | 17.2 KB | 表示 | |
| CIF形式データ |  emd_14271_validation.cif.gz emd_14271_validation.cif.gz | 22.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14271 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14271 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14271 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14271 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14271.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14271.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | DeepEMhancer sharpened map | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.24 Å | ||||||||||||||||||||||||||||||||||||
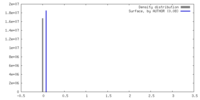
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14271_msk_1.map emd_14271_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
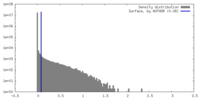
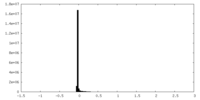
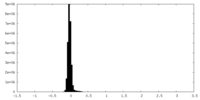
| 密度ヒストグラム |
-追加マップ: Local resolution filtered map
| ファイル | emd_14271_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Local resolution filtered map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
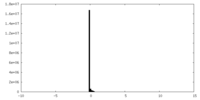
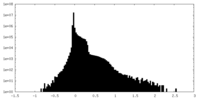
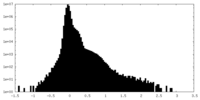
| 密度ヒストグラム |
-追加マップ: Unsharpened map
| ファイル | emd_14271_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
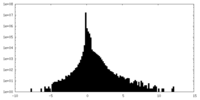
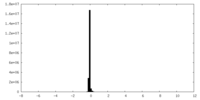
| 密度ヒストグラム |
-追加マップ: Sharpened map
| ファイル | emd_14271_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
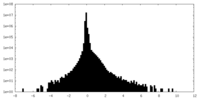
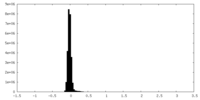
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_14271_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
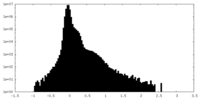
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_14271_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SARS-CoV-2 spike glycoprotein in complex with the 87G7 antibody F...
| 全体 | 名称: SARS-CoV-2 spike glycoprotein in complex with the 87G7 antibody Fab fragment |
|---|---|
| 要素 |
|
-超分子 #1: SARS-CoV-2 spike glycoprotein in complex with the 87G7 antibody F...
| 超分子 | 名称: SARS-CoV-2 spike glycoprotein in complex with the 87G7 antibody Fab fragment タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 分子量 | 理論値: 500 KDa |
-超分子 #2: SARS-CoV-2 spike protein
| 超分子 | 名称: SARS-CoV-2 spike protein / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: Fab
| 超分子 | 名称: Fab / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2-#3 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: SARS-CoV-2 spike protein
| 分子 | 名称: SARS-CoV-2 spike protein / タイプ: protein_or_peptide / ID: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MFVFLVLLPL VSSQCVNLTT RTQLPPAYTN SFTRGVYYPD KVFRSSVLHS TQDLFLPFFS NVTWFHAIHV SGTNGTKRFD NPVLPFNDGV YFASTEKSNI IRGWIFGTTL DSKTQSLLIV NNATNVVIKV CEFQFCNDPF LGVYYHKNNK SWMESEFRVY SSANNCTFEY ...文字列: MFVFLVLLPL VSSQCVNLTT RTQLPPAYTN SFTRGVYYPD KVFRSSVLHS TQDLFLPFFS NVTWFHAIHV SGTNGTKRFD NPVLPFNDGV YFASTEKSNI IRGWIFGTTL DSKTQSLLIV NNATNVVIKV CEFQFCNDPF LGVYYHKNNK SWMESEFRVY SSANNCTFEY VSQPFLMDLE GKQGNFKNLR EFVFKNIDGY FKIYSKHTPI NLVRDLPQGF SALEPLVDLP IGINITRFQT LLALHRSYLT PGDSSSGWTA GAAAYYVGYL QPRTFLLKYN ENGTITDAVD CALDPLSETK CTLKSFTVEK GIYQTSNFRV QPTESIVRFP NITNLCPFGE VFNATRFASV YAWNRKRISN CVADYSVLYN SASFSTFKCY GVSPTKLNDL CFTNVYADSF VIRGDEVRQI APGQTGKIAD YNYKLPDDFT GCVIAWNSNN LDSKVGGNYN YLYRLFRKSN LKPFERDIST EIYQAGSTPC NGVEGFNCYF PLQSYGFQPT NGVGYQPYRV VVLSFELLHA PATVCGPKKS TNLVKNKCVN FNFNGLTGTG VLTESNKKFL PFQQFGRDIA DTTDAVRDPQ TLEILDITPC SFGGVSVITP GTNTSNQVAV LYQDVNCTEV PVAIHADQLT PTWRVYSTGS NVFQTRAGCL IGAEHVNNSY ECDIPIGAGI CASYQTQTNS PAAARSVASQ SIIAYTMSLG AENSVAYSNN SIAIPTNFTI SVTTEILPVS MTKTSVDCTM YICGDSTECS NLLLQYGSFC TQLNRALTGI AVEQDKNTQE VFAQVKQIYK TPPIKDFGGF NFSQILPDPS KPSKRSPIED LLFNKVTLAD AGFIKQYGDC LGDIAARDLI CAQKFNGLTV LPPLLTDEMI AQYTSALLAG TITSGWTFGA GPALQIPFPM QMAYRFNGIG VTQNVLYENQ KLIANQFNSA IGKIQDSLSS TPSALGKLQD VVNQNAQALN TLVKQLSSNF GAISSVLNDI LSRLDPPEAE VQIDRLITGR LQSLQTYVTQ QLIRAAEIRA SANLAATKMS ECVLGQSKRV DFCGKGYHLM SFPQSAPHGV VFLHVTYVPA QEKNFTTAPA ICHDGKAHFP REGVFVSNGT HWFVTQRNFY EPQIITTDNT FVSGNCDVVI GIVNNTVYDP LQPELDSFKE ELDKYFKNHT SPDVDLGDIS GINASVVNIQ KEIDRLNEVA KNLNESLIDL QELGKYEQGS GYIPEAPRDG QAYVRKDGEW VLLSTFLGRS LEVLFQGPGH HHHHHHHSAW SHPQFEKGGG SGGGGSGGSA WSHPQFEK |
-分子 #2: 87G7 heavy chain variable domain
| 分子 | 名称: 87G7 heavy chain variable domain / タイプ: protein_or_peptide / ID: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLLESGGG LVQPGGSLRL SCVASGFTFS SYVMSWVRQA PGKGLEWVAA ISGSGGNTYY ADSVKGRFTI SRDNSKNTLY LQMNSLRAED TAVYYCAKEG TYYYGSGSFW GQGTLVTVSS |
-分子 #3: 87G7 light chain variable domain
| 分子 | 名称: 87G7 light chain variable domain / タイプ: protein_or_peptide / ID: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EIVLTQSPAT LSLSPGERAT LSCRASQSFH NYLAWYQQKP GRAPRLLIFD ASNRATGIPA RFSGSGSGTD FTLTISSLEP EDFAVYYCQQ RFNWPLTFGG GTKVEIK |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 4 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: TFS Selectris X / エネルギーフィルター - スリット幅: 10 eV |
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 2 / 実像数: 3831 / 平均電子線量: 51.5 e/Å2 詳細: 1331 images collected from grid 1 (0.02% FOM) and 2500 images collected from grid 2 (0% FOM) |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー






 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)