+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | cryo iDPC-STEM structure recorded with CSA 3.0 | |||||||||
 マップデータ マップデータ | cryo iDPC-STEM structure recorded with CSA 3.0 | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | tobacco mosaic virus / RNA virus / VIRUS | |||||||||
| 機能・相同性 | Tobacco mosaic virus-like, coat protein / Tobacco mosaic virus-like, coat protein superfamily / Virus coat protein (TMV like) / helical viral capsid / structural molecule activity / identical protein binding / Capsid protein 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Tobacco mosaic virus (strain vulgare) (ウイルス) Tobacco mosaic virus (strain vulgare) (ウイルス) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 4.3 Å | |||||||||
 データ登録者 データ登録者 | Sachse C / Leidl ML | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Methods / 年: 2022 ジャーナル: Nat Methods / 年: 2022タイトル: Single-particle cryo-EM structures from iDPC-STEM at near-atomic resolution. 著者: Ivan Lazić / Maarten Wirix / Max Leo Leidl / Felix de Haas / Daniel Mann / Maximilian Beckers / Evgeniya V Pechnikova / Knut Müller-Caspary / Ricardo Egoavil / Eric G T Bosch / Carsten Sachse /   要旨: In electron cryomicroscopy (cryo-EM), molecular images of vitrified biological samples are obtained by conventional transmission microscopy (CTEM) using large underfocuses and subsequently ...In electron cryomicroscopy (cryo-EM), molecular images of vitrified biological samples are obtained by conventional transmission microscopy (CTEM) using large underfocuses and subsequently computationally combined into a high-resolution three-dimensional structure. Here, we apply scanning transmission electron microscopy (STEM) using the integrated differential phase contrast mode also known as iDPC-STEM to two cryo-EM test specimens, keyhole limpet hemocyanin (KLH) and tobacco mosaic virus (TMV). The micrographs show complete contrast transfer to high resolution and enable the cryo-EM structure determination for KLH at 6.5 Å resolution, as well as for TMV at 3.5 Å resolution using single-particle reconstruction methods, which share identical features with maps obtained by CTEM of a previously acquired same-sized TMV data set. These data show that STEM imaging in general, and in particular the iDPC-STEM approach, can be applied to vitrified single-particle specimens to determine near-atomic resolution cryo-EM structures of biological macromolecules. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
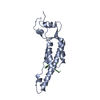
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13779.map.gz emd_13779.map.gz | 7.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13779-v30.xml emd-13779-v30.xml emd-13779.xml emd-13779.xml | 15.4 KB 15.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_13779_fsc.xml emd_13779_fsc.xml | 10.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_13779.png emd_13779.png | 120.5 KB | ||
| マスクデータ |  emd_13779_msk_1.map emd_13779_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-13779.cif.gz emd-13779.cif.gz | 5.3 KB | ||
| その他 |  emd_13779_half_map_1.map.gz emd_13779_half_map_1.map.gz emd_13779_half_map_2.map.gz emd_13779_half_map_2.map.gz | 80.5 MB 80.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13779 http://ftp.pdbj.org/pub/emdb/structures/EMD-13779 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13779 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13779 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13779.map.gz / 形式: CCP4 / 大きさ: 30.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13779.map.gz / 形式: CCP4 / 大きさ: 30.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | cryo iDPC-STEM structure recorded with CSA 3.0 | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.23 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13779_msk_1.map emd_13779_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half-map2
| ファイル | emd_13779_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half-map1
| ファイル | emd_13779_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tobacco mosaic virus
| 全体 | 名称:   Tobacco mosaic virus (ウイルス) Tobacco mosaic virus (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Tobacco mosaic virus
| 超分子 | 名称: Tobacco mosaic virus / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Tobacco mosaic virus (strain vulgare) (ウイルス) Tobacco mosaic virus (strain vulgare) (ウイルス) |
| 分子量 | 理論値: 131 kDa/nm |
-分子 #1: Capsid protein
| 分子 | 名称: Capsid protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Tobacco mosaic virus (strain vulgare) (ウイルス) Tobacco mosaic virus (strain vulgare) (ウイルス)株: vulgare |
| 分子量 | 理論値: 17.091998 KDa |
| 配列 | 文字列: SYSITTPSQF VFLSSAWADP IELINLCTNA LGNQFQTQQA RTVVQRQFSE VWKPSPQVTV RFPDSDFKVY RYNAVLDPLV TALLGAFDT RNRIIEVENQ ANPTTAETLD ATRRVDDATV AIRSAINNLI VELIRGTGSY NRSSFESSSG LVWT UniProtKB: Capsid protein |
-分子 #2: RNA (5'-R(P*GP*AP*A)-3')
| 分子 | 名称: RNA (5'-R(P*GP*AP*A)-3') / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Tobacco mosaic virus (strain vulgare) (ウイルス) Tobacco mosaic virus (strain vulgare) (ウイルス)株: vulgare |
| 分子量 | 理論値: 958.66 Da |
| 配列 | 文字列: GAA |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | helical array |
- 試料調製
試料調製
| 濃度 | 90 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV 詳細: blot force of +10 and a duration for blotting of 10 seconds. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 詳細 | iDPC-STEM |
| 撮影 | フィルム・検出器のモデル: OTHER / 平均電子線量: 35.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)