+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | RNA origami 5-helix tile | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNA / origami / nanostructure | |||||||||
| 生物種 | synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 5.71 Å | |||||||||
 データ登録者 データ登録者 | McRae EKS / Bogglid A / Boesen T / Andersen ES | |||||||||
| 資金援助 |  デンマーク, 1件 デンマーク, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Nanotechnol / 年: 2023 ジャーナル: Nat Nanotechnol / 年: 2023タイトル: Structure, folding and flexibility of co-transcriptional RNA origami. 著者: Ewan K S McRae / Helena Østergaard Rasmussen / Jianfang Liu / Andreas Bøggild / Michael T A Nguyen / Nestor Sampedro Vallina / Thomas Boesen / Jan Skov Pedersen / Gang Ren / Cody Geary / Ebbe Sloth Andersen /   要旨: RNA origami is a method for designing RNA nanostructures that can self-assemble through co-transcriptional folding with applications in nanomedicine and synthetic biology. However, to advance the ...RNA origami is a method for designing RNA nanostructures that can self-assemble through co-transcriptional folding with applications in nanomedicine and synthetic biology. However, to advance the method further, an improved understanding of RNA structural properties and folding principles is required. Here we use cryogenic electron microscopy to study RNA origami sheets and bundles at sub-nanometre resolution revealing structural parameters of kissing-loop and crossover motifs, which are used to improve designs. In RNA bundle designs, we discover a kinetic folding trap that forms during folding and is only released after 10 h. Exploration of the conformational landscape of several RNA designs reveal the flexibility of helices and structural motifs. Finally, sheets and bundles are combined to construct a multidomain satellite shape, which is characterized by individual-particle cryo-electron tomography to reveal the domain flexibility. Together, the study provides a structural basis for future improvements to the design cycle of genetically encoded RNA nanodevices. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_13636.map.gz emd_13636.map.gz | 4.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-13636-v30.xml emd-13636-v30.xml emd-13636.xml emd-13636.xml | 21.1 KB 21.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_13636_fsc.xml emd_13636_fsc.xml | 4.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_13636.png emd_13636.png | 46.8 KB | ||
| マスクデータ |  emd_13636_msk_1.map emd_13636_msk_1.map | 8 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-13636.cif.gz emd-13636.cif.gz | 5.9 KB | ||
| その他 |  emd_13636_additional_1.map.gz emd_13636_additional_1.map.gz emd_13636_half_map_1.map.gz emd_13636_half_map_1.map.gz emd_13636_half_map_2.map.gz emd_13636_half_map_2.map.gz | 7.6 MB 7.4 MB 7.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-13636 http://ftp.pdbj.org/pub/emdb/structures/EMD-13636 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13636 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-13636 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_13636_validation.pdf.gz emd_13636_validation.pdf.gz | 685.8 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_13636_full_validation.pdf.gz emd_13636_full_validation.pdf.gz | 685.4 KB | 表示 | |
| XML形式データ |  emd_13636_validation.xml.gz emd_13636_validation.xml.gz | 10.9 KB | 表示 | |
| CIF形式データ |  emd_13636_validation.cif.gz emd_13636_validation.cif.gz | 13.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13636 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13636 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13636 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-13636 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_13636.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_13636.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.59 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_13636_msk_1.map emd_13636_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
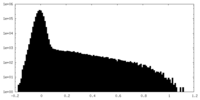
| 密度ヒストグラム |
-追加マップ: Sharpened map from cryoSPARC with bfactor 306.
| ファイル | emd_13636_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map from cryoSPARC with bfactor 306. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_13636_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_13636_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : 5 helix tile B
| 全体 | 名称: 5 helix tile B |
|---|---|
| 要素 |
|
-超分子 #1: 5 helix tile B
| 超分子 | 名称: 5 helix tile B / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: In vitro transcribed RNA purified by SEC. |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 180 KDa |
-分子 #1: 5HT-B
| 分子 | 名称: 5HT-B / タイプ: rna / ID: 1 / 詳細: In vitro transcribed RNA / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 179.904219 KDa |
| 配列 | 文字列: GGAACUUAUU CAUUAUACCC CUCAUUUUCG AGUGAGGCGG AUUAGAUUCG UCUGAUCGUA GUGGUGGUGG CUUGCUUCGG CGAGCCCGG CAGGCCUUCG GGCUUGCUCA GGGGUUCGCU CCUGAGAUUA UCAUCCAACC UCCAAGGAUG GUAAUCCGGC G UCGAUUGU ...文字列: GGAACUUAUU CAUUAUACCC CUCAUUUUCG AGUGAGGCGG AUUAGAUUCG UCUGAUCGUA GUGGUGGUGG CUUGCUUCGG CGAGCCCGG CAGGCCUUCG GGCUUGCUCA GGGGUUCGCU CCUGAGAUUA UCAUCCAACC UCCAAGGAUG GUAAUCCGGC G UCGAUUGU AAGGUCUAAA CAAUUGACGC ACCACUACUA CAGUCCCAAC GACUGAGGGA CUCGUCGACU CGGUUAAGAU CG GAAACCG GGUCGAGGUA UAGUGAAUGA GUUCCAAUUC UCCAUUUACG GCAUCUUGUG CGAACCGAUC ACGCACGAGA UGG UCCUUA CGGGGUGUCC CAACAGUCGA GGGGCACGCA GGAUGCCUAG AAUAGACCAC UAGGUAUCCU CAGUGCGCCA UGCA AUGGA GGAGCAUGGU GCACUGCAGG GCUCCUGAAA AGGAGUCCUG GCAGAAGGGU UCGCCUUUCU CCCGUAGGGA CGACU UUCU UUGAAAAAAG GAAGUCCCAG UUUGCUUCGG CGAACUCCGA CUCUAGGAAA CUAGGGUCGG GUAGAUGGAG AAUU |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: Freshly prepared and filtered through 0.22 micron filter prior to use. | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 99 % / チャンバー内温度: 294 K / 装置: LEICA EM GP 詳細: 3 microlitre droplet, 4 second delay before blotting, 6 second blot, 0 second delay before plunging.. | ||||||||||||
| 詳細 | Sample was purified by size exclusion chromatography and concentrated in an Amicon spin concentrator. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 1331 / 平均露光時間: 1.5 sec. / 平均電子線量: 60.0 e/Å2 / 詳細: Images were collected as 56 frame movies. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.75 µm / 倍率(公称値): 130000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Source name: PDB / Chain - Initial model type: experimental model |
|---|---|
| 詳細 | Helical templates and tetraloops were generated in RNAbuild. Kissing loops were modelling based on the PDB:2D1B structure. A combination of PHENIX RSR and ISOLDE were used to arrive at the final structure. |
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 306 / 当てはまり具合の基準: Correlation Coefficient |
| 得られたモデル |  PDB-7pts: |
 ムービー
ムービー コントローラー
コントローラー

























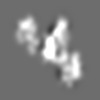






 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)