+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-12658 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the MukBEF monomer | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nucleoid / chromosome condensation / acyl carrier activity / chromosome segregation / DNA replication / cell division / calcium ion binding / DNA binding / ATP binding / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Photorhabdus thracensis (バクテリア) / Photorhabdus thracensis (バクテリア) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.8 Å | |||||||||
 データ登録者 データ登録者 | Buermann F / Lowe J | |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2021 ジャーナル: Mol Cell / 年: 2021タイトル: Cryo-EM structure of MukBEF reveals DNA loop entrapment at chromosomal unloading sites. 著者: Frank Bürmann / Louise F H Funke / Jason W Chin / Jan Löwe /  要旨: The ring-like structural maintenance of chromosomes (SMC) complex MukBEF folds the genome of Escherichia coli and related bacteria into large loops, presumably by active DNA loop extrusion. MukBEF ...The ring-like structural maintenance of chromosomes (SMC) complex MukBEF folds the genome of Escherichia coli and related bacteria into large loops, presumably by active DNA loop extrusion. MukBEF activity within the replication terminus macrodomain is suppressed by the sequence-specific unloader MatP. Here, we present the complete atomic structure of MukBEF in complex with MatP and DNA as determined by electron cryomicroscopy (cryo-EM). The complex binds two distinct DNA double helices corresponding to the arms of a plectonemic loop. MatP-bound DNA threads through the MukBEF ring, while the second DNA is clamped by the kleisin MukF, MukE, and the MukB ATPase heads. Combinatorial cysteine cross-linking confirms this topology of DNA loop entrapment in vivo. Our findings illuminate how a class of near-ubiquitous DNA organizers with important roles in genome maintenance interacts with the bacterial chromosome. #1:  ジャーナル: Biorxiv / 年: 2021 ジャーナル: Biorxiv / 年: 2021タイトル: DNA entrapment revealed by the structure of bacterial condensin MukBEF 著者: Buermann F / Funke LFH / Chin JW / Lowe J | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_12658.map.gz emd_12658.map.gz | 96.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-12658-v30.xml emd-12658-v30.xml emd-12658.xml emd-12658.xml | 22.2 KB 22.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_12658.png emd_12658.png | 35 KB | ||
| マスクデータ |  emd_12658_msk_1.map emd_12658_msk_1.map | 122.7 MB |  マスクマップ マスクマップ | |
| その他 |  emd_12658_additional_1.map.gz emd_12658_additional_1.map.gz emd_12658_half_map_1.map.gz emd_12658_half_map_1.map.gz emd_12658_half_map_2.map.gz emd_12658_half_map_2.map.gz | 114.7 MB 96.8 MB 96.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-12658 http://ftp.pdbj.org/pub/emdb/structures/EMD-12658 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12658 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-12658 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_12658_validation.pdf.gz emd_12658_validation.pdf.gz | 455.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_12658_full_validation.pdf.gz emd_12658_full_validation.pdf.gz | 455.4 KB | 表示 | |
| XML形式データ |  emd_12658_validation.xml.gz emd_12658_validation.xml.gz | 13.7 KB | 表示 | |
| CIF形式データ |  emd_12658_validation.cif.gz emd_12658_validation.cif.gz | 16.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12658 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12658 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12658 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-12658 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7nyyMC  7nywC  7nyxC  7nyzC  7nz0C  7nz2C  7nz3C  7nz4C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10755 (タイトル: MukBEF(E1407Q)-MatP-DNA in the presence of ATP EMPIAR-10755 (タイトル: MukBEF(E1407Q)-MatP-DNA in the presence of ATPData size: 8.5 TB Data #1: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 1 [micrographs - multiframe] Data #2: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 2 [micrographs - multiframe] Data #3: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 1 [micrographs - multiframe] Data #4: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 2 [micrographs - multiframe] Data #5: Unaligned multi-frame images of MukBEF(E1407Q)-MatP-DNA in the presence of ATP - Dataset 3, grid 3 [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_12658.map.gz / 形式: CCP4 / 大きさ: 122.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_12658.map.gz / 形式: CCP4 / 大きさ: 122.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.45358 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_12658_msk_1.map emd_12658_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
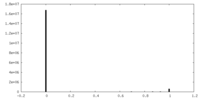
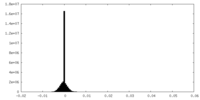
| 密度ヒストグラム |
-追加マップ: Sharpened map
| ファイル | emd_12658_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
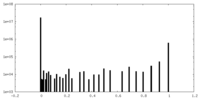
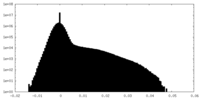
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_12658_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
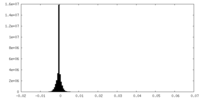
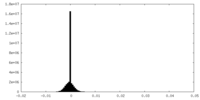
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_12658_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
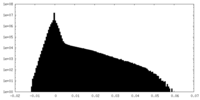
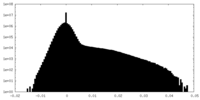
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Complex of MukBEF and AcpP
| 全体 | 名称: Complex of MukBEF and AcpP |
|---|---|
| 要素 |
|
-超分子 #1: Complex of MukBEF and AcpP
| 超分子 | 名称: Complex of MukBEF and AcpP / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#4 |
|---|
-超分子 #2: Complex of MukBEF
| 超分子 | 名称: Complex of MukBEF / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) |
| 組換発現 | 生物種:  |
-超分子 #3: Acyl carrier protein
| 超分子 | 名称: Acyl carrier protein / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #4 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Chromosome partition protein MukB
| 分子 | 名称: Chromosome partition protein MukB / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) |
| 分子量 | 理論値: 170.240188 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MIERGKFRSL TLVNWNGFFA RTFDLDELVT TLSGGNGAGK STTMAAFVTA LIPDLTLLHF RNTTEAGATS GSRDKGLHGK LRAGVCYST LDVINSRHQR VVVGVRLQQV AGRDRKVDIK PFMIQGLPTA IQPTQLLTEN VGERQARVLP LNELKDRLDE M EGVQFKQF ...文字列: MIERGKFRSL TLVNWNGFFA RTFDLDELVT TLSGGNGAGK STTMAAFVTA LIPDLTLLHF RNTTEAGATS GSRDKGLHGK LRAGVCYST LDVINSRHQR VVVGVRLQQV AGRDRKVDIK PFMIQGLPTA IQPTQLLTEN VGERQARVLP LNELKDRLDE M EGVQFKQF NSITDYHAQM FDLGVIPKRL RSASDRSKFY RLIEASLYGG ISSAITRSLR DYLLPENSGV RKAFQDMEAA LR ENRITLE AIRVTQSDRD LFKHLITEAT SYVSADYMRH ANERRTHLDE ALALRGELFG SHKQLATEQY RHVEMARELA EQS GASSDL ETDHQAASDH LNLVQTAMRQ QEKIDRYQVD LEELSYRLEE QTDVVEEAGE LQAEYEARTE ATEQEVDELK SQLA DYQQA LDVQQTRAIQ YQQALQALER ARELCRLPDL SVDNAEEWLE TFQAKEQQAT EALLALEQKL SVADAAHNQF EQAYQ LVKN IVGETSRSEA WQSARELLRD WPSQRHLADR VQPLRMRLSE LEQRLNNQQN AERLLSEFCK RQGRQYQAED LEALQN ELE ARQEALSLSV NEGGERRMEM RQELEQLKQK IQSLTARAPV WLAAQDTLNQ LCEQSGETLA SSNDVTEYMQ QLLERER EA TVERDEVAAQ KRELEKQIER LSQPSGAEDS RMIALAERFG GVLLSEIYDD ITIDDAPYFS ALYGPARHGI VVPDLSLV R PHLETLEDCP EDLYLIEGDP QSFDDSVFNA EEQTNAVLVK SSDRQWRYSR YPELPLFGRA ARENRLEALN LERDALAER YATLSFDVQK IQRAHQAFSQ FVGKHLSVAF DTDPEAEIRE LRQRHTELER EVSRFEDQTQ QQRQQYAQAK ESLTTLNRLI PQVTLLLDE TLIDRVEEVR EEMDEAQEAA RFLQQHGSAL TKLEPMVAVL QSDPQQHEQL QQDYETAKHS QHQAKQQAFA L VEIVQRRV HFSYSDSAGM LSENADLNDK LRQRLEHAES DRSRAREQLR QQQAQYSQFN QVLASLKSSY ETKQDMLKEL LQ EMKDIGV QADANAEMRA RERRDRLHEA LSVNRSRVNQ LEKQIAFCEA EMENVQKKLR KLERDYYQIR EQVVSAKAGW CAV MRMVKD NGVERRLHRR ELAYMEGGAL RSMSDKALGA LRLAVADNEH LRDALRLSED PKRPERKVQF FIAVYQHLRE RIRQ DIIRT DDPVDAIEQM EIELARLTEE LTAREQKLAI SSKSVANIIR KTIQREQNRI RMLNQGLQAV SFGQVRGVRL NVNVR ESHA ILLDVLSEQQ EQHQDLFNSQ RLTFSEAMAK LYQRLNPQVD MGQRLPQTIG EELLDYRNYL ELDVEVNRGS DGWLKA ESG ALSTGEAIGT GMSILVMVVQ SWEEESRRLR GKDISPCRLL FLDQAARLDA KSIATLFELC ERLQMQLIIA APENISP EK GTTYKLVRKV FKNHEHVHVV GLRGFGQDAP ATQLISDVTA |
-分子 #2: Chromosome partition protein MukF
| 分子 | 名称: Chromosome partition protein MukF / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) |
| 分子量 | 理論値: 50.193305 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSEYSQTVPE LVSWARKNDF SISLPVERLA FLMAIAVLNS ERLDGEMSEG ELIDAFREVC KGFEQTAESV AVRANNAIND MVRQKLLNR FTSELADGNA IYRLTPLGIS ISDYYIRQRE FSTLRLSMQL SIVANELHRA AEAAEEGGDE FHWHRNVFAP L KYSVAEIF ...文字列: MSEYSQTVPE LVSWARKNDF SISLPVERLA FLMAIAVLNS ERLDGEMSEG ELIDAFREVC KGFEQTAESV AVRANNAIND MVRQKLLNR FTSELADGNA IYRLTPLGIS ISDYYIRQRE FSTLRLSMQL SIVANELHRA AEAAEEGGDE FHWHRNVFAP L KYSVAEIF DSIDMSQRLM DEQQNFVKED IAALLNQDWQ AAIANCEQLL SETSGTLREL QDTLEAAGDK LQANLLRIQD AN MGSGGSE LVDKLVFDLQ SKLDRIISWG QQAIDLWIGY DRHVHKFIRT AIDMDKNRIF SQRLRQSVQH YFDNPWTLTV ANA ERLLDM RDEELALRNE EVTGELPLEL EYEEFSEIND QLAAMIEKAL LVYQQEQRPL DLGAVLRDYL AQHPLPRHFD VARI LVDQA VRLGVAEADF SGLPAEWLAI NDYGAKVQAH VIDTY |
-分子 #3: Chromosome partition protein MukE
| 分子 | 名称: Chromosome partition protein MukE / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus thracensis (バクテリア) Photorhabdus thracensis (バクテリア) |
| 分子量 | 理論値: 27.423848 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSSTHIEQFM PVKLAQALAN SLFPELDSQL RAGRHIGIDD LDNHAFLMDF QEQLEEFYAR YNVELIRAPE GFFYLRPRST TLIPRSVLS ELDMMVGKIL CYLYLSPERL ANQGIFTSQE LYEELISLAD EGKLMKFVNQ RSSGSDLDKQ KLQEKVRTTL N RLRRLGMV ...文字列: MSSTHIEQFM PVKLAQALAN SLFPELDSQL RAGRHIGIDD LDNHAFLMDF QEQLEEFYAR YNVELIRAPE GFFYLRPRST TLIPRSVLS ELDMMVGKIL CYLYLSPERL ANQGIFTSQE LYEELISLAD EGKLMKFVNQ RSSGSDLDKQ KLQEKVRTTL N RLRRLGMV YFLPNNNNKF TITEAVFRFG ADVRSGDDPR EIQLRMIRDG EAMPVEGSLS LDDSENDETP DNSAEGAGDE QP |
-分子 #4: Acyl carrier protein
| 分子 | 名称: Acyl carrier protein / タイプ: protein_or_peptide / ID: 4 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 8.64546 KDa |
| 配列 | 文字列: MSTIEERVKK IIGEQLGVKQ EEVTNNASFV EDLGADSLDT VELVMALEEE FDTEIPDEEA EKITTVQAAI DYINGHQA |
-分子 #5: 4'-PHOSPHOPANTETHEINE
| 分子 | 名称: 4'-PHOSPHOPANTETHEINE / タイプ: ligand / ID: 5 / コピー数: 2 / 式: PNS |
|---|---|
| 分子量 | 理論値: 358.348 Da |
| Chemical component information | 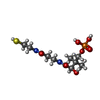 ChemComp-PNS: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.3 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 6.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 96150 |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)