+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10757 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
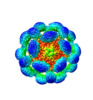
| タイトル | Cryo-EM structure of norovirus GI.4c VLPs with T=1 icosahedral symmetry | |||||||||
 マップデータ マップデータ | Cryo-EM structure of GII.4c VLPs with T=1 icosahedral symmetry | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a (ウイルス) Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a (ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.2 Å | |||||||||
 データ登録者 データ登録者 | Devant JM / Hansman GS | |||||||||
 引用 引用 |  ジャーナル: Virology / 年: 2021 ジャーナル: Virology / 年: 2021タイトル: Structural heterogeneity of a human norovirus vaccine candidate. 著者: Jessica M Devant / Grant S Hansman /  要旨: Human norovirus virus-like particles (VLPs) are assumed to be morphologically and antigenically similar to virion particles. The norovirus virion is assembled from 180 copies of the capsid protein ...Human norovirus virus-like particles (VLPs) are assumed to be morphologically and antigenically similar to virion particles. The norovirus virion is assembled from 180 copies of the capsid protein (VP1) and exhibits T = 3 icosahedral symmetry. In this study, we showed that the vaccine candidate GII.4c VP1 formed T = 1 and T = 3 VLPs, but mainly assembled into T = 4 icosahedral particles that were composed of 240 VP1 copies. In contrast, another clinically important genotype, GII.17, almost exclusively folded into T = 3 VLPs. Interestingly, the GII.4c T = 1 particles had higher binding capacities to norovirus-specific Nanobodies than to GII.4c T = 3 and T = 4 particles. Our data indicated that the occluded Nanobody-binding epitopes on the T = 1 particles were more accessible compared to the larger T = 3 and T = 4 particles. Overall, this new data revealed that GII.4c VLPs had a preference for forming the T = 4 icosahedral symmetry and future studies with varied sized norovirus VLPs should take caution when examining antigenicity. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10757.map.gz emd_10757.map.gz | 95 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10757-v30.xml emd-10757-v30.xml emd-10757.xml emd-10757.xml | 11 KB 11 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_10757.png emd_10757.png | 138.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10757 http://ftp.pdbj.org/pub/emdb/structures/EMD-10757 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10757 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10757 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10757.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10757.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of GII.4c VLPs with T=1 icosahedral symmetry | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.375 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a
| 全体 | 名称:  Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a (ウイルス) Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a
| 超分子 | 名称: Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a / タイプ: virus / ID: 1 / 親要素: 0 / NCBI-ID: 1631306 / 生物種: Norovirus 06-AM-11/2006/GII.4/Yerseke/2006a / Sci species strain: GII.4c / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: No / ウイルス・中空状態: Yes |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| Host system | 生物種:  Trichoplusia ni (イラクサキンウワバ) / 組換株: HighFive insect cells Trichoplusia ni (イラクサキンウワバ) / 組換株: HighFive insect cells |
| ウイルス殻 | Shell ID: 1 / 直径: 310.0 Å / T番号(三角分割数): 1 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 名称: PBS / 詳細: PBS buffer |
| グリッド | モデル: Quantifoil R0.6/1 / 材質: COPPER/RHODIUM / メッシュ: 300 / 前処理 - タイプ: PLASMA CLEANING |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 285 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 2 / 実像数: 3983 / 平均電子線量: 15.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 倍率(公称値): 64000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | ソフトウェア - 名称: CTFFIND (ver. 4) |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC (ver. 2.4.0) / 使用した粒子像数: 48973 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC (ver. 2.4.0) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: cryoSPARC (ver. 2.4.0) |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















