+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-10312 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of Photorhabdus luminescens Tc holotoxin pore, Mutation TccC3-D651A | |||||||||
 マップデータ マップデータ | Map of Tc holotoxin ABC-D651A in the pore form, filtered according to the local resolution | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Complex / Holotoxin / Photorhabdus / Insecticidal / TOXIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Photorhabdus luminescens (バクテリア) Photorhabdus luminescens (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Roderer D / Raunser S | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2019 ジャーナル: Proc Natl Acad Sci U S A / 年: 2019タイトル: Structure of a Tc holotoxin pore provides insights into the translocation mechanism. 著者: Daniel Roderer / Oliver Hofnagel / Roland Benz / Stefan Raunser /  要旨: Tc toxins are modular toxin systems of insect and human pathogenic bacteria. They are composed of a 1.4-MDa pentameric membrane translocator (TcA) and a 250-kDa cocoon (TcB and TcC) encapsulating the ...Tc toxins are modular toxin systems of insect and human pathogenic bacteria. They are composed of a 1.4-MDa pentameric membrane translocator (TcA) and a 250-kDa cocoon (TcB and TcC) encapsulating the 30-kDa toxic enzyme (C terminus of TcC). Binding of Tc toxins to target cells and a pH shift trigger the conformational transition from the soluble prepore state to the membrane-embedded pore. Subsequently, the toxic enzyme is translocated and released into the cytoplasm. A high-resolution structure of a holotoxin embedded in membranes is missing, leaving open the question of whether TcB-TcC has an influence on the conformational transition of TcA. Here we show in atomic detail a fully assembled 1.7-MDa Tc holotoxin complex from in the membrane. We find that the 5 TcA protomers conformationally adapt to fit around the cocoon during the prepore-to-pore transition. The architecture of the Tc toxin complex allows TcB-TcC to bind to an already membrane-embedded TcA pore to form a holotoxin. Importantly, assembly of the holotoxin at the membrane results in spontaneous translocation of the toxic enzyme, indicating that this process is not driven by a proton gradient or other energy source. Mammalian lipids with zwitterionic head groups are preferred over other lipids for the integration of Tc toxins. In a nontoxic Tc toxin variant, we can visualize part of the translocating toxic enzyme, which transiently interacts with alternating negative charges and hydrophobic stretches of the translocation channel, providing insights into the mechanism of action of Tc toxins. #1:  ジャーナル: Biorxiv ジャーナル: Biorxivタイトル: Structure of a Tc holotoxin pore provides insights into the translocation mechanism 著者: Roderer D / Hofnagel O / Benz R / Raunser S | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_10312.map.gz emd_10312.map.gz | 12.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-10312-v30.xml emd-10312-v30.xml emd-10312.xml emd-10312.xml | 22.5 KB 22.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_10312.png emd_10312.png | 112.4 KB | ||
| Filedesc metadata |  emd-10312.cif.gz emd-10312.cif.gz | 8.6 KB | ||
| その他 |  emd_10312_additional.map.gz emd_10312_additional.map.gz emd_10312_half_map_1.map.gz emd_10312_half_map_1.map.gz emd_10312_half_map_2.map.gz emd_10312_half_map_2.map.gz | 9 MB 21.7 MB 21.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-10312 http://ftp.pdbj.org/pub/emdb/structures/EMD-10312 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10312 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-10312 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_10312.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_10312.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map of Tc holotoxin ABC-D651A in the pore form, filtered according to the local resolution | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
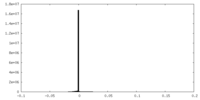
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.11 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
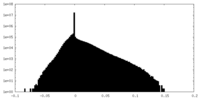
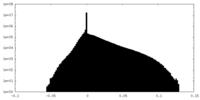
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Map with the center of reconstruction shifted towards...
| ファイル | emd_10312_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map with the center of reconstruction shifted towards the TcB-TcC component | ||||||||||||
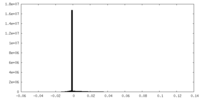
| 投影像・断面図 |
| ||||||||||||
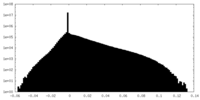
| 密度ヒストグラム |
-ハーフマップ: Half map 0
| ファイル | emd_10312_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 0 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_10312_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tc holotoxin composed of the TcdA1 pentamer and TcdB2-TccC3
| 全体 | 名称: Tc holotoxin composed of the TcdA1 pentamer and TcdB2-TccC3 |
|---|---|
| 要素 |
|
-超分子 #1: Tc holotoxin composed of the TcdA1 pentamer and TcdB2-TccC3
| 超分子 | 名称: Tc holotoxin composed of the TcdA1 pentamer and TcdB2-TccC3 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: Mutation D651A in TccC3 |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus luminescens (バクテリア) Photorhabdus luminescens (バクテリア) |
| 分子量 | 理論値: 1.7 MDa |
-分子 #1: TcdA1
| 分子 | 名称: TcdA1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 5 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus luminescens (バクテリア) Photorhabdus luminescens (バクテリア) |
| 分子量 | 理論値: 283.230375 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MNESVKEIPD VLKSQCGFNC LTDISHSSFN EFRQQVSEHL SWSETHDLYH DAQQAQKDNR LYEARILKRA NPQLQNAVHL AILAPNAEL IGYNNQFSGR ASQYVAPGTV SSMFSPAAYL TELYREARNL HASDSVYYLD TRRPDLKSMA LSQQNMDIEL S TLSLSNEL ...文字列: MNESVKEIPD VLKSQCGFNC LTDISHSSFN EFRQQVSEHL SWSETHDLYH DAQQAQKDNR LYEARILKRA NPQLQNAVHL AILAPNAEL IGYNNQFSGR ASQYVAPGTV SSMFSPAAYL TELYREARNL HASDSVYYLD TRRPDLKSMA LSQQNMDIEL S TLSLSNEL LLESIKTESK LENYTKVMEM LSTFRPSGAT PYHDAYENVR EVIQLQDPGL EQLNASPAIA GLMHQASLLG IN ASISPEL FNILTEEITE GNAEELYKKN FGNIEPASLA MPEYLKRYYN LSDEELSQFI GKASNFGQQE YSNNQLITPV VNS SDGTVK VYRITREYTT NAYQMDVELF PFGGENYRLD YKFKNFYNAS YLSIKLNDKR ELVRTEGAPQ VNIEYSANIT LNTA DISQP FEIGLTRVLP SGSWAYAAAK FTVEEYNQYS FLLKLNKAIR LSRATELSPT ILEGIVRSVN LQLDINTDVL GKVFL TKYY MQRYAIHAET ALILCNAPIS QRSYDNQPSQ FDRLFNTPLL NGQYFSTGDE EIDLNSGSTG DWRKTILKRA FNIDDV SLF RLLKITDHDN KDGKIKNNLK NLSNLYIGKL LADIHQLTID ELDLLLIAVG EGKTNLSAIS DKQLATLIRK LNTITSW LH TQKWSVFQLF IMTSTSYNKT LTPEIKNLLD TVYHGLQGFD KDKADLLHVM APYIAATLQL SSENVAHSVL LWADKLQP G DGAMTAEKFW DWLNTKYTPG SSEAVETQEH IVQYCQALAQ LEMVYHSTGI NENAFRLFVT KPEMFGAATG AAPAHDALS LIMLTRFADW VNALGEKASS VLAAFEANSL TAEQLADAMN LDANLLLQAS IQAQNHQHLP PVTPENAFSC WTSINTILQW VNVAQQLNV APQGVSALVG LDYIESMKET PTYAQWENAA GVLTAGLNSQ QANTLHAFLD ESRSAALSTY YIRQVAKAAA A IKSRDDLY QYLLIDNQVS AAIKTTRIAE AIASIQLYVN RALENVEENA NSGVISRQFF IDWDKYNKRY STWAGVSQLV YY PENYIDP TMRIGQTKMM DALLQSVSQS QLNADTVEDA FMSYLTSFEQ VANLKVISAY HDNINNDQGL TYFIGLSETD AGE YYWRSV DHSKFNDGKF AANAWSEWHK IDCPINPYKS TIRPVIYKSR LYLLWLEQKE ITKQTGNSKD GYQTETDYRY ELKL AHIRY DGTWNTPITF DVNKKISELK LEKNRAPGLY CAGYQGEDTL LVMFYNQQDT LDSYKNASMQ GLYIFADMAS KDMTP EQSN VYRDNSYQQF DTNNVRRVNN RYAEDYEIPS SVSSRKDYGW GDYYLSMVYN GDIPTINYKA ASSDLKIYIS PKLRII HNG YEGQKRNQCN LMNKYGKLGD KFIVYTSLGV NPNNSSNKLM FYPVYQYSGN TSGLNQGRLL FHRDTTYPSK VEAWIPG AK RSLTNQNAAI GDDYATDSLN KPDDLKQYIF MTDSKGTATD VSGPVEINTA ISPAKVQIIV KAGGKEQTFT ADKDVSIQ P SPSFDEMNYQ FNALEIDGSG LNFINNSASI DVTFTAFAED GRKLGYESFS IPVTLKVSTD NALTLHHNEN GAQYMQWQS YRTRLNTLFA RQLVARATTG IDTILSMETQ NIQEPQLGKG FYATFVIPPY NLSTHGDERW FKLYIKHVVD NNSHIIYSGQ LTDTNINIT LFIPLDDVPL NQDYHAKVYM TFKKSPSDGT WWGPHFVRDD KGIVTINPKS ILTHFESVNV LNNISSEPMD F SGANSLYF WELFYYTPML VAQRLLHEQN FDEANRWLKY VWSPSGYIVH GQIQNYQWNV RPLLEDTSWN SDPLDSVDPD AV AQHDPMH YKVSTFMRTL DLLIARGDHA YRQLERDTLN EAKMWYMQAL HLLGDKPYLP LSTTWSDPRL DRAADITTQN AHD SAIVAL RQNIPTPAPL SLRSANTLTD LFLPQINEVM MNYWQTLAQR VYNLRHNLSI DGQPLYLPIY ATPADPKALL SAAV ATSQG GGKLPESFMS LWRFPHMLEN ARGMVSQLTQ FGSTLQNIIE RQDAEALNAL LQNQAAELIL TNLSIQDKTI EELDA EKTV LEKSKAGAQS RFDSYGKLYD ENINAGENQA MTLRASAAGL TTAVQASRLA GAAADLVPNI FGFAGGGSRW GAIAEA TGY VMEFSANVMN TEADKISQSE TYRRRRQEWE IQRNNAEAEL KQIDAQLKSL AVRREAAVLQ KTSLKTQQEQ TQSQLAF LQ RKFSNQALYN WLRGRLAAIY FQFYDLAVAR CLMAEQAYRW ELNDDSARFI KPGAWQGTYA GLLAGETLML SLAQMEDA H LKRDKRALEV ERTVSLAEVY AGLPKDNGPF SLAQEIDKLV SQGSGSAGSG NNNLAFGAGT DTKTSLQASV SFADLKIRE DYPASLGKIR RIKQISVTLP ALLGPYQDVQ AILSYGDKAG LANGCEALAV SHGMNDSGQF QLDFNDGKFL PFEGIAIDQG TLTLSFPNA SMPEKGKQAT MLKTLNDIIL HIRYTIK UniProtKB: TcdA1 |
-分子 #2: TcdB2,TccC3
| 分子 | 名称: TcdB2,TccC3 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Photorhabdus luminescens (バクテリア) Photorhabdus luminescens (バクテリア) |
| 分子量 | 理論値: 274.14425 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MQNSQDFSIT ELSLPKGGGA ITGMGEALTP TGPDGMAALS LPLPISAGRG YAPAFTLNYN SGAGNSPFGL GWDCNVMTIR RRTHFGVPH YDETDTFLGP EGEVLVVADQ PRDESTLQGI NLGATFTVTG YRSRLESHFS RLEYWQPKTT GKTDFWLIYS P DGQVHLLG ...文字列: MQNSQDFSIT ELSLPKGGGA ITGMGEALTP TGPDGMAALS LPLPISAGRG YAPAFTLNYN SGAGNSPFGL GWDCNVMTIR RRTHFGVPH YDETDTFLGP EGEVLVVADQ PRDESTLQGI NLGATFTVTG YRSRLESHFS RLEYWQPKTT GKTDFWLIYS P DGQVHLLG KSPQARISNP SQTTQTAQWL LEASVSSRGE QIYYQYRAED DTGCEADEIT HHLQATAQRY LHIVYYGNRT AS ETLPGLD GSAPSQADWL FYLVFDYGER SNNLKTPPAF STTGSWLCRQ DRFSRYEYGF EIRTRRLCRQ VLMYHHLQAL DSK ITEHNG PTLVSRLILN YDESAIASTL VFVRRVGHEQ DGNVVTLPPL ELAYQDFSPR HHAHWQPMDV LANFNAIQRW QLVD LKGEG LPGLLYQDKG AWWYRSAQRL GEIGSDAVTW EKMQPLSVIP SLQSNASLVD INGDGQLDWV ITGPGLRGYH SQRPD GSWT RFTPLNALPV EYTHPRAQLA DLMGAGLSDL VLIGPKSVRL YANTRDGFAK GKDVVQSGEI TLPVPGADPR KLVAFS DVL GSGQAHLVEV SATKVTCWPN LGRGRFGQPI TLPGFSQPAT EFNPAQVYLA DLDGSGPTDL IYVHTNRLDI FLNKSGN GF AEPVTLRFPE GLRFDHTCQL QMADVQGLGV ASLILSVPHM SPHHWRCDLT NMKPWLLNEM NNNMGVHHTL RYRSSSQF W LDEKAAALTT GQTPVCYLPF PIHTLWQTET EDEISGNKLV TTLRYARGAW DGREREFRGF GYVEQTDSHQ LAQGNAPER TPPALTKNWY ATGLPVIDNA LSTEYWRDDQ AFAGFSPRFT TWQDNKDVPL TPEDDNSRYW FNRALKGQLL RSELYGLDDS TNKHVPYTV TEFRSQVRRL QHTDSRYPVL WSSVVESRNY HYERIASDPQ CSQNITLSSD RFGQPLKQLS VQYPRRQQPA I NLYPDTLP DKLLANSYDD QQRQLRLTYQ QSSWHHLTNN TVRVLGLPDS TRSDIFTYGA ENVPAGGLNL ELLSDKNSLI AD DKPREYL GQQKTAYTDG QNTTPLQTPT RQALIAFTET TVFNQSTLSA FNGSIPSDKL STTLEQAGYQ QTNYLFPRTG EDK VWVAHH GYTDYGTAAQ FWRPQKQSNT QLTGKITLIW DANYCVVVQT RDAAGLTTSA KYDWRFLTPV QLTDINDNQH LITL DALGR PITLRFWGTE NGKMTGYSSP EKASFSPPSD VNAAIELKKP LPVAQCQVYA PESWMPVLSQ KTFNRLAEQD WQKLY NARI ITEDGRICTL AYRRWVQSQK AIPQLISLLN NGPRLPPHSL TLTTDRYDHD PEQQIRQQVV FSDGFGRLLQ AAARHE AGM ARQRNEDGSL IINVQHTENR WAVTGRTEYD NKGQPIRTYQ PYFLNDWRYV SNDSARQEKE AYADTHVYDP IGREIKV IT AKGWFRRTLF TPWFTVNEDE NDTAAEVKKV KMPGSRPMKN IDPKLYQKTP TVSVYDNRGL IIRNIDFHRT TANGDPDT R ITRHQYDIHG HLNQSIDPRL YEAKQTNNTI KPNFLWQYDL TGNPLCTESI DAGRTVTLND IEGRPLLTVT ATGVIQTRQ YETSSLPGRL LSVAEQTPEE KTSRITERLI WAGNTEAEKD HNLAGQCVRH YDTAGVTRLE SLSLTGTVLS QSSQLLIDTQ EANWTGDNE TVWQNMLADD IYTTLSTFDA TGALLTQTDA KGNIQRLAYD VAGQLNGSWL TLKGQTEQVI IKSLTYSAAG Q KLREEHGN DVITEYSYEP ETQRLIGIKT RRPSDTKVLQ DLRYEYDPVG NVISIRNDAE ATRFWHNQKV MPENTYTYDS LY QLISATG REMANIGQQS HQFPSPALPS DNNTYTNYTR TYTYDRGGNL TKIQHSSPAT QNNYTTNITV SNRSNRAVLS TLT EDPAQV DALFDAGGHQ NTLISGQNLN WNTRGELQQV TLVKRDKGAN DDREWYRYSG DGRRMLKINE QQASNNAQTQ RVTY LPNLE LRLTQNSTAT TEDLQVITVG EAGRAQVRVL HWESGKPEDI DNNQLRYSYD NLIGSSQLEL DSEGQIISEE EYYPY GGTA LWAARNQTEA SYKTIRYSGK ERDATGLYYY GYRYYQPWIG RWLSSAPAGT IDGLNLYRMV RNNPVTLLDP DGLMPT IAE RIAALKKNKV TDSAPSPANA TNVAINIRPP VAPKPSLPKA STSSQPTTHP IGAANIKPTT SGSSIVAPLS PVGNKST SE ISLPESAQSS SSSTTSTNLQ KKSFTLYRAD NRSFEEMQSK FPEGFKAWTP LDTKMARQFA SIFIGQKDTS NLPKETVK N ISTWGAKPKL KDLSNYIKYT KDKSTVWVST AINTEAGGQS SGAPLHKIDM DLYEFAIDGQ KLNPLPEGRT KNMVPSLLL DTPQIETSSI IALNHGPVND AEISFLTTIP LKNVKPHKR UniProtKB: TcdB2, TccC3 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.1 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / 平均電子線量: 100.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: SPHIRE / 使用した粒子像数: 337823 |
| 初期 角度割当 | タイプ: NOT APPLICABLE |
| 最終 角度割当 | タイプ: NOT APPLICABLE |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)