+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 9d3g | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of CCR6 bound by SQA1 and OXM1 | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | MEMBRANE PROTEIN / GPCR / Antagonist / CCR6 / BRIL | ||||||
| 機能・相同性 | : / CHOLESTEROL / Chem-EBX 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)synthetic construct (人工物) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.26 Å | ||||||
 データ登録者 データ登録者 | Wasilko, D.J. / Wu, H. | ||||||
| 資金援助 | 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Structural basis for CCR6 modulation by allosteric antagonists. 著者: David Jonathan Wasilko / Brian S Gerstenberger / Kathleen A Farley / Wei Li / Jennifer Alley / Mark E Schnute / Ray J Unwalla / Jorge Victorino / Kimberly K Crouse / Ru Ding / Parag V ...著者: David Jonathan Wasilko / Brian S Gerstenberger / Kathleen A Farley / Wei Li / Jennifer Alley / Mark E Schnute / Ray J Unwalla / Jorge Victorino / Kimberly K Crouse / Ru Ding / Parag V Sahasrabudhe / Fabien Vincent / Richard K Frisbie / Alpay Dermenci / Andrew Flick / Chulho Choi / Gary Chinigo / James J Mousseau / John I Trujillo / Philippe Nuhant / Prolay Mondal / Vincent Lombardo / Daniel Lamb / Barbara J Hogan / Gurdeep Singh Minhas / Elena Segala / Christine Oswald / Ian W Windsor / Seungil Han / Mathieu Rappas / Robert M Cooke / Matthew F Calabrese / Gabriel Berstein / Atli Thorarensen / Huixian Wu /   要旨: The CC chemokine receptor 6 (CCR6) is a potential target for chronic inflammatory diseases. Previously, we reported an active CCR6 structure in complex with its cognate chemokine CCL20, revealing the ...The CC chemokine receptor 6 (CCR6) is a potential target for chronic inflammatory diseases. Previously, we reported an active CCR6 structure in complex with its cognate chemokine CCL20, revealing the molecular basis of CCR6 activation. Here, we present two inactive CCR6 structures in ternary complexes with different allosteric antagonists, CCR6/SQA1/OXM1 and CCR6/SQA1/OXM2. The oxomorpholine analogues, OXM1 and OXM2 are highly selective CCR6 antagonists which bind to an extracellular pocket and disrupt the receptor activation network. An energetically favoured U-shaped conformation in solution that resembles the bound form is observed for the active analogues. SQA1 is a squaramide derivative with close-in analogues reported as antagonists of chemokine receptors including CCR6. SQA1 binds to an intracellular pocket which overlaps with the G protein site, stabilizing a closed pocket that is a hallmark of inactive GPCRs. Minimal communication between the two allosteric pockets is observed, in contrast to the prevalent allosteric cooperativity model of GPCRs. This work highlights the versatility of GPCR antagonism by small molecules, complementing previous knowledge of CCR6 activation, and sheds light on drug discovery targeting CCR6. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  9d3g.cif.gz 9d3g.cif.gz | 204.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb9d3g.ent.gz pdb9d3g.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  9d3g.json.gz 9d3g.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  9d3g_validation.pdf.gz 9d3g_validation.pdf.gz | 1.4 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  9d3g_full_validation.pdf.gz 9d3g_full_validation.pdf.gz | 1.4 MB | 表示 | |
| XML形式データ |  9d3g_validation.xml.gz 9d3g_validation.xml.gz | 49.5 KB | 表示 | |
| CIF形式データ |  9d3g_validation.cif.gz 9d3g_validation.cif.gz | 72.6 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/d3/9d3g https://data.pdbj.org/pub/pdb/validation_reports/d3/9d3g ftp://data.pdbj.org/pub/pdb/validation_reports/d3/9d3g ftp://data.pdbj.org/pub/pdb/validation_reports/d3/9d3g | HTTPS FTP |
-関連構造データ
| 関連構造データ |  46534MC  9d3eC C: 同じ文献を引用 ( M: このデータのモデリングに利用したマップデータ |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 54623.020 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) Homo sapiens (ヒト)発現宿主:  |
|---|
-抗体 , 3種, 3分子 HKL
| #2: 抗体 | 分子量: 28832.098 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 発現宿主: Homo sapiens (ヒト) / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|---|
| #3: 抗体 | 分子量: 15755.214 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現) synthetic construct (人工物) / 発現宿主:  |
| #4: 抗体 | 分子量: 25343.348 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 発現宿主: Homo sapiens (ヒト) / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-非ポリマー , 3種, 3分子 

| #5: 化合物 | ChemComp-CLR / |
|---|---|
| #6: 化合物 | ChemComp-EBX / |
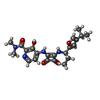
| #7: 化合物 | ChemComp-A1A2A / 分子量: 424.920 Da / 分子数: 1 / 由来タイプ: 合成 / 式: C24H25ClN2O3 / タイプ: SUBJECT OF INVESTIGATION |
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|---|
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: CCR6-BRIL/Fab/Nb in complex with SQA1 and OXM1 / タイプ: COMPLEX 詳細: CCR6-BRIL/Fab/Nb complex co-purified with SQA1 and OXM1. Entity ID: #1-#4 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 値: 120 kDa/nm / 実験値: NO |
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.5 詳細: 50 mM HEPES pH 7.5, 150 mM NaCl, 0.003% LMNG, 0.0003% CHS, 50 uM OXM1 and 50 uM of SQA1 |
| 試料 | 濃度: 1 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: CCR6-BRIL/Fab/Nb complex co-purified with SQA1 and OXM1. |
| 急速凍結 | 装置: FEI VITROBOT MARK IV / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 277 K |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 215000 X / 最大 デフォーカス(公称値): 2400 nm / 最小 デフォーカス(公称値): 800 nm / C2レンズ絞り径: 100 µm |
| 撮影 | 電子線照射量: 40 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) |
| 電子光学装置 | エネルギーフィルター名称: TFS Selectris / エネルギーフィルタースリット幅: 10 eV |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 5332464 | ||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.26 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 482484 / アルゴリズム: FOURIER SPACE / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: AB INITIO MODEL / 空間: REAL | ||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj









