+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8rkd | ||||||
|---|---|---|---|---|---|---|---|
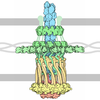
| タイトル | TadA/CpaF with AMPPNP | ||||||
 要素 要素 | Pilus assembly ATPase CpaF | ||||||
 キーワード キーワード | MOTOR PROTEIN / secretion / ATPase | ||||||
| 機能・相同性 | : / Type II/IV secretion system protein / Type II/IV secretion system protein / ATP hydrolysis activity / P-loop containing nucleoside triphosphate hydrolase / ADENOSINE-5'-DIPHOSPHATE / PHOSPHOAMINOPHOSPHONIC ACID-ADENYLATE ESTER / Pilus assembly ATPase CpaF 機能・相同性情報 機能・相同性情報 | ||||||
| 生物種 |  Caulobacter vibrioides NA1000 (バクテリア) Caulobacter vibrioides NA1000 (バクテリア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.8 Å | ||||||
 データ登録者 データ登録者 | Hohl, M. / Low, H. | ||||||
| 資金援助 |  英国, 1件 英国, 1件
| ||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Bidirectional pilus processing in the Tad pilus system motor CpaF. 著者: Michael Hohl / Emma J Banks / Max P Manley / Tung B K Le / Harry H Low /  要旨: The bacterial tight adherence pilus system (TadPS) assembles surface pili essential for adhesion and colonisation in many human pathogens. Pilus dynamics are powered by the ATPase CpaF (TadA), which ...The bacterial tight adherence pilus system (TadPS) assembles surface pili essential for adhesion and colonisation in many human pathogens. Pilus dynamics are powered by the ATPase CpaF (TadA), which drives extension and retraction cycles in Caulobacter crescentus through an unknown mechanism. Here we use cryogenic electron microscopy and cell-based light microscopy to characterise CpaF mechanism. We show that CpaF assembles into a hexamer with C2 symmetry in different nucleotide states. Nucleotide cycling occurs through an intra-subunit clamp-like mechanism that promotes sequential conformational changes between subunits. Moreover, a comparison of the active sites with different nucleotides bound suggests a mechanism for bidirectional motion. Conserved CpaF residues, predicted to interact with platform proteins CpaG (TadB) and CpaH (TadC), are mutated in vivo to establish their role in pilus processing. Our findings provide a model for how CpaF drives TadPS pilus dynamics and have broad implications for how other ancient type 4 filament family members power pilus assembly. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8rkd.cif.gz 8rkd.cif.gz | 747.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8rkd.ent.gz pdb8rkd.ent.gz | 626.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8rkd.json.gz 8rkd.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8rkd_validation.pdf.gz 8rkd_validation.pdf.gz | 1.6 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8rkd_full_validation.pdf.gz 8rkd_full_validation.pdf.gz | 1.7 MB | 表示 | |
| XML形式データ |  8rkd_validation.xml.gz 8rkd_validation.xml.gz | 77.5 KB | 表示 | |
| CIF形式データ |  8rkd_validation.cif.gz 8rkd_validation.cif.gz | 111.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rk/8rkd https://data.pdbj.org/pub/pdb/validation_reports/rk/8rkd ftp://data.pdbj.org/pub/pdb/validation_reports/rk/8rkd ftp://data.pdbj.org/pub/pdb/validation_reports/rk/8rkd | HTTPS FTP |
-関連構造データ
| 関連構造データ |  19275MC  8rjfC  8rklC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 46465.199 Da / 分子数: 6 / 由来タイプ: 組換発現 由来: (組換発現)  Caulobacter vibrioides NA1000 (バクテリア) Caulobacter vibrioides NA1000 (バクテリア)遺伝子: cpaF, CCNA_03037 / 発現宿主:  #2: 化合物 | ChemComp-ADP / #3: 化合物 | ChemComp-EPE / #4: 化合物 | #5: 化合物 | |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Hexameric complex of TadA / タイプ: COMPLEX / Entity ID: #1 / 由来: RECOMBINANT |
|---|---|
| 由来(天然) | 生物種:  Caulobacter vibrioides NA1000 (バクテリア) Caulobacter vibrioides NA1000 (バクテリア) |
| 由来(組換発現) | 生物種:  |
| 緩衝液 | pH: 7.4 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3000 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 40 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| EMソフトウェア | 名称: PHENIX / バージョン: 1.21rc1_4933: / カテゴリ: モデル精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.8 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 73200 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー





 PDBj
PDBj