+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8k9f | ||||||
|---|---|---|---|---|---|---|---|
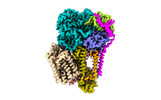
| タイトル | Cryo-EM structure of the photosynthetic alternative complex III from Chloroflexus aurantiacus at 2.9 angstrom | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | MEMBRANE PROTEIN / Photosynthetic alternative complex III | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報electron transfer activity / heme binding / membrane / metal ion binding / plasma membrane 類似検索 - 分子機能 | ||||||
| 生物種 |   Chloroflexus aurantiacus (バクテリア) Chloroflexus aurantiacus (バクテリア) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.9 Å | ||||||
 データ登録者 データ登録者 | Xu, X. | ||||||
| 資金援助 |  中国, 1件 中国, 1件
| ||||||
 引用 引用 |  ジャーナル: Plant Cell / 年: 2024 ジャーナル: Plant Cell / 年: 2024タイトル: Cryo-EM structure of HQNO-bound Alternative Complex III from the anoxygenic phototrophic bacterium Chloroflexus aurantiacus. 著者: Jiyu Xin / Zhenzhen Min / Lu Yu / Xinyi Yuan / Aokun Liu / Wenping Wu / Xin Zhang / Huimin He / Jingyi Wu / Yueyong Xin / Robert E Blankenship / Changlin Tian / Xiaoling Xu /   要旨: Alternative complex III (ACIII) couples quinol oxidation and electron acceptor reduction with potential transmembrane proton translocation. It is compositionally and structurally different from the ...Alternative complex III (ACIII) couples quinol oxidation and electron acceptor reduction with potential transmembrane proton translocation. It is compositionally and structurally different from the cytochrome bc1/b6f complexes, but functionally replaces these enzymes in the photosynthetic and/or respiratory electron transport chains (ETCs) of many bacteria. However, the true compositions and architectures of ACIIIs remain unclear, as do their structural and functional relevance in mediating the ETCs. We here determined cryogenic electron microscopy structures of photosynthetic ACIII isolated from Chloroflexus aurantiacus (CaACIIIp), in apo-form and in complexed form bound to a menadiol analog 2-heptyl-4-hydroxyquinoline-N-oxide (HQNO). Besides six canonical subunits (ActABCDEF), the structures revealed conformations of two previously unresolved subunits, ActG and I, which contributed to the complex stability. We also elucidated the structural basis of menaquinol oxidation and subsequent electron transfer along the [3Fe-4S]-6 hemes wire to its periplasmic electron acceptors, using electron paramagnetic resonance (EPR), spectroelectrochemistry, enzymatic analyses and molecular dynamics (MD) simulations. A unique insertion loop in ActE was shown to function in determining the binding specificity of CaACIIIp for downstream electron acceptors. This study broadens our understanding of the structural diversity and molecular evolution of ACIIIs, enabling further investigation of the (mena)quinol oxidoreductases evolved coupling mechanism in bacterial energy conservation. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8k9f.cif.gz 8k9f.cif.gz | 513.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8k9f.ent.gz pdb8k9f.ent.gz | 405 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8k9f.json.gz 8k9f.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8k9f_validation.pdf.gz 8k9f_validation.pdf.gz | 2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8k9f_full_validation.pdf.gz 8k9f_full_validation.pdf.gz | 2 MB | 表示 | |
| XML形式データ |  8k9f_validation.xml.gz 8k9f_validation.xml.gz | 79.7 KB | 表示 | |
| CIF形式データ |  8k9f_validation.cif.gz 8k9f_validation.cif.gz | 115.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/k9/8k9f https://data.pdbj.org/pub/pdb/validation_reports/k9/8k9f ftp://data.pdbj.org/pub/pdb/validation_reports/k9/8k9f ftp://data.pdbj.org/pub/pdb/validation_reports/k9/8k9f | HTTPS FTP |
-関連構造データ
| 関連構造データ |  36985MC  8k9eC  8x2jC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-タンパク質 , 5種, 5分子 ABCEG
| #1: タンパク質 | 分子量: 25247.039 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV2 |
|---|---|
| #2: タンパク質 | 分子量: 113115.359 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV3 |
| #3: タンパク質 | 分子量: 55223.520 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV4 |
| #5: タンパク質 | 分子量: 23017.016 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV6 |
| #7: タンパク質 | 分子量: 12485.551 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV8 |
-Quinol:cytochrome c oxidoreductase ... , 2種, 2分子 DF
| #4: タンパク質 | 分子量: 19648.570 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV5 |
|---|---|
| #6: タンパク質 | 分子量: 45721.672 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア)参照: UniProt: A9WEV7 |
-タンパク質・ペプチド , 1種, 1分子 I
| #8: タンパク質・ペプチド | 分子量: 4322.134 Da / 分子数: 1 / 由来タイプ: 天然 由来: (天然)   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) |
|---|
-非ポリマー , 7種, 14分子 






| #9: 化合物 | ChemComp-HEC / #10: 化合物 | #11: 化合物 | ChemComp-F3S / | #12: 化合物 | ChemComp-MG / | #13: 化合物 | ChemComp-JLQ / [( | 分子量: 663.906 Da / 分子数: 1 / 由来タイプ: 合成 / 式: C35H70NO8P #14: 化合物 | ChemComp-JL3 / [( | 分子量: 663.906 Da / 分子数: 1 / 由来タイプ: 合成 / 式: C35H70NO8P #15: 化合物 | ChemComp-JM9 / | 分子量: 765.240 Da / 分子数: 1 / 由来タイプ: 合成 / 式: C48H92O6 |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Alternative complex III / タイプ: COMPLEX / Entity ID: #1-#8 / 由来: NATURAL |
|---|---|
| 由来(天然) | 生物種:   Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) Chloroflexus aurantiacus (strain ATCC 29366 / DSM 635 / J-10-fl) (バクテリア) |
| 緩衝液 | pH: 8 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1800 nm / 最小 デフォーカス(公称値): 1000 nm |
| 撮影 | 電子線照射量: 50 e/Å2 フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) |
- 解析
解析
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 3次元再構成 | 解像度: 2.9 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 103633 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




 PDBj
PDBj





















