+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7ydq | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of PfNT1(Y190A)-GFP in complex with GSK4 | |||||||||
 要素 要素 | Nucleoside transporter 1,Green fluorescent protein | |||||||||
 キーワード キーワード | MEMBRANE PROTEIN / malaria / nucleoside transporter / GSK4 / TRANSPORT PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Transport of nucleosides and free purine and pyrimidine bases across the plasma membrane / Ribavirin ADME / adenosine transport / Azathioprine ADME / nucleoside transmembrane transporter activity / purine nucleobase transport / serine-type endopeptidase inhibitor activity / extracellular space / metal ion binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.04 Å | |||||||||
 データ登録者 データ登録者 | Wang, C. / Yu, L.Y. / Li, J.L. / Ren, R.B. / Deng, D. | |||||||||
| 資金援助 |  中国, 2件 中国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Structural basis of the substrate recognition and inhibition mechanism of Plasmodium falciparum nucleoside transporter PfENT1. 著者: Chen Wang / Leiye Yu / Jiying Zhang / Yanxia Zhou / Bo Sun / Qingjie Xiao / Minhua Zhang / Huayi Liu / Jinhong Li / Jialu Li / Yunzi Luo / Jie Xu / Zhong Lian / Jingwen Lin / Xiang Wang / ...著者: Chen Wang / Leiye Yu / Jiying Zhang / Yanxia Zhou / Bo Sun / Qingjie Xiao / Minhua Zhang / Huayi Liu / Jinhong Li / Jialu Li / Yunzi Luo / Jie Xu / Zhong Lian / Jingwen Lin / Xiang Wang / Peng Zhang / Li Guo / Ruobing Ren / Dong Deng /  要旨: By lacking de novo purine biosynthesis enzymes, Plasmodium falciparum requires purine nucleoside uptake from host cells. The indispensable nucleoside transporter ENT1 of P. falciparum facilitates ...By lacking de novo purine biosynthesis enzymes, Plasmodium falciparum requires purine nucleoside uptake from host cells. The indispensable nucleoside transporter ENT1 of P. falciparum facilitates nucleoside uptake in the asexual blood stage. Specific inhibitors of PfENT1 prevent the proliferation of P. falciparum at submicromolar concentrations. However, the substrate recognition and inhibitory mechanism of PfENT1 are still elusive. Here, we report cryo-EM structures of PfENT1 in apo, inosine-bound, and inhibitor-bound states. Together with in vitro binding and uptake assays, we identify that inosine is the primary substrate of PfENT1 and that the inosine-binding site is located in the central cavity of PfENT1. The endofacial inhibitor GSK4 occupies the orthosteric site of PfENT1 and explores the allosteric site to block the conformational change of PfENT1. Furthermore, we propose a general "rocker switch" alternating access cycle for ENT transporters. Understanding the substrate recognition and inhibitory mechanisms of PfENT1 will greatly facilitate future efforts in the rational design of antimalarial drugs. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7ydq.cif.gz 7ydq.cif.gz | 141.6 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7ydq.ent.gz pdb7ydq.ent.gz | 89.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7ydq.json.gz 7ydq.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7ydq_validation.pdf.gz 7ydq_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7ydq_full_validation.pdf.gz 7ydq_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  7ydq_validation.xml.gz 7ydq_validation.xml.gz | 30.2 KB | 表示 | |
| CIF形式データ |  7ydq_validation.cif.gz 7ydq_validation.cif.gz | 44.8 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/yd/7ydq https://data.pdbj.org/pub/pdb/validation_reports/yd/7ydq ftp://data.pdbj.org/pub/pdb/validation_reports/yd/7ydq ftp://data.pdbj.org/pub/pdb/validation_reports/yd/7ydq | HTTPS FTP |
-関連構造データ
| 関連構造データ |  33756MC  7wn0C  7wn1C M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 77035.766 Da / 分子数: 1 / 変異: Y190A / 由来タイプ: 組換発現 詳細: PfNT1(Y190A) fused with GFP the GFP was inserted into PfNT1 between K370 and K371 由来: (組換発現)   遺伝子: PF3D7_1347200, GFP / 細胞株 (発現宿主): IPLB-Sf-21-AE(Sf9) 発現宿主:  参照: UniProt: Q8IDM6, UniProt: P42212 |
|---|---|
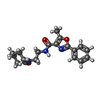
| #2: 化合物 | ChemComp-IRX / |
| 研究の焦点であるリガンドがあるか | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: nucleoside/nucleobase transporter fusion with GFP / タイプ: COMPLEX 詳細: the cDNA of the GFP was cloned into PfNT1 between K370 and K371 Entity ID: #1 / 由来: RECOMBINANT | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 47.5 kDa/nm / 実験値: NO | ||||||||||||
| 由来(天然) |
| ||||||||||||
| 由来(組換発現) | 生物種:  | ||||||||||||
| 緩衝液 | pH: 6 | ||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1800 nm / 最小 デフォーカス(公称値): 1100 nm |
| 撮影 | 電子線照射量: 52.452 e/Å2 フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 4.04 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 329768 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 精密化 | 交差検証法: NONE 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 171.65 Å2 | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー





 PDBj
PDBj