+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7ntc | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Trimeric SARS-CoV-2 spike ectodomain bound to P008_056 Fab | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | VIRAL PROTEIN / SARS-CoV-2 / spike / biliverdin / COVID19 / Antibody / Fab / epitope / NTD | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / host cell endoplasmic reticulum-Golgi intermediate compartment membrane ...Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / entry receptor-mediated virion attachment to host cell / receptor-mediated endocytosis of virus by host cell / Attachment and Entry / membrane fusion / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / receptor ligand activity / host cell surface receptor binding / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / SARS-CoV-2 activates/modulates innate and adaptive immune responses / host cell plasma membrane / virion membrane / identical protein binding / membrane / plasma membrane 類似検索 - 分子機能 | ||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | ||||||
 データ登録者 データ登録者 | Rosa, A. / Pye, V.E. / Nans, A. / Cherepanov, P. | ||||||
| 資金援助 |  英国, 1件 英国, 1件
| ||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2021 ジャーナル: Sci Adv / 年: 2021タイトル: SARS-CoV-2 can recruit a heme metabolite to evade antibody immunity. 著者: Annachiara Rosa / Valerie E Pye / Carl Graham / Luke Muir / Jeffrey Seow / Kevin W Ng / Nicola J Cook / Chloe Rees-Spear / Eleanor Parker / Mariana Silva Dos Santos / Carolina Rosadas / ...著者: Annachiara Rosa / Valerie E Pye / Carl Graham / Luke Muir / Jeffrey Seow / Kevin W Ng / Nicola J Cook / Chloe Rees-Spear / Eleanor Parker / Mariana Silva Dos Santos / Carolina Rosadas / Alberto Susana / Hefin Rhys / Andrea Nans / Laura Masino / Chloe Roustan / Evangelos Christodoulou / Rachel Ulferts / Antoni G Wrobel / Charlotte-Eve Short / Michael Fertleman / Rogier W Sanders / Judith Heaney / Moira Spyer / Svend Kjær / Andy Riddell / Michael H Malim / Rupert Beale / James I MacRae / Graham P Taylor / Eleni Nastouli / Marit J van Gils / Peter B Rosenthal / Massimo Pizzato / Myra O McClure / Richard S Tedder / George Kassiotis / Laura E McCoy / Katie J Doores / Peter Cherepanov /     要旨: The coronaviral spike is the dominant viral antigen and the target of neutralizing antibodies. We show that SARS-CoV-2 spike binds biliverdin and bilirubin, the tetrapyrrole products of heme ...The coronaviral spike is the dominant viral antigen and the target of neutralizing antibodies. We show that SARS-CoV-2 spike binds biliverdin and bilirubin, the tetrapyrrole products of heme metabolism, with nanomolar affinity. Using cryo-electron microscopy and x-ray crystallography, we mapped the tetrapyrrole interaction pocket to a deep cleft on the spike N-terminal domain (NTD). At physiological concentrations, biliverdin significantly dampened the reactivity of SARS-CoV-2 spike with immune sera and inhibited a subset of neutralizing antibodies. Access to the tetrapyrrole-sensitive epitope is gated by a flexible loop on the distal face of the NTD. Accompanied by profound conformational changes in the NTD, antibody binding requires relocation of the gating loop, which folds into the cleft vacated by the metabolite. Our results indicate that SARS-CoV-2 spike NTD harbors a dominant epitope, access to which can be controlled by an allosteric mechanism that is regulated through recruitment of a metabolite. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7ntc.cif.gz 7ntc.cif.gz | 675.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7ntc.ent.gz pdb7ntc.ent.gz | 561.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7ntc.json.gz 7ntc.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7ntc_validation.pdf.gz 7ntc_validation.pdf.gz | 2.7 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7ntc_full_validation.pdf.gz 7ntc_full_validation.pdf.gz | 2.7 MB | 表示 | |
| XML形式データ |  7ntc_validation.xml.gz 7ntc_validation.xml.gz | 114.5 KB | 表示 | |
| CIF形式データ |  7ntc_validation.cif.gz 7ntc_validation.cif.gz | 171.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/nt/7ntc https://data.pdbj.org/pub/pdb/validation_reports/nt/7ntc ftp://data.pdbj.org/pub/pdb/validation_reports/nt/7ntc ftp://data.pdbj.org/pub/pdb/validation_reports/nt/7ntc | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-抗体 , 2種, 2分子 HL
| #2: 抗体 | 分子量: 27239.400 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / Cell (発現宿主): Expi293 / 発現宿主: Homo sapiens (ヒト) / Cell (発現宿主): Expi293 / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|---|
| #3: 抗体 | 分子量: 25253.180 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / Cell (発現宿主): Expi293 / 発現宿主: Homo sapiens (ヒト) / Cell (発現宿主): Expi293 / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-タンパク質 / 非ポリマー , 2種, 5分子 ABC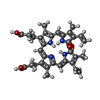

| #1: タンパク質 | 分子量: 142269.859 Da / 分子数: 3 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: S, 2 / Cell (発現宿主): Expi293 / 発現宿主:  Homo sapiens (ヒト) / 参照: UniProt: P0DTC2 Homo sapiens (ヒト) / 参照: UniProt: P0DTC2#5: 化合物 | |
|---|
-糖 , 2種, 54分子 
| #4: 多糖 | 2-acetamido-2-deoxy-beta-D-glucopyranose-(1-4)-2-acetamido-2-deoxy-beta-D-glucopyranose #6: 糖 | ChemComp-NAG / |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | Y |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 値: 0.47886 MDa / 実験値: NO | ||||||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||||||
| 緩衝液 | pH: 8 詳細: 150 mM NaCl, 1 mM ethylenediaminetetraacetic acid (EDTA), 25 mM Tris-HCl, pH 8.0 | ||||||||||||||||||||||||||||
| 試料 | 濃度: 0.6 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES 詳細: SARS-CoV-2 spike ectodomain (0.6 mg/ml final concentration in TBSE supplemented with 0.1% n-octylglucoside) with 0.2 mg/ml P008_056 Fab | ||||||||||||||||||||||||||||
| 試料支持 | グリッドのタイプ: Quantifoil R2/2 | ||||||||||||||||||||||||||||
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 51 e/Å2 / 検出モード: COUNTING フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 撮影したグリッド数: 1 / 実像数: 17010 詳細: A total of 17010 movies were collected with a pixel size of 1.38 Angstrom and total electron exposure of 51 electrons per square Angstrom, spread over 40 frames. |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19rc5_4047: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 78291 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: OTHER / 空間: REAL 詳細: in addition to the spike: 6APC and 6PHB were used as templates for the heavy and light chains of the Fab respectively | ||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 6ZGE | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj







