+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the NuA3 complex bound to Ace-coenzyme A | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | NuA3 / Cryo-EM / Histone / nucleosome / TRANSFERASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報PI5P Regulates TP53 Acetylation / NuA3b histone acetyltransferase complex / NuA3a histone acetyltransferase complex / NuA3 histone acetyltransferase complex / histone H3K36me3 reader activity / Platelet degranulation / SUMOylation of transcription cofactors / transcription factor TFIIF complex / mediator complex / Ino80 complex ...PI5P Regulates TP53 Acetylation / NuA3b histone acetyltransferase complex / NuA3a histone acetyltransferase complex / NuA3 histone acetyltransferase complex / histone H3K36me3 reader activity / Platelet degranulation / SUMOylation of transcription cofactors / transcription factor TFIIF complex / mediator complex / Ino80 complex / histone H3K4me3 reader activity / silent mating-type cassette heterochromatin formation / SWI/SNF complex / transcription factor TFIID complex / RNA polymerase II general transcription initiation factor activity / histone acetyltransferase activity / NuA4 histone acetyltransferase complex / subtelomeric heterochromatin formation / RNA polymerase II preinitiation complex assembly / histone acetyltransferase / transcription coregulator activity / transcription initiation at RNA polymerase II promoter / positive regulation of transcription elongation by RNA polymerase II / chromatin organization / histone binding / transcription by RNA polymerase II / chromosome, telomeric region / chromatin remodeling / DNA repair / chromatin binding / regulation of DNA-templated transcription / regulation of transcription by RNA polymerase II / DNA-templated transcription / chromatin / positive regulation of transcription by RNA polymerase II / DNA binding / zinc ion binding / nucleus / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.13 Å | |||||||||
 データ登録者 データ登録者 | Zhang HQ / Wang YR | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Structure of the NuA3 complex bound to Acetyl-coenzyme A 著者: Wang YR / Zhang HQ | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_65145.map.gz emd_65145.map.gz | 79 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-65145-v30.xml emd-65145-v30.xml emd-65145.xml emd-65145.xml | 21 KB 21 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_65145_fsc.xml emd_65145_fsc.xml | 9.2 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_65145.png emd_65145.png | 51.4 KB | ||
| Filedesc metadata |  emd-65145.cif.gz emd-65145.cif.gz | 7.1 KB | ||
| その他 |  emd_65145_half_map_1.map.gz emd_65145_half_map_1.map.gz emd_65145_half_map_2.map.gz emd_65145_half_map_2.map.gz | 77.8 MB 77.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-65145 http://ftp.pdbj.org/pub/emdb/structures/EMD-65145 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-65145 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-65145 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9vkwMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_65145.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_65145.map.gz / 形式: CCP4 / 大きさ: 83.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.9643 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_65145_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_65145_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : NuA3
| 全体 | 名称: NuA3 |
|---|---|
| 要素 |
|
-超分子 #1: NuA3
| 超分子 | 名称: NuA3 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Histone acetyltransferase SAS3
| 分子 | 名称: Histone acetyltransferase SAS3 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: histone acetyltransferase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 97.722461 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSLTANDESP KPKKNALLKN LEIDDLIHSQ FVRSDTNGHR TTRRLFNSDA SISHRIRGSV RSDKGLNKIK KGLISQQSKL ASENSSQNI VNRDNKMGAV SFPIIEPNIE VSEELKVRIK YDSIKFFNFE RLISKSSVIA PLVNKNITSS GPLIGFQRRV N RLKQTWDL ...文字列: MSLTANDESP KPKKNALLKN LEIDDLIHSQ FVRSDTNGHR TTRRLFNSDA SISHRIRGSV RSDKGLNKIK KGLISQQSKL ASENSSQNI VNRDNKMGAV SFPIIEPNIE VSEELKVRIK YDSIKFFNFE RLISKSSVIA PLVNKNITSS GPLIGFQRRV N RLKQTWDL ATENMEYPYS SDNTPFRDND SWQWYVPYGG TIKKMKDFST KRTLPTWEDK IKFLTFLENS KSATYINGNV SL CNHNETD QENEDRKKRK GKVPRIKNKV WFSQIEYIVL RNYEIKPWYT SPFPEHINQN KMVFICEFCL KYMTSRYTFY RHQ LKCLTF KPPGNEIYRD GKLSVWEIDG RENVLYCQNL CLLAKCFINS KTLYYDVEPF IFYILTERED TENHPYQNAA KFHF VGYFS KEKFNSNDYN LSCILTLPIY QRKGYGQFLM EFSYLLSRKE SKFGTPQKPL SDLGLLTYRT FWKIKCAEVL LKLRD SARR RSNNKNEDTF QQVSLNDIAK LTGMIPTDVV FGLEQLQVLY RHKTRSLSSL DDFNYIIKID SWNRIENIYK TWSSKN YPR VKYDKLLWEP IILGPSFGIN GMMNLEPTAL ADEALTNETM APVISNNTHI ENYNNSRAHN KRRRRRRRSS EHKTSKL HV NNIIEPEVPA TDFFEDTVSS LTEYMCDYKN TNNDRLIYQA EKRVLESIHD RKGIPRSKFS TETHWELCFT IKNSETPL G NHAARRNDTG ISSLEQDEVE NDVDTELYVG ENAKEDEDED EDFTLDDDIE DEQISEENDE EEDTYEEDSD DDEDGKRKG QEQDENDIES HIRKERVRKR RKITLIEDDE E UniProtKB: Histone acetyltransferase SAS3 |
-分子 #2: NuA3 HAT complex component NTO1
| 分子 | 名称: NuA3 HAT complex component NTO1 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 86.146328 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MNRGSLDDGP KLREEKHFQD FYPDLNADTL LPFIVPLVET KDNSTDTDSD DISNRNNREI GSVKSVQTKE LIFKGRVTTE PLVLKKNEV EFQKCKITTN ELKGKKNPYC VRFNESFISR YYHINKVRNR KSYKQQQKEF DGVEAPYFTK FSSKEAPNIT I STSTKSAI ...文字列: MNRGSLDDGP KLREEKHFQD FYPDLNADTL LPFIVPLVET KDNSTDTDSD DISNRNNREI GSVKSVQTKE LIFKGRVTTE PLVLKKNEV EFQKCKITTN ELKGKKNPYC VRFNESFISR YYHINKVRNR KSYKQQQKEF DGVEAPYFTK FSSKEAPNIT I STSTKSAI QKFASISPNL VNFKPQYDMD EQDELYLHYL NKRYFKDQMS HEIFEILMTT LETEWFHIEK HIPSTNSLIA RH NILRDCK NYELYGSDDG TGLSMDQACA VCLGTDSDNL NTIVFCDGCD IAVHQECYGI IFIPEGKWLC RRCMISKNNF ATC LMCPSH TGAFKQTDTG SWVHNICALW LPELYFSNLH YMEPIEGVQN VSVSRWKLNC YICKKKMGAC IQCFQRNCFT AYHV TCARR AGLYMSKGKC TIQELASNQF SQKYSVESFC HKHAPRGWQT SIEGINKARK YFSLLSTLQT ETPQHNEAND RTNSK FNKT IWKTPNQTPV APHVFAEILQ KVVDFFGLAN PPAGAFDICK YWSMKRELTG GTPLTACFEN NSLGSLTEEQ VQTRID FAN DQLEDLYRLK ELTTLVKKRT QASNSLSRSR KKVFDIVKSP QKYLLKINVL DIFIKSEQFK ALERLVTEPK LLVILEK CK HCDFDTVQIF KEEIMHFFEV LETLPGASRI LQTVSSKAKE QVTNLIGLIE HVDIKKLLSR DFIINDDKIE ERPWSGPV I MEEEGLSDAE ELSAGEHRML KLILNSG UniProtKB: NuA3 HAT complex component NTO1 |
-分子 #3: Protein YNG1
| 分子 | 名称: Protein YNG1 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 25.391049 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MEHLANENSD SDIRYSFLST LDHLPCELIR SLRLMQTIDL FKNEEDEPGM ERACRDLLLV ATYINDLVDD QIHFLKQHKK ELEIQKSVT KNFNSSLENI KSKLTLEEPG AYKEPKLLLK INLKKAKSRE RKESITSPTI GINQGDVTEG NNNQEEVYCF C RNVSYGPM ...文字列: MEHLANENSD SDIRYSFLST LDHLPCELIR SLRLMQTIDL FKNEEDEPGM ERACRDLLLV ATYINDLVDD QIHFLKQHKK ELEIQKSVT KNFNSSLENI KSKLTLEEPG AYKEPKLLLK INLKKAKSRE RKESITSPTI GINQGDVTEG NNNQEEVYCF C RNVSYGPM VACDNPACPF EWFHYGCVGL KQAPKGKWYC SKDCKEIANQ RSKSKRQKRR K UniProtKB: Protein YNG1 |
-分子 #4: Transcription initiation factor TFIID subunit 14
| 分子 | 名称: Transcription initiation factor TFIID subunit 14 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 27.473154 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MVATVKRTIR IKTQQHILPE VPPVENFPVR QWSIEIVLLD DEGKEIPATI FDKVIYHLHP TFANPNRTFT DPPFRIEEQG WGGFPLDIS VFLLEKAGER KIPHDLNFLQ ESYEVEHVIQ IPLNKPLLTE ELAKSGSTEE TTANTGTIGK RRTTTNTTAE P KAKRAKTG ...文字列: MVATVKRTIR IKTQQHILPE VPPVENFPVR QWSIEIVLLD DEGKEIPATI FDKVIYHLHP TFANPNRTFT DPPFRIEEQG WGGFPLDIS VFLLEKAGER KIPHDLNFLQ ESYEVEHVIQ IPLNKPLLTE ELAKSGSTEE TTANTGTIGK RRTTTNTTAE P KAKRAKTG SASTVKGSVD LEKLAFGLTK LNEDDLVGVV QMVTDNKTPE MNVTNNVEEG EFIIDLYSLP EGLLKSLWDY VK KNTE UniProtKB: Transcription initiation factor TFIID subunit 14 |
-分子 #5: Chromatin modification-related protein EAF6
| 分子 | 名称: Chromatin modification-related protein EAF6 / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 12.915704 KDa |
| 組換発現 | 生物種:  Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MTDELKSYEA LKAELKKSLQ DRREQEDTFD NLQQEIYDKE TEYFSHNSNN NHSGHGGAHG SKSHYSGNII KGFDTFSKSH HSHADSAFN NNDRIFSLSS ATYVKQQHGQ SQND UniProtKB: Chromatin modification-related protein EAF6 |
-分子 #6: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 6 / コピー数: 4 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #7: ACETYL COENZYME *A
| 分子 | 名称: ACETYL COENZYME *A / タイプ: ligand / ID: 7 / コピー数: 1 / 式: ACO |
|---|---|
| 分子量 | 理論値: 809.571 Da |
| Chemical component information | 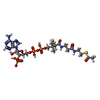 ChemComp-ACO: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





































