+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of mouse TRPM3 alpha 2 in complex with antagonist Ononetin | |||||||||
 マップデータ マップデータ | Cryo-EM structure of mouse TRPM3 alpha 2 in complex with antagonist Ononetin | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Ca2+ channel Ononetin-bound Closed conformation / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報protein tetramerization / calcium channel activity / calmodulin binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.61 Å | |||||||||
 データ登録者 データ登録者 | Shkumatov AV / Schenck S / Brunner JD | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Cryo-EM structure of mouse TRPM3 alpha 2 in complex with antagonist Ononetin 著者: Shkumatov AV / Schenck S / Brunner JD | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_53173.map.gz emd_53173.map.gz | 237.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-53173-v30.xml emd-53173-v30.xml emd-53173.xml emd-53173.xml | 28 KB 28 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_53173_fsc.xml emd_53173_fsc.xml | 18.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_53173.png emd_53173.png | 128.8 KB | ||
| マスクデータ |  emd_53173_msk_1.map emd_53173_msk_1.map | 476.8 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-53173.cif.gz emd-53173.cif.gz | 7.5 KB | ||
| その他 |  emd_53173_additional_1.map.gz emd_53173_additional_1.map.gz emd_53173_additional_2.map.gz emd_53173_additional_2.map.gz emd_53173_half_map_1.map.gz emd_53173_half_map_1.map.gz emd_53173_half_map_2.map.gz emd_53173_half_map_2.map.gz | 237.7 MB 104 MB 441.4 MB 441.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-53173 http://ftp.pdbj.org/pub/emdb/structures/EMD-53173 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-53173 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-53173 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9qhmMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_53173.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_53173.map.gz / 形式: CCP4 / 大きさ: 476.8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of mouse TRPM3 alpha 2 in complex with antagonist Ononetin | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.693 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_53173_msk_1.map emd_53173_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Input for consensus map together with main map
| ファイル | emd_53173_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Input for consensus map together with main map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: Consensus map used for model building and phenix validation
| ファイル | emd_53173_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Consensus map used for model building and phenix validation | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: halfB
| ファイル | emd_53173_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | halfB | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: halfA
| ファイル | emd_53173_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | halfA | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tetrameric assembly of mouse TRPM3 alpha 2 with inhibitor Ononetin
| 全体 | 名称: Tetrameric assembly of mouse TRPM3 alpha 2 with inhibitor Ononetin |
|---|---|
| 要素 |
|
-超分子 #1: Tetrameric assembly of mouse TRPM3 alpha 2 with inhibitor Ononetin
| 超分子 | 名称: Tetrameric assembly of mouse TRPM3 alpha 2 with inhibitor Ononetin タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 161 KDa |
-分子 #1: MKIAA1616 protein
| 分子 | 名称: MKIAA1616 protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 161.96325 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MSGKKWRDAG ELERGCSDRE DSAESRRRSR SASRGRFAES WKRLSSKQGS TKRSGLPAQQ TPAQKSWIER AFYKRECVHI IPSTKDPHR CCCGRLIGQH VGLTPSISVL QNEKNESRLS RNDIQSEKWS ISKHTQLSPT DAFGTIEFQG GGHSNKAMYV R VSFDTKPD ...文字列: MSGKKWRDAG ELERGCSDRE DSAESRRRSR SASRGRFAES WKRLSSKQGS TKRSGLPAQQ TPAQKSWIER AFYKRECVHI IPSTKDPHR CCCGRLIGQH VGLTPSISVL QNEKNESRLS RNDIQSEKWS ISKHTQLSPT DAFGTIEFQG GGHSNKAMYV R VSFDTKPD LLLHLMTKEW QLELPKLLIS VHGGLQNFEL QPKLKQVFGK GLIKAAMTTG AWIFTGGVNT GVIRHVGDAL KD HASKSRG KICTIGIAPW GIVENQEDLI GRDVVRPYQT MSNPMSKLTV LNSMHSHFIL ADNGTTGKYG AEVKLRRQLE KHI SLQKIN TRIGQGVPVV ALIVEGGPNV ISIVLEYLRD TPPVPVVVCD GSGRASDILA FGHKYSEEGG LINESLRDQL LVTI QKTFT YTRTQAQHLF IILMECMKKK ELITVFRMGS EGHQDIDLAI LTALLKGANA SAPDQLSLAL AWNRVDIARS QIFIY GQQW PVGSLEQAML DALVLDRVDF VKLLIENGVS MHRFLTISRL EELYNTRHGP SNTLYHLVRD VKKGNLPPDY RISLID IGL VIEYLMGGAY RCNYTRKRFR TLYHNLFGPK RPKALKLLGM EDDIPLRRGR KTTKKREEEV DIDLDDPEIN HFPFPFH EL MVWAVLMKRQ KMALFFWQHG EEAMAKALVA CKLCKAMAHE ASENDMVDDI SQELNHNSRD FGQLAVELLD QSYKQDEQ L AMKLLTYELK NWSNATCLQL AVAAKHRDFI AHTCSQMLLT DMWMGRLRMR KNSGLKVILG ILLPPSILSL EFKNKDDMP YMTQAQEIHL QEKEPEEPEK PTKEKDEEDM ELTAMLGRSN GESSRKKDEE EVQSRHRLIP VGRKIYEFYN APIVKFWFYT LAYIGYLML FNYIVLVKME RWPSTQEWIV ISYIFTLGIE KMREILMSEP GKLLQKVKVW LQEYWNVTDL IAILLFSVGM I LRLQDQPF RSDGRVIYCV NIIYWYIRLL DIFGVNKYLG PYVMMIGKMM IDMMYFVIIM LVVLMSFGVA RQAILFPNEE PS WKLAKNI FYMPYWMIYG EVFADQIDPP CGQNETREDG KTIQLPPCKT GAWIVPAIMA CYLLVANILL VNLLIAVFNN TFF EVKSIS NQVWKFQRYQ LIMTFHERPV LPPPLIIFSH MTMIFQHVCC RWRKHESDQD ERDYGLKLFI TDDELKKVHD FEEQ CIEEY FREKDDRFNS SNDERIRVTS ERVENMSMRL EEVNEREHSM KASLQTVDIR LAQLEDLIGR MATALERLTG LERAE SNKI RSRTSSDCTD AAYIVRQSSF NSQEGNTFKL QESIDPAGEE TISPTSPTLM PRMRSHSFYS VALEVLFQGP QGTEQK LIS EEDLRGASMD EKTTGWRGGH VVEGLAGELE QLRARLEHHP QGQREP UniProtKB: Transient receptor potential cation channel subfamily M member 3 |
-分子 #2: 1-[2,4-bis(oxidanyl)phenyl]-2-(4-methoxyphenyl)ethanone
| 分子 | 名称: 1-[2,4-bis(oxidanyl)phenyl]-2-(4-methoxyphenyl)ethanone タイプ: ligand / ID: 2 / コピー数: 4 / 式: A1D6M |
|---|---|
| 分子量 | 理論値: 258.269 Da |
-分子 #3: 1,2-DIACYL-GLYCEROL-3-SN-PHOSPHATE
| 分子 | 名称: 1,2-DIACYL-GLYCEROL-3-SN-PHOSPHATE / タイプ: ligand / ID: 3 / コピー数: 4 / 式: 3PH |
|---|---|
| 分子量 | 理論値: 704.998 Da |
| Chemical component information |  ChemComp-3PH: |
-分子 #4: (25R)-14beta,17beta-spirost-5-en-3beta-ol
| 分子 | 名称: (25R)-14beta,17beta-spirost-5-en-3beta-ol / タイプ: ligand / ID: 4 / コピー数: 8 / 式: YUV |
|---|---|
| 分子量 | 理論値: 414.621 Da |
| Chemical component information | 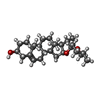 ChemComp-YUV: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
詳細: 10 mM Hepes pH 7.5, 150 mM NaCl, 0.063% Glycodiosgenin, 10 uM Ononetin | |||||||||||||||
| グリッド | モデル: Quantifoil R2/1 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GRAPHENE / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 279.15 K / 装置: LEICA EM GP / 詳細: GP2. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL CRYO ARM 300 |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 62.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.0 µm 最小 デフォーカス(公称値): 0.7000000000000001 µm |
 ムービー
ムービー コントローラー
コントローラー











 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)






























































