+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | HsSTING with cGAMP/C53/DCA | |||||||||
 マップデータ マップデータ | HsSTING cGAMP/C53/DCA with C2 symmetry | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Innate immunity / membrane protein / IMMUNE SYSTEM | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報STING complex / STAT6-mediated induction of chemokines / serine/threonine protein kinase complex / protein localization to endoplasmic reticulum / 2',3'-cyclic GMP-AMP binding / cyclic-di-GMP binding / STING mediated induction of host immune responses / positive regulation of type I interferon-mediated signaling pathway / IRF3-mediated induction of type I IFN / proton channel activity ...STING complex / STAT6-mediated induction of chemokines / serine/threonine protein kinase complex / protein localization to endoplasmic reticulum / 2',3'-cyclic GMP-AMP binding / cyclic-di-GMP binding / STING mediated induction of host immune responses / positive regulation of type I interferon-mediated signaling pathway / IRF3-mediated induction of type I IFN / proton channel activity / reticulophagy / cGAS/STING signaling pathway / pattern recognition receptor signaling pathway / cellular response to exogenous dsRNA / cytoplasmic pattern recognition receptor signaling pathway / protein complex oligomerization / autophagosome membrane / positive regulation of macroautophagy / autophagosome assembly / cellular response to interferon-beta / positive regulation of defense response to virus by host / positive regulation of type I interferon production / endoplasmic reticulum-Golgi intermediate compartment membrane / signaling adaptor activity / activation of innate immune response / positive regulation of interferon-beta production / autophagosome / secretory granule membrane / Regulation of innate immune responses to cytosolic DNA / cytoplasmic vesicle membrane / antiviral innate immune response / protein serine/threonine kinase binding / SARS-CoV-1 activates/modulates innate immune responses / peroxisome / regulation of inflammatory response / defense response to virus / RNA polymerase II-specific DNA-binding transcription factor binding / mitochondrial outer membrane / transcription coactivator activity / endosome / cilium / ciliary basal body / Golgi membrane / innate immune response / Neutrophil degranulation / ubiquitin protein ligase binding / endoplasmic reticulum membrane / protein kinase binding / perinuclear region of cytoplasm / SARS-CoV-2 activates/modulates innate and adaptive immune responses / protein homodimerization activity / positive regulation of transcription by RNA polymerase II / nucleoplasm / identical protein binding / plasma membrane / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.93 Å | |||||||||
 データ登録者 データ登録者 | Gharpure A / Ward AB / Lairson LL | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Microbiota-derived secondary bile acids promote STING activation and antitumor activity 著者: Yang X / Zhang X / Li W / Gharpure A / Hansel A / Tillack A / Wu C / Hsieh Y / Sulpizio A / Dikiy S / Zhao X / Forli S / Ward AB / Parker CG / Hang HC | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_49094.map.gz emd_49094.map.gz | 117.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-49094-v30.xml emd-49094-v30.xml emd-49094.xml emd-49094.xml | 22.7 KB 22.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_49094.png emd_49094.png | 104.1 KB | ||
| Filedesc metadata |  emd-49094.cif.gz emd-49094.cif.gz | 6.5 KB | ||
| その他 |  emd_49094_additional_1.map.gz emd_49094_additional_1.map.gz emd_49094_half_map_1.map.gz emd_49094_half_map_1.map.gz emd_49094_half_map_2.map.gz emd_49094_half_map_2.map.gz | 117.9 MB 115.7 MB 115.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-49094 http://ftp.pdbj.org/pub/emdb/structures/EMD-49094 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-49094 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-49094 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  9n7fMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_49094.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_49094.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HsSTING cGAMP/C53/DCA with C2 symmetry | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.718 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: HsSTING cGAMP/C53/DCA with C1 symmetry
| ファイル | emd_49094_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | HsSTING cGAMP/C53/DCA with C1 symmetry | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_49094_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_49094_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Stimulator of interferon genes
| 全体 | 名称: Stimulator of interferon genes |
|---|---|
| 要素 |
|
-超分子 #1: Stimulator of interferon genes
| 超分子 | 名称: Stimulator of interferon genes / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 400 KDa |
-分子 #1: Stimulator of interferon genes protein
| 分子 | 名称: Stimulator of interferon genes protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 40.246 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MPHSSLHPSI PCPRGHGAQK AALVLLSACL VTLWGLGEPP EHTLRYLVLH LASLQLGLLL NGVCSLAEEL RHIHSRYRGS YWRTVRACL GCPLRRGALL LLSIYFYYSL PNAVGPPFTW MLALLGLSQA LNILLGLKGL APAEISAVCE KGNFNVAHGL A WSYYIGYL ...文字列: MPHSSLHPSI PCPRGHGAQK AALVLLSACL VTLWGLGEPP EHTLRYLVLH LASLQLGLLL NGVCSLAEEL RHIHSRYRGS YWRTVRACL GCPLRRGALL LLSIYFYYSL PNAVGPPFTW MLALLGLSQA LNILLGLKGL APAEISAVCE KGNFNVAHGL A WSYYIGYL RLILPELQAR IRTYNQHYNN LLRGAVSQRL YILLPLDCGV PDNLSMADPN IRFLDKLPQQ TGDHAGIKDR VY SNSIYEL LENGQRAGTC VLEYATPLQT LFAMSQYSQA GFSREDRLEQ AKLFCRTLED ILADAPESQN NCRLIAYQEP ADD SSFSLS QEVLRHLRQE EKEEVTVGGG SGGGSGGSAW SHPQFEK UniProtKB: Stimulator of interferon genes protein |
-分子 #2: 1-[(2-chloro-6-fluorophenyl)methyl]-3,3-dimethyl-2-oxo-N-[(2,4,6-...
| 分子 | 名称: 1-[(2-chloro-6-fluorophenyl)methyl]-3,3-dimethyl-2-oxo-N-[(2,4,6-trifluorophenyl)methyl]-2,3-dihydro-1H-indole-6-carboxamide タイプ: ligand / ID: 2 / コピー数: 2 / 式: 9IM |
|---|---|
| 分子量 | 理論値: 490.877 Da |
| Chemical component information | 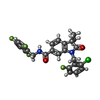 ChemComp-9IM: |
-分子 #3: cGAMP
| 分子 | 名称: cGAMP / タイプ: ligand / ID: 3 / コピー数: 2 / 式: 1SY |
|---|---|
| 分子量 | 理論値: 674.411 Da |
| Chemical component information | 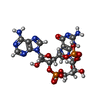 ChemComp-1SY: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 8 mg/mL | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| |||||||||||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS GLACIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: TFS FALCON 4i (4k x 4k) 実像数: 5839 / 平均露光時間: 3.2 sec. / 平均電子線量: 45.12 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 20.0 µm / 照射モード: SPOT SCAN / 撮影モード: OTHER / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.5 µm / 最小 デフォーカス(公称値): 0.6 µm / 倍率(公称値): 190000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)













































