登録情報 データベース : EMDB / ID : EMD-4882タイトル Cryo-EM structure of E. coli RNA polymerase elongation complex bound to CTP substrate 複合体 : Cryo-EM structure of E. coli RNA polymerase elongation complex bound to CTP substrate複合体 : RNA polymeraseタンパク質・ペプチド : DNA-directed RNA polymerase subunit alphaタンパク質・ペプチド : DNA-directed RNA polymerase subunit betaタンパク質・ペプチド : DNA-directed RNA polymerase subunit beta'タンパク質・ペプチド : DNA-directed RNA polymerase subunit omega複合体 : nucleic acidsDNA : Non-template DNADNA : Template DNARNA : RNAリガンド : ZINC IONリガンド : CYTIDINE-5'-TRIPHOSPHATEリガンド : MAGNESIUM ION / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Escherichia coli K-12 (大腸菌)手法 / / 解像度 : 3.6 Å Abdelkareem M / Saint-Andre C 資金援助 Organization Grant number 国 European Research Council 679734
ジャーナル : Mol Cell / 年 : 2019タイトル : Structural Basis of Transcription: RNA Polymerase Backtracking and Its Reactivation.著者 : Mo'men Abdelkareem / Charlotte Saint-André / Maria Takacs / Gabor Papai / Corinne Crucifix / Xieyang Guo / Julio Ortiz / Albert Weixlbaumer / 要旨 : Regulatory sequences or erroneous incorporations during DNA transcription cause RNA polymerase backtracking and inactivation in all kingdoms of life. Reactivation requires RNA transcript cleavage. ... Regulatory sequences or erroneous incorporations during DNA transcription cause RNA polymerase backtracking and inactivation in all kingdoms of life. Reactivation requires RNA transcript cleavage. Essential transcription factors (GreA and GreB, or TFIIS) accelerate this reaction. We report four cryo-EM reconstructions of Escherichia coli RNA polymerase representing the entire reaction pathway: (1) a backtracked complex; a backtracked complex with GreB (2) before and (3) after RNA cleavage; and (4) a reactivated, substrate-bound complex with GreB before RNA extension. Compared with eukaryotes, the backtracked RNA adopts a different conformation. RNA polymerase conformational changes cause distinct GreB states: a fully engaged GreB before cleavage; a disengaged GreB after cleavage; and a dislodged, loosely bound GreB removed from the active site to allow RNA extension. These reconstructions provide insight into the catalytic mechanism and dynamics of RNA cleavage and extension and suggest how GreB targets backtracked complexes without interfering with canonical transcription. 履歴 登録 2019年4月18日 - ヘッダ(付随情報) 公開 2019年5月22日 - マップ公開 2019年7月3日 - 更新 2024年5月22日 - 現状 2024年5月22日 処理サイト : PDBe / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
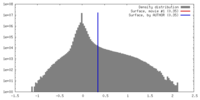
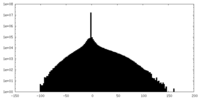
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 データ登録者
データ登録者 フランス, 1件
フランス, 1件  引用
引用 ジャーナル: Mol Cell / 年: 2019
ジャーナル: Mol Cell / 年: 2019
 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_4882.map.gz
emd_4882.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-4882-v30.xml
emd-4882-v30.xml emd-4882.xml
emd-4882.xml EMDBヘッダ
EMDBヘッダ emd_4882.png
emd_4882.png emd-4882.cif.gz
emd-4882.cif.gz emd_4882_additional.map.gz
emd_4882_additional.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-4882
http://ftp.pdbj.org/pub/emdb/structures/EMD-4882 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4882
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4882 emd_4882_validation.pdf.gz
emd_4882_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_4882_full_validation.pdf.gz
emd_4882_full_validation.pdf.gz emd_4882_validation.xml.gz
emd_4882_validation.xml.gz emd_4882_validation.cif.gz
emd_4882_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4882
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4882 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4882
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4882 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_4882.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_4882.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 画像解析
画像解析 ムービー
ムービー コントローラー
コントローラー























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)