+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SARS-CoV-2 Frameshift Stimulatory Element with Upstream Multibranch Loop | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNA / Coronavirus / SARS-CoV-2 / Programmed -1 Ribosomal Frameshifting / -1 PRF / Frameshift Stimulatory Element / FSE / Attenuator Hairpin | |||||||||
| 生物種 |   Severe acute respiratory syndrome coronavirus (SARS コロナウイルス) Severe acute respiratory syndrome coronavirus (SARS コロナウイルス) | |||||||||
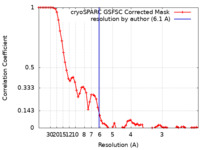
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.1 Å | |||||||||
 データ登録者 データ登録者 | Peterson JM / Becker ST / O'Leary CA / Juneja P / Yang Y / Moss WN | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2024 ジャーナル: Biochemistry / 年: 2024タイトル: Structure of the SARS-CoV-2 Frameshift Stimulatory Element with an Upstream Multibranch Loop. 著者: Jake M Peterson / Scott T Becker / Collin A O'Leary / Puneet Juneja / Yang Yang / Walter N Moss /  要旨: The severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) frameshift stimulatory element (FSE) is necessary for programmed -1 ribosomal frameshifting (-1 PRF) and optimized viral efficacy. The ...The severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) frameshift stimulatory element (FSE) is necessary for programmed -1 ribosomal frameshifting (-1 PRF) and optimized viral efficacy. The FSE has an abundance of context-dependent alternate conformations, but two of the structures most crucial to -1 PRF are an attenuator hairpin and a three-stem H-type pseudoknot structure. A crystal structure of the pseudoknot alone features three RNA stems in a helically stacked linear structure, whereas a 6.9 Å cryo-EM structure including the upstream heptameric slippery site resulted in a bend between two stems. Our previous research alluded to an extended upstream multibranch loop that includes both the attenuator hairpin and the slippery site-a conformation not previously modeled. We aim to provide further context to the SARS-CoV-2 FSE via computational and medium resolution cryo-EM approaches, by presenting a 6.1 Å cryo-EM structure featuring a linear pseudoknot structure and a dynamic upstream multibranch loop. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_43137.map.gz emd_43137.map.gz | 15.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-43137-v30.xml emd-43137-v30.xml emd-43137.xml emd-43137.xml | 17.9 KB 17.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_43137_fsc.xml emd_43137_fsc.xml | 6.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_43137.png emd_43137.png | 132.1 KB | ||
| マスクデータ |  emd_43137_msk_1.map emd_43137_msk_1.map | 30.5 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-43137.cif.gz emd-43137.cif.gz | 5 KB | ||
| その他 |  emd_43137_additional_1.map.gz emd_43137_additional_1.map.gz emd_43137_half_map_1.map.gz emd_43137_half_map_1.map.gz emd_43137_half_map_2.map.gz emd_43137_half_map_2.map.gz | 28.6 MB 28.3 MB 28.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-43137 http://ftp.pdbj.org/pub/emdb/structures/EMD-43137 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43137 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43137 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_43137_validation.pdf.gz emd_43137_validation.pdf.gz | 892.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_43137_full_validation.pdf.gz emd_43137_full_validation.pdf.gz | 891.7 KB | 表示 | |
| XML形式データ |  emd_43137_validation.xml.gz emd_43137_validation.xml.gz | 14.1 KB | 表示 | |
| CIF形式データ |  emd_43137_validation.cif.gz emd_43137_validation.cif.gz | 18 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43137 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43137 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43137 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43137 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_43137.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_43137.map.gz / 形式: CCP4 / 大きさ: 30.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.133 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_43137_msk_1.map emd_43137_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_43137_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_43137_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_43137_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Severe acute respiratory syndrome coronavirus
| 全体 | 名称:  Severe acute respiratory syndrome coronavirus (SARS コロナウイルス) Severe acute respiratory syndrome coronavirus (SARS コロナウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Severe acute respiratory syndrome coronavirus
| 超分子 | 名称: Severe acute respiratory syndrome coronavirus / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: PCR amplified and transcribed using T7 polymerase. / NCBI-ID: 2901879 / 生物種: Severe acute respiratory syndrome coronavirus / Sci species strain: Wuhan-Hu-1 / ウイルスタイプ: VIRION / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: Yes |
|---|---|
| 宿主 | 生物種:  Homo sapiens (ヒト) / 株: Wuhan-Hu-1 Homo sapiens (ヒト) / 株: Wuhan-Hu-1 |
-分子 #1: Frameshift Stimulatory Element with Upstream Multi-branch Loop
| 分子 | 名称: Frameshift Stimulatory Element with Upstream Multi-branch Loop タイプ: rna / ID: 1 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 37.90141 KDa |
| 配列 | 文字列: GGGAACCCAU GCUUCAGUCA GCUGAUGCAC AAUCGUUUUU AAACGGGUUU CCGGUGUAAG UGCAGCCCGU CUUACACCGU GCGGCACAG GCACUAGUAC UGAUGUCGUA UACAGGGCU GENBANK: GENBANK: NC_045512.2 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 40 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 4 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS GLACIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 3 / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 36000 |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-8vci: |
 ムービー
ムービー コントローラー
コントローラー




 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)