+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM Structure of Diffocin - postcontracted - Baseplate - final state | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Phage tail-like / bacteriocin / baseplate / post-contraction / VIRUS LIKE PARTICLE | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Bacteriophage Mu-like, Gp48 / Protein of unknown function DUF2634 / Bacteriophage Mu-like, Gp48 / Protein of unknown function (DUF2634) / : / Baseplate protein J-like / Baseplate J-like protein / Tail sheath protein, subtilisin-like domain / Phage tail sheath protein subtilisin-like domain / Tail sheath protein, C-terminal domain / Phage tail sheath C-terminal domain 類似検索 - ドメイン・相同性 | ||||||||||||
| 生物種 |  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.1 Å | ||||||||||||
 データ登録者 データ登録者 | Cai XY / He Y / Zhou ZH | ||||||||||||
| 資金援助 |  米国, 3件 米国, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Atomic structures of a bacteriocin targeting Gram-positive bacteria. 著者: Xiaoying Cai / Yao He / Iris Yu / Anthony Imani / Dean Scholl / Jeff F Miller / Z Hong Zhou /  要旨: Due to envelope differences between Gram-positive and Gram-negative bacteria, engineering precision bactericidal contractile nanomachines requires atomic-level understanding of their structures; ...Due to envelope differences between Gram-positive and Gram-negative bacteria, engineering precision bactericidal contractile nanomachines requires atomic-level understanding of their structures; however, only those killing Gram-negative bacteria are currently known. Here, we report the atomic structures of an engineered diffocin, a contractile syringe-like molecular machine that kills the Gram-positive bacterium Clostridioides difficile. Captured in one pre-contraction and two post-contraction states, each structure fashions six proteins in the bacteria-targeting baseplate, two proteins in the energy-storing trunk, and a collar linking the sheath with the membrane-penetrating tube. Compared to contractile machines targeting Gram-negative bacteria, major differences reside in the baseplate and contraction magnitude, consistent with target envelope differences. The multifunctional hub-hydrolase protein connects the tube and baseplate and is positioned to degrade peptidoglycan during penetration. The full-length tape measure protein forms a coiled-coil helix bundle homotrimer spanning the entire diffocin. Our study offers mechanical insights and principles for designing potent protein-based precision antibiotics. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_42964.map.gz emd_42964.map.gz | 95.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-42964-v30.xml emd-42964-v30.xml emd-42964.xml emd-42964.xml | 17.6 KB 17.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_42964.png emd_42964.png | 65.2 KB | ||
| マスクデータ |  emd_42964_msk_1.map emd_42964_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-42964.cif.gz emd-42964.cif.gz | 6.1 KB | ||
| その他 |  emd_42964_half_map_1.map.gz emd_42964_half_map_1.map.gz emd_42964_half_map_2.map.gz emd_42964_half_map_2.map.gz | 79.3 MB 79.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-42964 http://ftp.pdbj.org/pub/emdb/structures/EMD-42964 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42964 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-42964 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_42964_validation.pdf.gz emd_42964_validation.pdf.gz | 1.2 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_42964_full_validation.pdf.gz emd_42964_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  emd_42964_validation.xml.gz emd_42964_validation.xml.gz | 12.7 KB | 表示 | |
| CIF形式データ |  emd_42964_validation.cif.gz emd_42964_validation.cif.gz | 14.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42964 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42964 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42964 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-42964 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8v43MC  8v3tC  8v3wC  8v3xC  8v3yC  8v3zC  8v40C  8v41C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_42964.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_42964.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
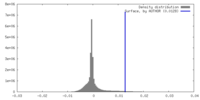
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_42964_msk_1.map emd_42964_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
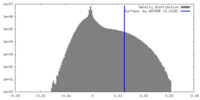
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_42964_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_42964_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
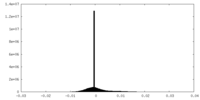
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Diffocin
| 全体 | 名称: Diffocin |
|---|---|
| 要素 |
|
-超分子 #1: Diffocin
| 超分子 | 名称: Diffocin / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) |
-分子 #1: TRI-2 (CD1371)
| 分子 | 名称: TRI-2 (CD1371) / タイプ: protein_or_peptide / ID: 1 / コピー数: 12 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) |
| 分子量 | 理論値: 39.603281 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MYSDQTYEVI KNRTLENINL DIYKGEGSFL NNMVSGNNLE LSKIYLELSK MHKMAFIQDT YNQFLDKRVN EFGVYRKLGT ESNGEVEFI GEKGTVINNG TIISYRDLLF VVIKDVTIGS EEGDNSPVQA LEVGKKYNLP TNCEFKLVDN ISGVTKITNT R SFEGGTDI ...文字列: MYSDQTYEVI KNRTLENINL DIYKGEGSFL NNMVSGNNLE LSKIYLELSK MHKMAFIQDT YNQFLDKRVN EFGVYRKLGT ESNGEVEFI GEKGTVINNG TIISYRDLLF VVIKDVTIGS EEGDNSPVQA LEVGKKYNLP TNCEFKLVDN ISGVTKITNT R SFEGGTDI ETDEELKERF YKIQRNQATS GNKAHYEEWA LEVDGVYNVK VYPRWDGPGT VKVLIFGKNN QAVDTETIER CQ QHIDEEK PIGPTITVVT PLPIEISISA VMKLEDGYTL DNVKESFLES INTYFRDIRG EIIYTKVMGI LINTTGVHDL SNL LINGST DNITINEDKI PSVTTVNFSE VENQ UniProtKB: Base plate protein |
-分子 #2: TRI-1 (CD1372)
| 分子 | 名称: TRI-1 (CD1372) / タイプ: protein_or_peptide / ID: 2 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) |
| 分子量 | 理論値: 26.473488 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MKLIDKLPSF DRNYIVEEIQ GAYDTELNIL KEDIDDTFNQ LFVDTATWGL DMWEDILCIE KKELDFDTRR SNIKAKMRSR GTSTIEVIK SICEAYTKSE TDIKVYSDEF TFVLSFIANN CDYKTLLDCS DMIERVKPAH LLHYLEPIIL DKSMVYCGGG M VCSEEVKV ...文字列: MKLIDKLPSF DRNYIVEEIQ GAYDTELNIL KEDIDDTFNQ LFVDTATWGL DMWEDILCIE KKELDFDTRR SNIKAKMRSR GTSTIEVIK SICEAYTKSE TDIKVYSDEF TFVLSFIANN CDYKTLLDCS DMIERVKPAH LLHYLEPIIL DKSMVYCGGG M VCSEEVKV HPYFEPIIKC SAVVNCGAGM ISREEIKVYP LSIKCIENNC KINIAIANDT GVENVVVYPK SEVV UniProtKB: Base plate protein |
-分子 #3: Sheath initiator (CD1370)
| 分子 | 名称: Sheath initiator (CD1370) / タイプ: protein_or_peptide / ID: 3 / コピー数: 6 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) |
| 分子量 | 理論値: 16.549959 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSTIFPFIGV PEDYILPKTE ELPIFREVAW DFEKDEPILE KGDFKIIEKK EALKVWIYKC IKTNRYEHEI YSLEYGTELS ELIGQKYTK GLTESEASRF IKEALLINPY ILEVNVKSAN FNRDILSANV KVSTIYGEVE INV UniProtKB: DUF2634 domain-containing protein |
-分子 #4: Sheath (CD1363)
| 分子 | 名称: Sheath (CD1363) / タイプ: protein_or_peptide / ID: 4 / コピー数: 18 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Clostridioides difficile (バクテリア) Clostridioides difficile (バクテリア) |
| 分子量 | 理論値: 39.26843 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAIGLPSINI SFKELATTVK ERSARGIIAM VLKDAKALGL NEIHEKEDIP VDLSAENKEY INLALMGNVN TPNKLLVYVI EGEADIQTA LDFLETKEFN YLCMPKAVEA DKTAIKNWII KLRDIDKVKV KAVLGKVVGN HEGIINFTTE DVLVGEKKYS V DEFTSRVA ...文字列: MAIGLPSINI SFKELATTVK ERSARGIIAM VLKDAKALGL NEIHEKEDIP VDLSAENKEY INLALMGNVN TPNKLLVYVI EGEADIQTA LDFLETKEFN YLCMPKAVEA DKTAIKNWII KLRDIDKVKV KAVLGKVVGN HEGIINFTTE DVLVGEKKYS V DEFTSRVA GLIAGTPLSQ SVTYTKLSDV VDIPKMTKVD AESRVNKGEL ILIKEAGAIR IARGVNSLTE LTAEKGEMFQ KI KIVDTLD IIHSDIRKVI IDDYIGKVTN SYDNKCLLIV AIKSYLEELE KSALIESDST VEIDFEAQKS YLKSKGVDLS YMT LQEIKE ANTGSKVFLK AKIKVLDAME DIDLSIEI UniProtKB: Phage tail sheath protein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 6.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 11219 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)