+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Human sodium-dependent vitamin C transporter 1 in an apo occluded state | |||||||||
 マップデータ マップデータ | FSC-weighted, sharpened and masked map by PostProcess | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Transporter / Membrane protein / Ascorbic acid / Vitamin C / Sodium / TRANSPORT PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報nucleobase transport / L-ascorbate:sodium symporter activity / L-ascorbic acid transmembrane transporter activity / L-ascorbic acid transmembrane transport / nucleobase transmembrane transporter activity / dehydroascorbic acid transmembrane transporter activity / dehydroascorbic acid transport / sodium ion transmembrane transporter activity / Vitamin C (ascorbate) metabolism / L-ascorbic acid metabolic process ...nucleobase transport / L-ascorbate:sodium symporter activity / L-ascorbic acid transmembrane transporter activity / L-ascorbic acid transmembrane transport / nucleobase transmembrane transporter activity / dehydroascorbic acid transmembrane transporter activity / dehydroascorbic acid transport / sodium ion transmembrane transporter activity / Vitamin C (ascorbate) metabolism / L-ascorbic acid metabolic process / urate transmembrane transporter activity / intracellular organelle / sodium ion transport / basal plasma membrane / lung development / brain development / response to toxic substance / apical plasma membrane / extracellular exosome / plasma membrane / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.85 Å | |||||||||
 データ登録者 データ登録者 | Kobayashi TA / Kusakizako T / Nureki O | |||||||||
| 資金援助 |  日本, 1件 日本, 1件
| |||||||||
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Publishedタイトル: Cryo-EM structures of human sodium-dependent vitamin C transporter 1 著者: Kobayashi TA / Kusakizako T / Nureki O | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_36206.map.gz emd_36206.map.gz | 2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-36206-v30.xml emd-36206-v30.xml emd-36206.xml emd-36206.xml | 17.3 KB 17.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_36206_fsc.xml emd_36206_fsc.xml | 10.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_36206.png emd_36206.png | 98.8 KB | ||
| マスクデータ |  emd_36206_msk_1.map emd_36206_msk_1.map | 6.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-36206.cif.gz emd-36206.cif.gz | 6.6 KB | ||
| その他 |  emd_36206_half_map_1.map.gz emd_36206_half_map_1.map.gz emd_36206_half_map_2.map.gz emd_36206_half_map_2.map.gz | 5.5 MB 5.5 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-36206 http://ftp.pdbj.org/pub/emdb/structures/EMD-36206 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36206 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-36206 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_36206_validation.pdf.gz emd_36206_validation.pdf.gz | 874 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_36206_full_validation.pdf.gz emd_36206_full_validation.pdf.gz | 873.5 KB | 表示 | |
| XML形式データ |  emd_36206_validation.xml.gz emd_36206_validation.xml.gz | 13.1 KB | 表示 | |
| CIF形式データ |  emd_36206_validation.cif.gz emd_36206_validation.cif.gz | 17.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36206 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36206 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36206 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-36206 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_36206.map.gz / 形式: CCP4 / 大きさ: 6.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_36206.map.gz / 形式: CCP4 / 大きさ: 6.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | FSC-weighted, sharpened and masked map by PostProcess | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.996 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_36206_msk_1.map emd_36206_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
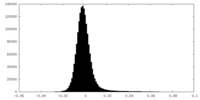
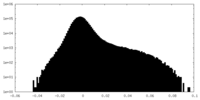
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_36206_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
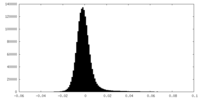
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_36206_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
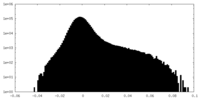
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human SVCT1 dimer in an apo occluded state
| 全体 | 名称: Human SVCT1 dimer in an apo occluded state |
|---|---|
| 要素 |
|
-超分子 #1: Human SVCT1 dimer in an apo occluded state
| 超分子 | 名称: Human SVCT1 dimer in an apo occluded state / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Solute carrier family 23 member 1
| 分子 | 名称: Solute carrier family 23 member 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 64.860707 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MRAQEDLEGR TQHETTRDPS TPLPTEPKFD MLYKIEDVPP WYLCILLGFQ HYLTCFSGTI AVPFLLAEAL CVGHDQHMVS QLIGTIFTC VGITTLIQTT VGIRLPLFQA SAFAFLVPAK AILALERWKC PPEEEIYGNW SLPLNTSHIW HPRIREVQGA I MVSSVVEV ...文字列: MRAQEDLEGR TQHETTRDPS TPLPTEPKFD MLYKIEDVPP WYLCILLGFQ HYLTCFSGTI AVPFLLAEAL CVGHDQHMVS QLIGTIFTC VGITTLIQTT VGIRLPLFQA SAFAFLVPAK AILALERWKC PPEEEIYGNW SLPLNTSHIW HPRIREVQGA I MVSSVVEV VIGLLGLPGA LLNYIGPLTV TPTVSLIGLS VFQAAGDRAG SHWGISACSI LLIILFSQYL RNLTFLLPVY RW GKGLTLL RIQIFKMFPI MLAIMTVWLL CYVLTLTDVL PTDPKAYGFQ ARTDARGDIM AIAPWIRIPY PCQWGLPTVT AAA VLGMFS ATLAGIIESI GDYYACARLA GAPPPPVHAI NRGIFTEGIC CIIAGLLGTG NGSTSSSPNI GVLGITKVGS RRVV QYGAA IMLVLGTIGK FTALFASLPD PILGGMFCTL FGMITAVGLS NLQFVDMNSS RNLFVLGFSM FFGLTLPNYL ESNPG AINT GILEVDQILI VLLTTEMFVG GCLAFILDNT VPGSPEERGL IQWKAGAHAN SDMSSSLKSY DFPIGMGIVK RITFLK YIP ICPVFKGFSS SSKDQIAIPE DTPENTETAS VCTKV UniProtKB: Solute carrier family 23 member 1 |
-分子 #2: Lauryl Maltose Neopentyl Glycol
| 分子 | 名称: Lauryl Maltose Neopentyl Glycol / タイプ: ligand / ID: 2 / コピー数: 3 / 式: AV0 |
|---|---|
| 分子量 | 理論値: 1.005188 KDa |
| Chemical component information |  ChemComp-AV0: |
-分子 #3: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 3 / コピー数: 2 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-分子 #4: CHOLESTEROL
| 分子 | 名称: CHOLESTEROL / タイプ: ligand / ID: 4 / コピー数: 1 / 式: CLR |
|---|---|
| 分子量 | 理論値: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-分子 #5: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 5 / コピー数: 1 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-分子 #6: PALMITIC ACID
| 分子 | 名称: PALMITIC ACID / タイプ: ligand / ID: 6 / コピー数: 1 / 式: PLM |
|---|---|
| 分子量 | 理論値: 256.424 Da |
| Chemical component information |  ChemComp-PLM: |
-分子 #7: water
| 分子 | 名称: water / タイプ: ligand / ID: 7 / コピー数: 2 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7 |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 25 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 5907 / 平均電子線量: 50.9 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.6 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 105000 |
| 試料ステージ | ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー











 Z
Z Y
Y X
X