+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
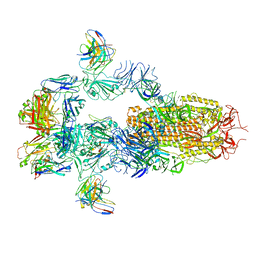
| タイトル | Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 and BA7125 fab (local refinement) | |||||||||
 マップデータ マップデータ | Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 and BA7125 fab (local refinement) | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | VIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報symbiont-mediated disruption of host tissue / Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / viral translation / host extracellular space / symbiont-mediated-mediated suppression of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion ...symbiont-mediated disruption of host tissue / Maturation of spike protein / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / viral translation / host extracellular space / symbiont-mediated-mediated suppression of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / entry receptor-mediated virion attachment to host cell / membrane fusion / Attachment and Entry / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / host cell surface receptor binding / symbiont-mediated suppression of host innate immune response / receptor ligand activity / endocytosis involved in viral entry into host cell / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / symbiont entry into host cell / virion attachment to host cell / SARS-CoV-2 activates/modulates innate and adaptive immune responses / host cell plasma membrane / virion membrane / identical protein binding / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.98 Å | |||||||||
 データ登録者 データ登録者 | Liu Z / Liu S | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Discov / 年: 2023 ジャーナル: Cell Discov / 年: 2023タイトル: Biparatopic antibody BA7208/7125 effectively neutralizes SARS-CoV-2 variants including Omicron BA.1-BA.5. 著者: Wang Y / Yan A / Song D / Dong C / Rao M / Gao Y / Qi R / Ma X / Wang Q / Xu H / Liu H / Han J / Duan M / Liu S / Yu X / Zong M / Feng J / Jiao J / Zhang H / Li M / Yu B / Wang Y / Meng F / ...著者: Wang Y / Yan A / Song D / Dong C / Rao M / Gao Y / Qi R / Ma X / Wang Q / Xu H / Liu H / Han J / Duan M / Liu S / Yu X / Zong M / Feng J / Jiao J / Zhang H / Li M / Yu B / Wang Y / Meng F / Ni X / Li Y / Shen Z / Sun B / Shao X / Zhao H / Zhao Y / Li R / Zhang Y / Du G / Lu J / You C / Jiang H / Zhang L / Wang L / Dou C / Liu Z / Zhao J | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_33140.map.gz emd_33140.map.gz | 482.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-33140-v30.xml emd-33140-v30.xml emd-33140.xml emd-33140.xml | 22.1 KB 22.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_33140.png emd_33140.png | 733 KB | ||
| Filedesc metadata |  emd-33140.cif.gz emd-33140.cif.gz | 6.3 KB | ||
| その他 |  emd_33140_half_map_1.map.gz emd_33140_half_map_1.map.gz emd_33140_half_map_2.map.gz emd_33140_half_map_2.map.gz | 474.6 MB 474.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-33140 http://ftp.pdbj.org/pub/emdb/structures/EMD-33140 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33140 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-33140 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_33140_validation.pdf.gz emd_33140_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_33140_full_validation.pdf.gz emd_33140_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_33140_validation.xml.gz emd_33140_validation.xml.gz | 18.7 KB | 表示 | |
| CIF形式データ |  emd_33140_validation.cif.gz emd_33140_validation.cif.gz | 22.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33140 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33140 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33140 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-33140 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_33140.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_33140.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 and BA7125 fab (local refinement) | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.66 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 ...
| 全体 | 名称: Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 and BA7125 fab (local refinement) |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 ...
| 超分子 | 名称: Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with BA7208 and BA7125 fab (local refinement) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: BA7125 fab
| 分子 | 名称: BA7125 fab / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.514258 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLQQWGAG LLKPSETLSL TCAVYGESFS GYYWSWIRQS PGKGLEWIGQ INHSGNTNYN PSLKSRVTMS VDTSKNQFSL KLSSVTAAD TAVYYCAREL GHDYWGQGTL VTVSSASTKG PSVFPLAPSS KSTSGGTAAL GCLVKDYFPE PVTVSWNSGA L TSGVHTFP ...文字列: EVQLQQWGAG LLKPSETLSL TCAVYGESFS GYYWSWIRQS PGKGLEWIGQ INHSGNTNYN PSLKSRVTMS VDTSKNQFSL KLSSVTAAD TAVYYCAREL GHDYWGQGTL VTVSSASTKG PSVFPLAPSS KSTSGGTAAL GCLVKDYFPE PVTVSWNSGA L TSGVHTFP AVLQSSGLYS LSSVVTVPSS SLGTQTYICN VNHKPSNTKV DKKVEPKSCD KT |
-分子 #2: BA7125 fab
| 分子 | 名称: BA7125 fab / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.328883 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EIVMTQSPGT LSLSPGERAT LSCRASQSIS SSYLAWFQQK PGQAPRLLIY GASSRAPGIP DRFSGSGSGT DFTLTISRLE PEDFAVYYC QQYGDSPLTF GGGTKVDIKR TVAAPSVFIF PPSDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD ...文字列: EIVMTQSPGT LSLSPGERAT LSCRASQSIS SSYLAWFQQK PGQAPRLLIY GASSRAPGIP DRFSGSGSGT DFTLTISRLE PEDFAVYYC QQYGDSPLTF GGGTKVDIKR TVAAPSVFIF PPSDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD SKDSTYSLSS TLTLSKADYE KHKVYACEVT HQGLSSPVTK SFNRGEC |
-分子 #3: Spike glycoprotein
| 分子 | 名称: Spike glycoprotein / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 21.973684 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: NLCPFGEVFN ATRFASVYAW NRKRISNCVA DYSVLYNSAS FSTFKCYGVS PTKLNDLCFT NVYADSFVIR GDEVRQIAPG QTGKIADYN YKLPDDFTGC VIAWNSNNLD SKVGGNYNYR YRLFRKSNLK PFERDISTEI YQAGSKPCNG VEGFNCYFPL Q SYGFQPTN ...文字列: NLCPFGEVFN ATRFASVYAW NRKRISNCVA DYSVLYNSAS FSTFKCYGVS PTKLNDLCFT NVYADSFVIR GDEVRQIAPG QTGKIADYN YKLPDDFTGC VIAWNSNNLD SKVGGNYNYR YRLFRKSNLK PFERDISTEI YQAGSKPCNG VEGFNCYFPL Q SYGFQPTN GVGYQPYRVV VLSFELLHAP ATVCGPK UniProtKB: Spike glycoprotein |
-分子 #4: BA7208 fab
| 分子 | 名称: BA7208 fab / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.398379 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVQSGAE VKKPGESLKI SCKGSGYSFT SYYWIGWVRQ MPGKGLEWMG IVYPDDSDTR YSPSFQGQVT ISADKSISTA YLQWSSLKA SDTAMYYCVR HPGGGDWYFD LWGRGTLVTV SSASTKGPSV FPLAPSSKST SGGTAALGCL VKDYFPEPVT V SWNSGALT ...文字列: EVQLVQSGAE VKKPGESLKI SCKGSGYSFT SYYWIGWVRQ MPGKGLEWMG IVYPDDSDTR YSPSFQGQVT ISADKSISTA YLQWSSLKA SDTAMYYCVR HPGGGDWYFD LWGRGTLVTV SSASTKGPSV FPLAPSSKST SGGTAALGCL VKDYFPEPVT V SWNSGALT SGVHTFPAVL QSSGLYSLSS VVTVPSSSLG TQTYICNVNH KPSNTKVDKK VEPKSCDKT |
-分子 #5: BA7208 fab
| 分子 | 名称: BA7208 fab / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.518082 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DIQMTQSPST LSASVGDRVT ITCRASQSIS SWLAWYQQKP GKAPKLLIYK ASSLESGVPS RFSGSGSGTE FTLTITSLQP DDFATYYCQ QYDSFSWTFG QGTKLEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS ...文字列: DIQMTQSPST LSASVGDRVT ITCRASQSIS SWLAWYQQKP GKAPKLLIYK ASSLESGVPS RFSGSGSGTE FTLTITSLQP DDFATYYCQ QYDSFSWTFG QGTKLEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS KDSTYSLSST LTLSKADYEK HKVYACEVTH QGLSSPVTKS FNRGEC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 1.39 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 5.0 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー