+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | N2 neuraminidase of A/Hong_Kong/2671/2019 in complex with 3 FNI9 Fab molecules | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | viral glycoprotein / antibody / Fab / influenza / VIRAL PROTEIN-IMMUNE SYSTEM complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報: / : / : / exo-alpha-sialidase / viral budding from plasma membrane / carbohydrate metabolic process / host cell plasma membrane / virion membrane / membrane / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |   Influenza A virus (A型インフルエンザウイルス) / Influenza A virus (A型インフルエンザウイルス) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Dang HV / Snell G | |||||||||
| 資金援助 | 1件
| |||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2023 ジャーナル: Nature / 年: 2023タイトル: A pan-influenza antibody inhibiting neuraminidase via receptor mimicry. 著者: Corey Momont / Ha V Dang / Fabrizia Zatta / Kevin Hauser / Caihong Wang / Julia di Iulio / Andrea Minola / Nadine Czudnochowski / Anna De Marco / Kaitlin Branch / David Donermeyer / Siddhant ...著者: Corey Momont / Ha V Dang / Fabrizia Zatta / Kevin Hauser / Caihong Wang / Julia di Iulio / Andrea Minola / Nadine Czudnochowski / Anna De Marco / Kaitlin Branch / David Donermeyer / Siddhant Vyas / Alex Chen / Elena Ferri / Barbara Guarino / Abigail E Powell / Roberto Spreafico / Samantha S Yim / Dale R Balce / Istvan Bartha / Marcel Meury / Tristan I Croll / David M Belnap / Michael A Schmid / William Timothy Schaiff / Jessica L Miller / Elisabetta Cameroni / Amalio Telenti / Herbert W Virgin / Laura E Rosen / Lisa A Purcell / Antonio Lanzavecchia / Gyorgy Snell / Davide Corti / Matteo Samuele Pizzuto /    要旨: Rapidly evolving influenza A viruses (IAVs) and influenza B viruses (IBVs) are major causes of recurrent lower respiratory tract infections. Current influenza vaccines elicit antibodies ...Rapidly evolving influenza A viruses (IAVs) and influenza B viruses (IBVs) are major causes of recurrent lower respiratory tract infections. Current influenza vaccines elicit antibodies predominantly to the highly variable head region of haemagglutinin and their effectiveness is limited by viral drift and suboptimal immune responses. Here we describe a neuraminidase-targeting monoclonal antibody, FNI9, that potently inhibits the enzymatic activity of all group 1 and group 2 IAVs, as well as Victoria/2/87-like, Yamagata/16/88-like and ancestral IBVs. FNI9 broadly neutralizes seasonal IAVs and IBVs, including the immune-evading H3N2 strains bearing an N-glycan at position 245, and shows synergistic activity when combined with anti-haemagglutinin stem-directed antibodies. Structural analysis reveals that D107 in the FNI9 heavy chain complementarity-determinant region 3 mimics the interaction of the sialic acid carboxyl group with the three highly conserved arginine residues (R118, R292 and R371) of the neuraminidase catalytic site. FNI9 demonstrates potent prophylactic activity against lethal IAV and IBV infections in mice. The unprecedented breadth and potency of the FNI9 monoclonal antibody supports its development for the prevention of influenza illness by seasonal and pandemic viruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29706.map.gz emd_29706.map.gz | 163 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29706-v30.xml emd-29706-v30.xml emd-29706.xml emd-29706.xml | 21.6 KB 21.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_29706.png emd_29706.png | 45.2 KB | ||
| マスクデータ |  emd_29706_msk_1.map emd_29706_msk_1.map | 325 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-29706.cif.gz emd-29706.cif.gz | 6.9 KB | ||
| その他 |  emd_29706_additional_1.map.gz emd_29706_additional_1.map.gz emd_29706_half_map_1.map.gz emd_29706_half_map_1.map.gz emd_29706_half_map_2.map.gz emd_29706_half_map_2.map.gz | 306.9 MB 301.9 MB 301.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29706 http://ftp.pdbj.org/pub/emdb/structures/EMD-29706 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29706 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29706 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29706_validation.pdf.gz emd_29706_validation.pdf.gz | 1.1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29706_full_validation.pdf.gz emd_29706_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  emd_29706_validation.xml.gz emd_29706_validation.xml.gz | 17.2 KB | 表示 | |
| CIF形式データ |  emd_29706_validation.cif.gz emd_29706_validation.cif.gz | 20.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29706 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29706 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29706 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29706 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8g3oMC  8g30C  8g3mC  8g3nC  8g3pC  8g3qC  8g3rC  8g3vC  8g3zC  8g40C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29706.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29706.map.gz / 形式: CCP4 / 大きさ: 325 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.83 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_29706_msk_1.map emd_29706_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
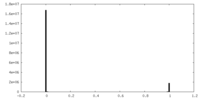
| 密度ヒストグラム |
-追加マップ: #1
| ファイル | emd_29706_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
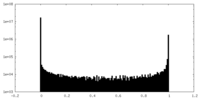
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_29706_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
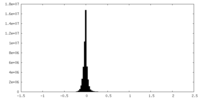
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_29706_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
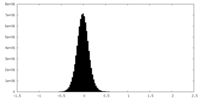
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : 3 FNI9 Fabs in complex with tetrameric N2 NA protein from A/Hong_...
| 全体 | 名称: 3 FNI9 Fabs in complex with tetrameric N2 NA protein from A/Hong_Kong/2671/2019 strain |
|---|---|
| 要素 |
|
-超分子 #1: 3 FNI9 Fabs in complex with tetrameric N2 NA protein from A/Hong_...
| 超分子 | 名称: 3 FNI9 Fabs in complex with tetrameric N2 NA protein from A/Hong_Kong/2671/2019 strain タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 詳細: Fab fragment generated by proteolytic cleavage of FNI9 IgG1 antibody |
|---|---|
| 由来(天然) | 生物種:   Influenza A virus (A型インフルエンザウイルス) Influenza A virus (A型インフルエンザウイルス) |
| 分子量 | 理論値: 420 KDa |
-分子 #1: FNI9 Fab heavy chain
| 分子 | 名称: FNI9 Fab heavy chain / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.418053 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: QVHLVQSGAE VKEPGSSVTV SCKASGGSFN NQAISWVRQA PGQGLEWMGG IFPISGTPTS AQRFQGRVTF TADESTTTVY MDLSSLRSD DTAVYYCARA GSDYFNRDLG WENYYFASWG QGTLVTVSSA STKGPSVFPL APSSKSTSGG TAALGCLVKD Y FPEPVTVS ...文字列: QVHLVQSGAE VKEPGSSVTV SCKASGGSFN NQAISWVRQA PGQGLEWMGG IFPISGTPTS AQRFQGRVTF TADESTTTVY MDLSSLRSD DTAVYYCARA GSDYFNRDLG WENYYFASWG QGTLVTVSSA STKGPSVFPL APSSKSTSGG TAALGCLVKD Y FPEPVTVS WNSGALTSGV HTFPAVLQSS GLYSLSSVVT VPSSSLGTQT YICNVNHKPS NTKVDKKVEP KSC |
-分子 #2: FNI9 Fab light chain
| 分子 | 名称: FNI9 Fab light chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.565068 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: EIVMTQSPAT LSLSSGERAT LSCRASRSVS SNLAWYQQKP GQAPRLLIYD ASTRATGFSA RFAGSGSGTE FTLTISSLQS EDSAIYYCQ QYNNWPPWTF GQGTKVEIKR TVAAPSVFIF PPSDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD ...文字列: EIVMTQSPAT LSLSSGERAT LSCRASRSVS SNLAWYQQKP GQAPRLLIYD ASTRATGFSA RFAGSGSGTE FTLTISSLQS EDSAIYYCQ QYNNWPPWTF GQGTKVEIKR TVAAPSVFIF PPSDEQLKSG TASVVCLLNN FYPREAKVQW KVDNALQSGN S QESVTEQD SKDSTYSLSS TLTLSKADYE KHKVYACEVT HQGLSSPVTK SFNRGEC |
-分子 #3: Neuraminidase
| 分子 | 名称: Neuraminidase / タイプ: protein_or_peptide / ID: 3 / 詳細: A/Hong_Kong/2671/2019 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Influenza A virus (A型インフルエンザウイルス) Influenza A virus (A型インフルエンザウイルス) |
| 分子量 | 理論値: 54.570906 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: METDTLLLWV LLLWVPGSTG DHHHHHHGSG LNDIFEAQKI EWHEGSIINE TADDIVYRLT VIIDDRYESL KNLITLRADR LEMIINDNV STILASGLVP RGSGSAEYRN WSKPQCGITG FAPFSKDNSI RLSAGGDIWV TREPYVSCDL DKCYQFALGQ G TTLNNVHS ...文字列: METDTLLLWV LLLWVPGSTG DHHHHHHGSG LNDIFEAQKI EWHEGSIINE TADDIVYRLT VIIDDRYESL KNLITLRADR LEMIINDNV STILASGLVP RGSGSAEYRN WSKPQCGITG FAPFSKDNSI RLSAGGDIWV TREPYVSCDL DKCYQFALGQ G TTLNNVHS NNTVRDRTPY RTLLMNELGV PFHLGTKQVC IAWSSSSCHD GKAWLHVCIT GDDKNATASF IYNGRLVDSV VS WSNDILR TQESECVCIN GTCTVVMTDG NATGKADTKI LFIEEGKIVH TSKLSGSAQH VEECSCYPRY PGVRCVCRDN WKG SNRPII DINIKDHSIV SSYVCSGLVG DTPRKSDSSS SSHCLNPNNE EGGHGVKGWA FDDGNDVWMG RTINETSRLG YETF KVVEG WSNPKSKLQI NRQVIVDRGD RSGYSGIFSV EGKSCINRCF YVELIRGRKE ETEVLWTSNS IVVFCGTSGT YGTGS WPDG ADLNLMHT UniProtKB: Neuraminidase |
-分子 #7: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 7 / コピー数: 5 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.2 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
詳細: 50 mM Tris-HCl, 150 mM NaCl, 10 mM CaCl2, pH 8.0 | ||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD | ||||||||||||
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 52.32 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER / 詳細: ab initio |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 3.1 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 58739 |
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)