+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-26162 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Nipah Virus attachment (G) glycoprotein ectodomain in complex with nAH1.3 neutralizing antibody Fab fragment (local refinement of the distal region) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報membrane fusion involved in viral entry into host cell / exo-alpha-sialidase activity / clathrin-dependent endocytosis of virus by host cell / host cell surface receptor binding / viral envelope / virion attachment to host cell / host cell plasma membrane / virion membrane / identical protein binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Nipah henipavirus (ウイルス) / Nipah henipavirus (ウイルス) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Wang ZQ / Seattle Structural Genomics Center for Infectious Disease (SSGCID) / Veesler D | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2022 ジャーナル: Science / 年: 2022タイトル: Architecture and antigenicity of the Nipah virus attachment glycoprotein. 著者: Zhaoqian Wang / Moushimi Amaya / Amin Addetia / Ha V Dang / Gabriella Reggiano / Lianying Yan / Andrew C Hickey / Frank DiMaio / Christopher C Broder / David Veesler /  要旨: Nipah virus (NiV) and Hendra virus (HeV) are zoonotic henipaviruses (HNVs) responsible for outbreaks of encephalitis and respiratory illness. The entry of HNVs into host cells requires the attachment ...Nipah virus (NiV) and Hendra virus (HeV) are zoonotic henipaviruses (HNVs) responsible for outbreaks of encephalitis and respiratory illness. The entry of HNVs into host cells requires the attachment (G) and fusion (F) glycoproteins, which are the main targets of antibody responses. To understand viral infection and host immunity, we determined a cryo-electron microscopy structure of the NiV G homotetrameric ectodomain in complex with the nAH1.3 broadly neutralizing antibody Fab fragment. We show that a cocktail of two nonoverlapping G-specific antibodies neutralizes NiV and HeV synergistically and limits the emergence of escape mutants. Analysis of polyclonal serum antibody responses elicited by vaccination of macaques with NiV G indicates that the receptor binding head domain is immunodominant. These results pave the way for implementing multipronged therapeutic strategies against these deadly pathogens. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26162.map.gz emd_26162.map.gz | 350.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26162-v30.xml emd-26162-v30.xml emd-26162.xml emd-26162.xml | 19.5 KB 19.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_26162.png emd_26162.png | 64.2 KB | ||
| その他 |  emd_26162_additional_1.map.gz emd_26162_additional_1.map.gz emd_26162_half_map_1.map.gz emd_26162_half_map_1.map.gz emd_26162_half_map_2.map.gz emd_26162_half_map_2.map.gz | 186.9 MB 344.3 MB 344.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26162 http://ftp.pdbj.org/pub/emdb/structures/EMD-26162 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26162 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26162 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_26162_validation.pdf.gz emd_26162_validation.pdf.gz | 930.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_26162_full_validation.pdf.gz emd_26162_full_validation.pdf.gz | 929.7 KB | 表示 | |
| XML形式データ |  emd_26162_validation.xml.gz emd_26162_validation.xml.gz | 17.5 KB | 表示 | |
| CIF形式データ |  emd_26162_validation.cif.gz emd_26162_validation.cif.gz | 20.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26162 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26162 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26162 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26162 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26162.map.gz / 形式: CCP4 / 大きさ: 371.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26162.map.gz / 形式: CCP4 / 大きさ: 371.3 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.05 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
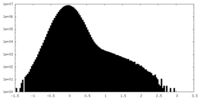
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: #1
| ファイル | emd_26162_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
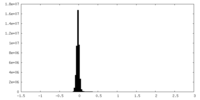
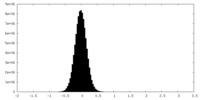
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_26162_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
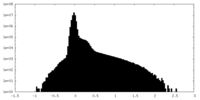
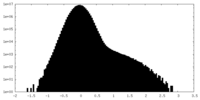
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_26162_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
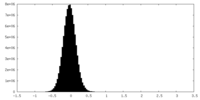
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Nipah Virus attachment protein ectodomain in complex with nAH1.3 ...
| 全体 | 名称: Nipah Virus attachment protein ectodomain in complex with nAH1.3 neutralizing antibody Fab fragment |
|---|---|
| 要素 |
|
-超分子 #1: Nipah Virus attachment protein ectodomain in complex with nAH1.3 ...
| 超分子 | 名称: Nipah Virus attachment protein ectodomain in complex with nAH1.3 neutralizing antibody Fab fragment タイプ: complex / キメラ: Yes / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Nipah henipavirus (ウイルス) Nipah henipavirus (ウイルス) |
-分子 #1: Glycoprotein G
| 分子 | 名称: Glycoprotein G / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Nipah henipavirus (ウイルス) Nipah henipavirus (ウイルス) |
| 分子量 | 理論値: 60.358535 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: HHHHHHIQNY TRSTDNQAVI KDALQGIQQQ IKGLADKIGT EIGPKVSLID TSSTITIPAN IGLLGSKISQ STASINENVN EKCKFTLPP LKIHECNISC PNPLPFREYR PQTEGVSNLV GLPNNICLQK TSNQILKPKL ISYTLPVVGQ SGTCITDPLL A MDEGYFAY ...文字列: HHHHHHIQNY TRSTDNQAVI KDALQGIQQQ IKGLADKIGT EIGPKVSLID TSSTITIPAN IGLLGSKISQ STASINENVN EKCKFTLPP LKIHECNISC PNPLPFREYR PQTEGVSNLV GLPNNICLQK TSNQILKPKL ISYTLPVVGQ SGTCITDPLL A MDEGYFAY SHLERIGSCS RGVSKQRIIG VGEVLDRGDE VPSLFMTNVW TPPNPNTVYH CSAVYNNEFY YVLCAVSTVG DP ILNSTYW SGSLMMTRLA VKPKSNGGGY NQHQLALRSI EKGRYDKVMP YGPSGIKQGD TLYFPAVGFL VRTEFKYNDS NCP ITKCQY SKPENCRLSM GIRPNSHYIL RSGLLKYNLS DGENPKVVFI EISDQRLSIG SPSKIYDSLG QPVFYQASFS WDTM IKFGD VLTVNPLVVN WRNNTVISRP GQSQCPRFNT CPEICWEGVY NDAFLIDRIN WISAGVFLDS NQTAENPVFT VFKDN EILY RAQLASEDTN AQKTITNCFL LKNKIWCISL VEIYDTGDNV IRPKLFAVKI PEQCY |
-分子 #2: nAH1.3 Fab heavy chain
| 分子 | 名称: nAH1.3 Fab heavy chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 50.643941 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVKLEESGGG LVQPGGSMKL SCVASGFSFS YYWMNWVRQS PEKGLEWVAE IRLKSNNYGT HYAESVKGRF TISRDDSKSS VYLQMNNLR PEDTGIYYCT RVITTVFAYW GQGTLVTVSA AKTTPPSVYP LAPGSAAQTN SMVTLGCLVK GYFPEPVTVT W NSGSLSSG ...文字列: EVKLEESGGG LVQPGGSMKL SCVASGFSFS YYWMNWVRQS PEKGLEWVAE IRLKSNNYGT HYAESVKGRF TISRDDSKSS VYLQMNNLR PEDTGIYYCT RVITTVFAYW GQGTLVTVSA AKTTPPSVYP LAPGSAAQTN SMVTLGCLVK GYFPEPVTVT W NSGSLSSG VHTFPAVLQS DLYTLSSSVT VPSSTWPSET VTCNVAHPAS STKVDKKIVP RDCGCKPCIC TVPEVSSVFI FP PKPKDVL TITLTPKVTC VVVDISKDDP EVQFSWFVDD VEVHTAQTQP REEQFNSTFR SVSELPIMHQ DWLNGKEFKC RVN SAAFPA PIEKTISKTK GRPKAPQVYT IPPPKEQMAK DKVSLTCMIT DFFPEDITVE WQWNGQPAEN YKNTQPIMDT DGSY FVYSK LNVQKSNWEA GNTFTCSVLH EGLHNHHTEK SLSHSPGKGG SGGGSWSHPQ FEK |
-分子 #3: nAH1.3 Fab light chain
| 分子 | 名称: nAH1.3 Fab light chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 23.947473 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DIVLTQSPAS LAVSLGQRAT ISCRASESVH DYGISFMNWF QQKPGQPPKL LIYSASNQGS GVPARFSGSG SGTDFSLNIH PMEEDDIAM YFCQQSKEVP YTFGGGTKLE IKRADAAPTV SIFPPSSEQL TSGGASVVCF LNNFYPKDIN VKWKIDGSER Q NGVLNSWT ...文字列: DIVLTQSPAS LAVSLGQRAT ISCRASESVH DYGISFMNWF QQKPGQPPKL LIYSASNQGS GVPARFSGSG SGTDFSLNIH PMEEDDIAM YFCQQSKEVP YTFGGGTKLE IKRADAAPTV SIFPPSSEQL TSGGASVVCF LNNFYPKDIN VKWKIDGSER Q NGVLNSWT DQDSKDSTYS MSSTLTLTKD EYERHNSYTC EATHKTSTSP IVKSFNRNEC |
-分子 #6: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 6 / コピー数: 1 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: SUPER-RESOLUTION / 平均電子線量: 70.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: cryoSPARC / 使用した粒子像数: 168035 |
| 初期 角度割当 | タイプ: PROJECTION MATCHING |
| 最終 角度割当 | タイプ: PROJECTION MATCHING |
 ムービー
ムービー コントローラー
コントローラー


















 Z
Z Y
Y X
X