+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2484 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Pre-fusion structure of trimeric HIV-1 envelope glycoprotein determined by cryo-electron microscopy | |||||||||
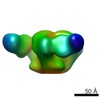
 マップデータ マップデータ | Structure of HIV-1 gp140 trimer bound to VRC03 Fab | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HIV-1 envelope glycoprotein / SOSIP gp140 trimer / HIV-1 Env / pre-fusion state | |||||||||
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.0 Å | |||||||||
 データ登録者 データ登録者 | Bartesaghi A / Merk A / Borgnia MJ / Milne JLS / Subramaniam S | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2013 ジャーナル: Nat Struct Mol Biol / 年: 2013タイトル: Prefusion structure of trimeric HIV-1 envelope glycoprotein determined by cryo-electron microscopy. 著者: Alberto Bartesaghi / Alan Merk / Mario J Borgnia / Jacqueline L S Milne / Sriram Subramaniam /  要旨: The activation of trimeric HIV-1 envelope glycoprotein (Env) by its binding to the cell-surface receptor CD4 and co-receptors (CCR5 or CXCR4) represents the first of a series of events that lead to ...The activation of trimeric HIV-1 envelope glycoprotein (Env) by its binding to the cell-surface receptor CD4 and co-receptors (CCR5 or CXCR4) represents the first of a series of events that lead to fusion between viral and target-cell membranes. Here, we present the cryo-EM structure, at subnanometer resolution (~6 Å at 0.143 FSC), of the 'closed', prefusion state of trimeric HIV-1 Env complexed to the broadly neutralizing antibody VRC03. We show that three gp41 helices at the core of the trimer serve as an anchor around which the rest of Env is reorganized upon activation to the 'open' quaternary conformation. The architecture of trimeric HIV-1 Env in the prefusion state and in the activated intermediate state resembles the corresponding states of influenza hemagglutinin trimers, thus providing direct evidence for the similarity in entry mechanisms used by HIV-1, influenza and related enveloped viruses. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2484.map.gz emd_2484.map.gz | 55.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2484-v30.xml emd-2484-v30.xml emd-2484.xml emd-2484.xml | 13 KB 13 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  EMD-2484_square.png EMD-2484_square.png | 290.9 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2484 http://ftp.pdbj.org/pub/emdb/structures/EMD-2484 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2484 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2484 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_2484_validation.pdf.gz emd_2484_validation.pdf.gz | 240.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_2484_full_validation.pdf.gz emd_2484_full_validation.pdf.gz | 239.5 KB | 表示 | |
| XML形式データ |  emd_2484_validation.xml.gz emd_2484_validation.xml.gz | 6.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2484 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2484 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2484 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2484 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  4cc8MC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10004 (タイトル: Pre-fusion structure of trimeric HIV-1 envelope glycoprotein determined by cryo-electron microscopy EMPIAR-10004 (タイトル: Pre-fusion structure of trimeric HIV-1 envelope glycoprotein determined by cryo-electron microscopyData size: 117.8 Data #1: HIV-1 envelope glycoprotein micrographs [micrographs - single frame]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2484.map.gz / 形式: CCP4 / 大きさ: 62.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2484.map.gz / 形式: CCP4 / 大きさ: 62.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Structure of HIV-1 gp140 trimer bound to VRC03 Fab | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.08 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Complex of KNH1144 SOSIP gp140 trimer with VRC03 Fab.
| 全体 | 名称: Complex of KNH1144 SOSIP gp140 trimer with VRC03 Fab. |
|---|---|
| 要素 |
|
-超分子 #1000: Complex of KNH1144 SOSIP gp140 trimer with VRC03 Fab.
| 超分子 | 名称: Complex of KNH1144 SOSIP gp140 trimer with VRC03 Fab. タイプ: sample / ID: 1000 / 集合状態: Tetramer (gp41, gp120, Fab Heavy, Fab Light) / Number unique components: 4 |
|---|---|
| 分子量 | 理論値: 670 KDa |
-分子 #1: gp120
| 分子 | 名称: gp120 / タイプ: protein_or_peptide / ID: 1 / Name.synonym: Envelope glycoprotein / コピー数: 3 / 集合状態: monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)株: HIV-1 isolate 00KE_KNH1144 / 別称: HIV-1 |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換プラスミド: SOSIP-PPI4 and furin-pcDNA3.1 Homo sapiens (ヒト) / 組換プラスミド: SOSIP-PPI4 and furin-pcDNA3.1 |
-分子 #2: gp41
| 分子 | 名称: gp41 / タイプ: protein_or_peptide / ID: 2 / Name.synonym: Envelope Glycoprotein 詳細: Complete ectodomain of HIV-1 Env from the Clade A strain KNH1144 inlcuding residues in the membrane proximal external region with the following residue substitutions A662E, S668N, and S676T コピー数: 3 / 集合状態: monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)株: HIV-1 isolate 00KE_KNH1144 / 別称: HIV-1 |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換プラスミド: SOSIP-PPI4 and furin-pcDNA3.1 Homo sapiens (ヒト) / 組換プラスミド: SOSIP-PPI4 and furin-pcDNA3.1 |
-分子 #3: Monoclonal antibody VRC03 Fab Heavy chain
| 分子 | 名称: Monoclonal antibody VRC03 Fab Heavy chain / タイプ: protein_or_peptide / ID: 3 / Name.synonym: VRC03 Fab / 詳細: Fab fragment / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK 293 Homo sapiens (ヒト) / 組換細胞: HEK 293 |
-分子 #4: Monoclonal antibody VRC03 Fab Light chain
| 分子 | 名称: Monoclonal antibody VRC03 Fab Light chain / タイプ: protein_or_peptide / ID: 4 / Name.synonym: VRC03 Fab / 詳細: Fab fragment / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK 293 Homo sapiens (ヒト) / 組換細胞: HEK 293 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.65 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 / 詳細: TNE Buffer (10 mM Tris, 150 mM NaCl, 1 mM EDTA) |
| グリッド | 詳細: Protochips C-flat R 2/2, plasma cleaned |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV 手法: blot for 6 seconds, blot offset of -2, plunge into an ethane slurry cooled by liquid nitrogen |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 日付 | 2011年8月9日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) 実像数: 4713 / 平均電子線量: 10 e/Å2 / ビット/ピクセル: 16 |
| 電子線 | 加速電圧: 80 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 75000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 詳細 | Particles were selected manually, classified in 2D using IMAGIC and 3D refinement was done with FREALIGN. |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C3 (3回回転対称) / 解像度のタイプ: BY AUTHOR / 解像度: 6.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: EMAN, IMAGIC, FREALIGN / 使用した粒子像数: 88125 |
| 最終 2次元分類 | クラス数: 500 |
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - #0 - Chain ID: G / Chain - #1 - Chain ID: H / Chain - #2 - Chain ID: L |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | 3SE8, Chain G and chains H, L fitted as two separate rigid bodies into map. 3HMG helix fitted by hand into map. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-4cc8: |
-原子モデル構築 2
| 初期モデル | PDB ID: Chain - Chain ID: B |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Protocol: Rigid body. Automated fitting procedures. Only residues 92-122 of chain B were fitted. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-4cc8: |
 ムービー
ムービー コントローラー
コントローラー









 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)























