+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23861 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Asymmetric structure of the uncleaved full-length HIV-1 envelope glycoprotein trimer in state U2 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / virus-mediated perturbation of host defense response / fusion of virus membrane with host endosome membrane / viral envelope ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / virus-mediated perturbation of host defense response / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / apoptotic process / host cell plasma membrane / structural molecule activity / virion membrane / identical protein binding / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   HIV-1 (ヒト免疫不全ウイルス) HIV-1 (ヒト免疫不全ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.7 Å | |||||||||
 データ登録者 データ登録者 | Zhang SJ / Wang KY / Wang WL / Sodroksi J / Mao YD | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: J Virol / 年: 2021 ジャーナル: J Virol / 年: 2021タイトル: Asymmetric Structures and Conformational Plasticity of the Uncleaved Full-Length Human Immunodeficiency Virus Envelope Glycoprotein Trimer. 著者: Shijian Zhang / Kunyu Wang / Wei Li Wang / Hanh T Nguyen / Shuobing Chen / Maolin Lu / Eden P Go / Haitao Ding / Robert T Steinbock / Heather Desaire / John C Kappes / Joseph Sodroski / Youdong Mao /   要旨: The functional human immunodeficiency virus (HIV-1) envelope glycoprotein (Env) trimer [(gp120/gp41)] is produced by cleavage of a conformationally flexible gp160 precursor. gp160 cleavage or the ...The functional human immunodeficiency virus (HIV-1) envelope glycoprotein (Env) trimer [(gp120/gp41)] is produced by cleavage of a conformationally flexible gp160 precursor. gp160 cleavage or the binding of BMS-806, an entry inhibitor, stabilizes the pretriggered, "closed" (state 1) conformation recognized by rarely elicited broadly neutralizing antibodies. Poorly neutralizing antibodies (pNAbs) elicited at high titers during natural infection recognize more "open" Env conformations (states 2 and 3) induced by binding the receptor, CD4. We found that BMS-806 treatment and cross-linking decreased the exposure of pNAb epitopes on cell surface gp160; however, after detergent solubilization, cross-linked and BMS-806-treated gp160 sampled non-state-1 conformations that could be recognized by pNAbs. Cryo-electron microscopy of the purified BMS-806-bound gp160 revealed two hitherto unknown asymmetric trimer conformations, providing insights into the allosteric coupling between trimer opening and structural variation in the gp41 HR1 region. The individual protomer structures in the asymmetric gp160 trimers resemble those of other genetically modified or antibody-bound cleaved HIV-1 Env trimers, which have been suggested to assume state-2-like conformations. Asymmetry of the uncleaved Env potentially exposes surfaces of the trimer to pNAbs. To evaluate the effect of stabilizing a state-1-like conformation of the membrane Env precursor, we treated cells expressing wild-type HIV-1 Env with BMS-806. BMS-806 treatment decreased both gp160 cleavage and the addition of complex glycans, implying that gp160 conformational flexibility contributes to the efficiency of these processes. Selective pressure to maintain flexibility in the precursor of functional Env allows the uncleaved Env to sample asymmetric conformations that potentially skew host antibody responses toward pNAbs. The envelope glycoprotein (Env) trimers on the surface of human immunodeficiency virus (HIV-1) mediate the entry of the virus into host cells and serve as targets for neutralizing antibodies. The functional Env trimer is produced by cleavage of the gp160 precursor in the infected cell. We found that the HIV-1 Env precursor is highly plastic, allowing it to assume different asymmetric shapes. This conformational plasticity is potentially important for Env cleavage and proper modification by sugars. Having a flexible, asymmetric Env precursor that can misdirect host antibody responses without compromising virus infectivity would be an advantage for a persistent virus like HIV-1. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23861.map.gz emd_23861.map.gz | 131.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23861-v30.xml emd-23861-v30.xml emd-23861.xml emd-23861.xml | 9.5 KB 9.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_23861.png emd_23861.png | 180.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23861 http://ftp.pdbj.org/pub/emdb/structures/EMD-23861 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23861 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23861 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_23861_validation.pdf.gz emd_23861_validation.pdf.gz | 353.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_23861_full_validation.pdf.gz emd_23861_full_validation.pdf.gz | 352.9 KB | 表示 | |
| XML形式データ |  emd_23861_validation.xml.gz emd_23861_validation.xml.gz | 6.3 KB | 表示 | |
| CIF形式データ |  emd_23861_validation.cif.gz emd_23861_validation.cif.gz | 7.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23861 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23861 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23861 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23861 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7n6wMC  7n6uC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10163 (タイトル: Asymmetric structures of the uncleaved full-length HIV-1 envelope glycoprotein trimer EMPIAR-10163 (タイトル: Asymmetric structures of the uncleaved full-length HIV-1 envelope glycoprotein trimerData size: 4.0 TB Data #1: Drift-corrected micrographs of the uncleaved full-length HIV-1 envelope glycoprotein trimer (300 kV) [micrographs - single frame] Data #2: Drift-corrected micrographs of the uncleaved full-length HIV-1 envelope glycoprotein trimer (200 kV) [micrographs - single frame] Data #3: The classified particle stacks of the full-length HIV-1 envelope precursor in the P2 class [picked particles - single frame - processed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23861.map.gz / 形式: CCP4 / 大きさ: 144.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23861.map.gz / 形式: CCP4 / 大きさ: 144.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.685 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
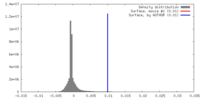
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : The uncleaved full-length human immunodeficiency virus (HIV-1) en...
| 全体 | 名称: The uncleaved full-length human immunodeficiency virus (HIV-1) envelope glycoprotein trimer |
|---|---|
| 要素 |
|
-超分子 #1: The uncleaved full-length human immunodeficiency virus (HIV-1) en...
| 超分子 | 名称: The uncleaved full-length human immunodeficiency virus (HIV-1) envelope glycoprotein trimer タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   HIV-1 (ヒト免疫不全ウイルス) HIV-1 (ヒト免疫不全ウイルス) |
| 組換発現 | 生物種:  |
-分子 #1: HIV-1 gp160 glycoprotein
| 分子 | 名称: HIV-1 gp160 glycoprotein / タイプ: protein_or_peptide / ID: 1 / 光学異性体: DEXTRO |
|---|---|
| 配列 | 文字列: MRVKEKYQHL WRWGWRWGTM LLGMLMICSA TEKLWVTVYY GVPVWKEATT TLFCASDAKA YDTEVHNVWA THACVPTDPN PQEVVLENVT EHFNMWKNNM VEQMQEDIIS LWDQSLKPCV KLTPLCVTLN CKDVNATNTT NDSEGTMERG EIKNCSFNIT TSIRDEVQKE ...文字列: MRVKEKYQHL WRWGWRWGTM LLGMLMICSA TEKLWVTVYY GVPVWKEATT TLFCASDAKA YDTEVHNVWA THACVPTDPN PQEVVLENVT EHFNMWKNNM VEQMQEDIIS LWDQSLKPCV KLTPLCVTLN CKDVNATNTT NDSEGTMERG EIKNCSFNIT TSIRDEVQKE YALFYKLDVV PIDNNNTSYR LISCDTSVIT QACPKISFEP IPIHYCAPAG FAILKCNDKT FNGKGPCKNV STVQCTHGIR PVVSTQLLLN GSLAEEEVVI RSDNFTNNAK TIIVQLKESV EINCTRPNNN TRKSIHIGPG RAFYTTGEII GDIRQAHCNI SRAKWNDTLK QIVIKLREQF ENKTIVFNHS SGGDPEIVMH SFNCGGEFFY CNSTQLFNST WNNNTEGSNN TEGNTITLPC RIKQIINMWQ EVGKAMYAPP IRGQIRCSSN ITGLLLTRDG GINENGTEIF RPGGGDMRDN WRSELYKYKV VKIEPLGVAP TKAKRRVVQS EKSAVGIGAV FLGFLGAAGS TMGAASMTLT VQARLLLSGI VQQQNNLLRA IEAQQRMLQL TVWGIKQLQA RVLAVERYLG DQQLLGIWGC SGKLICTTAV PWNASWSNKS LDRIWNNMTW MEWEREIDNY TSEIYTLIEE SQNQQEKNEQ ELLELDKWAS LWNWFDITKW LWYIKIFIMI VGGLVGLRLV FTVLSIVNRV RQGYSPLSFQ TLLPAPRGPD RPEGIEEEGG ERDRDRSGRL VNGSLALIWD DLRSLCLFSY HRLRDLLLIV TRIVELLGRR GWEALKYWWN LLQYWSQELK NSAVSLLNAT AIAVAEGTDR VIEVVQGACR AIRHIPRRIR QGLERILL |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 QUANTUM (4k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.7 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 55571 |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)