| 登録情報 | データベース: EMDB / ID: EMD-23378
|
|---|
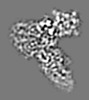
| タイトル | CryoEM structure of Mayaro virus |
|---|
 マップデータ マップデータ | CryoEM density map of MAYV focused region |
|---|
 試料 試料 | - ウイルス:
 Mayaro virus (マヤロウイルス) Mayaro virus (マヤロウイルス)- タンパク質・ペプチド: Capsid protein
- タンパク質・ペプチド: E1 protein
- タンパク質・ペプチド: E2 protein
|
|---|
 キーワード キーワード | alphavirus / togavirus / enveloped virus / pathogen / VIRAL PROTEIN |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
togavirin / T=4 icosahedral viral capsid / symbiont-mediated suppression of host toll-like receptor signaling pathway / host cell cytoplasm / serine-type endopeptidase activity / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / host cell nucleus / host cell plasma membrane ...togavirin / T=4 icosahedral viral capsid / symbiont-mediated suppression of host toll-like receptor signaling pathway / host cell cytoplasm / serine-type endopeptidase activity / fusion of virus membrane with host endosome membrane / symbiont entry into host cell / virion attachment to host cell / host cell nucleus / host cell plasma membrane / virion membrane / structural molecule activity / proteolysis / RNA binding / membrane類似検索 - 分子機能 Alphavirus E2 glycoprotein, domain B / Peptidase S3, togavirin / Alphavirus E2 glycoprotein / Alphavirus E3 spike glycoprotein / Alphavirus E1 glycoprotein / Alphavirus E2 glycoprotein, domain A / Alphavirus E2 glycoprotein, domain C / Alphavirus E2 glycoprotein / Alphavirus core protein / Alphavirus E3 glycoprotein ...Alphavirus E2 glycoprotein, domain B / Peptidase S3, togavirin / Alphavirus E2 glycoprotein / Alphavirus E3 spike glycoprotein / Alphavirus E1 glycoprotein / Alphavirus E2 glycoprotein, domain A / Alphavirus E2 glycoprotein, domain C / Alphavirus E2 glycoprotein / Alphavirus core protein / Alphavirus E3 glycoprotein / Alphavirus E1 glycoprotein / Alphavirus core protein (CP) domain profile. / Flavivirus/Alphavirus glycoprotein, immunoglobulin-like domain superfamily / Flavivirus glycoprotein, central and dimerisation domain superfamily / Flaviviral glycoprotein E, dimerisation domain / Immunoglobulin E-set / Peptidase S1, PA clan, chymotrypsin-like fold / Peptidase S1, PA clan類似検索 - ドメイン・相同性 Structural polyprotein / Structural polyprotein / Structural polyprotein類似検索 - 構成要素 |
|---|
| 生物種 |  Mayaro virus (マヤロウイルス) Mayaro virus (マヤロウイルス) |
|---|
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.4 Å |
|---|
 データ登録者 データ登録者 | Chmielewski D / Kaelber J |
|---|
| 資金援助 |  米国, 5件 米国, 5件 | Organization | Grant number | 国 |
|---|
| National Institutes of Health/National Institute Of Allergy and Infectious Diseases (NIH/NIAID) | P01AI120943 |  米国 米国 | | National Institutes of Health/National Institute Of Allergy and Infectious Diseases (NIH/NIAID) | P41GM103832 |  米国 米国 | | National Institutes of Health/National Institute Of Allergy and Infectious Diseases (NIH/NIAID) | K22AI125474 |  米国 米国 | | National Institutes of Health/National Institute Of Allergy and Infectious Diseases (NIH/NIAID) | R01AI153433 |  米国 米国 | | National Institutes of Health/National Institute Of Allergy and Infectious Diseases (NIH/NIAID) | R24AI120942 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: To Be Published ジャーナル: To Be Published
タイトル: Near-atomic resolution Cryo-EM structure of Mayaro virus identifies key structural determinants of alphavirus particle formation
著者: Chmielewski D / Kaelber JT / Jin J / Weaver S / Auguste AJ / Chiu W |
|---|
| 履歴 | | 登録 | 2021年1月27日 | - |
|---|
| ヘッダ(付随情報) 公開 | 2022年2月9日 | - |
|---|
| マップ公開 | 2022年2月9日 | - |
|---|
| 更新 | 2024年11月13日 | - |
|---|
| 現状 | 2024年11月13日 | 処理サイト: RCSB / 状態: 公開 |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Mayaro virus (マヤロウイルス)
Mayaro virus (マヤロウイルス) データ登録者
データ登録者 米国, 5件
米国, 5件  引用
引用 ジャーナル: To Be Published
ジャーナル: To Be Published 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_23378.map.gz
emd_23378.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-23378-v30.xml
emd-23378-v30.xml emd-23378.xml
emd-23378.xml EMDBヘッダ
EMDBヘッダ emd_23378.png
emd_23378.png emd-23378.cif.gz
emd-23378.cif.gz emd_23378_additional_1.map.gz
emd_23378_additional_1.map.gz emd_23378_additional_2.map.gz
emd_23378_additional_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-23378
http://ftp.pdbj.org/pub/emdb/structures/EMD-23378 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23378
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23378 emd_23378_validation.pdf.gz
emd_23378_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_23378_full_validation.pdf.gz
emd_23378_full_validation.pdf.gz emd_23378_validation.xml.gz
emd_23378_validation.xml.gz emd_23378_validation.cif.gz
emd_23378_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23378
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23378 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23378
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-23378 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_23378.map.gz / 形式: CCP4 / 大きさ: 1.4 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_23378.map.gz / 形式: CCP4 / 大きさ: 1.4 GB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) 試料の構成要素
試料の構成要素 Mayaro virus (マヤロウイルス)
Mayaro virus (マヤロウイルス) Mayaro virus (マヤロウイルス)
Mayaro virus (マヤロウイルス) Mayaro virus (マヤロウイルス)
Mayaro virus (マヤロウイルス) Mayaro virus (マヤロウイルス)
Mayaro virus (マヤロウイルス) 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)