+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-20212 | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Bimetallic dodecameric cage design 3 (BMC3) from cytochrome cb562 | |||||||||||||||
 マップデータ マップデータ | 2.6 A map of dodecameric cage | |||||||||||||||
 試料 試料 |
| |||||||||||||||
| 機能・相同性 | Cytochrome b562 / Cytochrome b562 / Cytochrome c/b562 / electron transport chain / periplasmic space / electron transfer activity / iron ion binding / heme binding / Soluble cytochrome b562 機能・相同性情報 機能・相同性情報 | |||||||||||||||
| 生物種 |  | |||||||||||||||
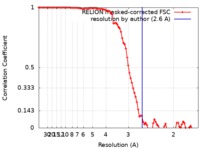
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.6 Å | |||||||||||||||
 データ登録者 データ登録者 | Golub E / Subramanian RH / Yan X / Alberstein RG / Tezcan FA | |||||||||||||||
| 資金援助 |  米国, European Union, 米国, European Union,  ドイツ, 4件 ドイツ, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nature / 年: 2020 ジャーナル: Nature / 年: 2020タイトル: Constructing protein polyhedra via orthogonal chemical interactions. 著者: Eyal Golub / Rohit H Subramanian / Julian Esselborn / Robert G Alberstein / Jake B Bailey / Jerika A Chiong / Xiaodong Yan / Timothy Booth / Timothy S Baker / F Akif Tezcan /  要旨: Many proteins exist naturally as symmetrical homooligomers or homopolymers. The emergent structural and functional properties of such protein assemblies have inspired extensive efforts in ...Many proteins exist naturally as symmetrical homooligomers or homopolymers. The emergent structural and functional properties of such protein assemblies have inspired extensive efforts in biomolecular design. As synthesized by ribosomes, proteins are inherently asymmetric. Thus, they must acquire multiple surface patches that selectively associate to generate the different symmetry elements needed to form higher-order architectures-a daunting task for protein design. Here we address this problem using an inorganic chemical approach, whereby multiple modes of protein-protein interactions and symmetry are simultaneously achieved by selective, 'one-pot' coordination of soft and hard metal ions. We show that a monomeric protein (protomer) appropriately modified with biologically inspired hydroxamate groups and zinc-binding motifs assembles through concurrent Fe and Zn coordination into discrete dodecameric and hexameric cages. Our cages closely resemble natural polyhedral protein architectures and are, to our knowledge, unique among designed systems in that they possess tightly packed shells devoid of large apertures. At the same time, they can assemble and disassemble in response to diverse stimuli, owing to their heterobimetallic construction on minimal interprotein-bonding footprints. With stoichiometries ranging from [2 Fe:9 Zn:6 protomers] to [8 Fe:21 Zn:12 protomers], these protein cages represent some of the compositionally most complex protein assemblies-or inorganic coordination complexes-obtained by design. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_20212.map.gz emd_20212.map.gz | 56.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-20212-v30.xml emd-20212-v30.xml emd-20212.xml emd-20212.xml | 18.8 KB 18.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_20212_fsc.xml emd_20212_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_20212.png emd_20212.png | 82.2 KB | ||
| その他 |  emd_20212_half_map_1.map.gz emd_20212_half_map_1.map.gz emd_20212_half_map_2.map.gz emd_20212_half_map_2.map.gz | 49.8 MB 49.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-20212 http://ftp.pdbj.org/pub/emdb/structures/EMD-20212 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20212 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20212 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_20212_validation.pdf.gz emd_20212_validation.pdf.gz | 604.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_20212_full_validation.pdf.gz emd_20212_full_validation.pdf.gz | 604.3 KB | 表示 | |
| XML形式データ |  emd_20212_validation.xml.gz emd_20212_validation.xml.gz | 16.3 KB | 表示 | |
| CIF形式データ |  emd_20212_validation.cif.gz emd_20212_validation.cif.gz | 21.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20212 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20212 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20212 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20212 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_20212.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_20212.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 2.6 A map of dodecameric cage | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8452 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-ハーフマップ: half-map 2 prior to postprocessing in Relion 3.0
| ファイル | emd_20212_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map 2 prior to postprocessing in Relion 3.0 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half-map 1 prior to postprocessing in Relion 3.0
| ファイル | emd_20212_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map 1 prior to postprocessing in Relion 3.0 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Bimetallic dodecameric cage 3 (BMC3)
| 全体 | 名称: Bimetallic dodecameric cage 3 (BMC3) |
|---|---|
| 要素 |
|
-超分子 #1: Bimetallic dodecameric cage 3 (BMC3)
| 超分子 | 名称: Bimetallic dodecameric cage 3 (BMC3) / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 詳細: Cryo-EM reconstruction of self-assembled BMC3 dodecameric cages |
|---|---|
| 由来(天然) | 生物種:  |
| 組換発現 | 生物種:  |
| 分子量 | 実験値: 150 KDa |
-分子 #1: Soluble cytochrome b562
| 分子 | 名称: Soluble cytochrome b562 / タイプ: protein_or_peptide / ID: 1 / コピー数: 12 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 11.809307 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: ADLEHNMHTL NDNLKHIEKA DNATTVKDAL TKMQAAAQDA WSATPPKLED KSPDSPEMSD FRCGFWELIG QINAALHLAK QCKVKEAQA AAEQLKTTCN ACHQKYR |
-分子 #2: HEME C
| 分子 | 名称: HEME C / タイプ: ligand / ID: 2 / コピー数: 12 / 式: HEC |
|---|---|
| 分子量 | 理論値: 618.503 Da |
| Chemical component information |  ChemComp-HEC: |
-分子 #3: ACETOHYDROXAMIC ACID
| 分子 | 名称: ACETOHYDROXAMIC ACID / タイプ: ligand / ID: 3 / コピー数: 24 / 式: HAE |
|---|---|
| 分子量 | 理論値: 75.067 Da |
| Chemical component information |  ChemComp-HAE: |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 24 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #5: FE (III) ION
| 分子 | 名称: FE (III) ION / タイプ: ligand / ID: 5 / コピー数: 8 / 式: FE |
|---|---|
| 分子量 | 理論値: 55.845 Da |
-分子 #6: water
| 分子 | 名称: water / タイプ: ligand / ID: 6 / コピー数: 171 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8.5 / 構成要素 - 濃度: 20.0 millimolar / 構成要素 - 名称: Tris |
|---|---|
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 400 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 101.325 kPa / 詳細: The grid was glow discharged at 20 mA for 30 s. |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
| 詳細 | Protein solutions containing 20 micromolar BMC3 in 20 mM Tris (pH 8.5) were incubated with [FeSO4] = 20 micromolar, [ZnCl2] = 60 micromolar for 2-3 h to form cages. Samples were concentrated 10 fold prior to grid preparation. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 実像数: 4672 / 平均露光時間: 10.0 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: |
|---|---|
| 詳細 | Symmetry mates were generated from the atomic model to build the dodecameric cage. Chain IDs were re-assigned to ascend from A-L. The cage PDB was manually fit to the EM density map in UCSF Chimera and refined using phenix.real_space_refine |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-6ovh: |
 ムービー
ムービー コントローラー
コントローラー




















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)