[日本語] English
 万見
万見- EMDB-20086: In situ structure of rotavirus VP1 RNA-dependent RNA polymerase (TLP) -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-20086 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | In situ structure of rotavirus VP1 RNA-dependent RNA polymerase (TLP) | |||||||||
 マップデータ マップデータ | filtered, B-sharpened, masked | |||||||||
 試料 試料 | Rhesus rotavirus != Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) Rhesus rotavirus
| |||||||||
 キーワード キーワード | Rotavirus / RNA-dependent RNA polymerase / VP1 / VP2 / VIRAL PROTEIN-TRANSFERASE complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報T=2 icosahedral viral capsid / viral inner capsid / viral genome replication / virion component / viral nucleocapsid / RNA-directed RNA polymerase / RNA-dependent RNA polymerase activity / nucleotide binding / DNA-templated transcription / RNA binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス) Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.5 Å | |||||||||
 データ登録者 データ登録者 | Jenni S / Salgado EN | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: J Mol Biol / 年: 2019 ジャーナル: J Mol Biol / 年: 2019タイトル: In situ Structure of Rotavirus VP1 RNA-Dependent RNA Polymerase. 著者: Simon Jenni / Eric N Salgado / Tobias Herrmann / Zongli Li / Timothy Grant / Nikolaus Grigorieff / Stefano Trapani / Leandro F Estrozi / Stephen C Harrison /   要旨: Rotaviruses, like other non-enveloped, double-strand RNA viruses, package an RNA-dependent RNA polymerase (RdRp) with each duplex of their segmented genomes. Rotavirus cell entry results in loss of ...Rotaviruses, like other non-enveloped, double-strand RNA viruses, package an RNA-dependent RNA polymerase (RdRp) with each duplex of their segmented genomes. Rotavirus cell entry results in loss of an outer protein layer and delivery into the cytosol of an intact, inner capsid particle (the "double-layer particle," or DLP). The RdRp, designated VP1, is active inside the DLP; each VP1 achieves many rounds of mRNA transcription from its associated genome segment. Previous work has shown that one VP1 molecule lies close to each 5-fold axis of the icosahedrally symmetric DLP, just beneath the inner surface of its protein shell, embedded in tightly packed RNA. We have determined a high-resolution structure for the rotavirus VP1 RdRp in situ, by local reconstruction of density around individual 5-fold positions. We have analyzed intact virions ("triple-layer particles"), non-transcribing DLPs and transcribing DLPs. Outer layer dissociation enables the DLP to synthesize RNA, in vitro as well as in vivo, but appears not to induce any detectable structural change in the RdRp. Addition of NTPs, Mg, and S-adenosylmethionine, which allows active transcription, results in conformational rearrangements, in both VP1 and the DLP capsid shell protein, that allow a transcript to exit the polymerase and the particle. The position of VP1 (among the five symmetrically related alternatives) at one vertex does not correlate with its position at other vertices. This stochastic distribution of site occupancies limits long-range order in the 11-segment, double-strand RNA genome. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_20086.map.gz emd_20086.map.gz | 9.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-20086-v30.xml emd-20086-v30.xml emd-20086.xml emd-20086.xml | 22.3 KB 22.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_20086_fsc.xml emd_20086_fsc.xml | 12.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_20086.png emd_20086.png | 144.8 KB | ||
| マスクデータ |  emd_20086_msk_1.map emd_20086_msk_1.map | 103 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-20086.cif.gz emd-20086.cif.gz | 6.9 KB | ||
| その他 |  emd_20086_additional_1.map.gz emd_20086_additional_1.map.gz emd_20086_additional_2.map.gz emd_20086_additional_2.map.gz emd_20086_half_map_1.map.gz emd_20086_half_map_1.map.gz emd_20086_half_map_2.map.gz emd_20086_half_map_2.map.gz | 94.4 MB 45.9 MB 9.4 MB 9.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-20086 http://ftp.pdbj.org/pub/emdb/structures/EMD-20086 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20086 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20086 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_20086_validation.pdf.gz emd_20086_validation.pdf.gz | 708.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_20086_full_validation.pdf.gz emd_20086_full_validation.pdf.gz | 707.8 KB | 表示 | |
| XML形式データ |  emd_20086_validation.xml.gz emd_20086_validation.xml.gz | 18.2 KB | 表示 | |
| CIF形式データ |  emd_20086_validation.cif.gz emd_20086_validation.cif.gz | 23.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20086 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20086 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20086 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-20086 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_20086.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_20086.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | filtered, B-sharpened, masked | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.23 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
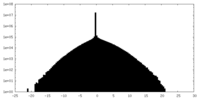
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_20086_msk_1.map emd_20086_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: filtered, B-sharpened
| ファイル | emd_20086_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | filtered, B-sharpened | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: filtered
| ファイル | emd_20086_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | filtered | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half-map 1, unmodified
| ファイル | emd_20086_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map 1, unmodified | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half-map 2, unmodified
| ファイル | emd_20086_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half-map 2, unmodified | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Rhesus rotavirus
| 全体 | 名称:  Rhesus rotavirus (ウイルス) Rhesus rotavirus (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3])
| 超分子 | 名称: Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: all / 詳細: TLP / NCBI-ID: 444185 生物種: Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) Sci species strain: RVA/Monkey/United States/RRV/1975/G3P5B[3] ウイルスタイプ: VIRION / ウイルス・単離状態: SEROTYPE / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|
-分子 #1: Inner capsid protein VP2
| 分子 | 名称: Inner capsid protein VP2 / タイプ: protein_or_peptide / ID: 1 / コピー数: 10 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス) Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス)株: RVA/Monkey/United States/RRV/1975/G3P5B[3] |
| 分子量 | 理論値: 103.425992 KDa |
| 配列 | 文字列: MAYRKRGARR ETNLKQDDRM QEKEENKNVN TNSENKNATK PQLSEKVLSQ KEEVITDNQE EIKIADEVKK SNKEESKQLL EVLKTKEEH QKEVQYEILQ KTIPTFEPKE SILKKLEDIK PEQVKKQTKL FRIFEPRQLP VYRANGEKEL RNRWYWKLKR D TLPDGDYD ...文字列: MAYRKRGARR ETNLKQDDRM QEKEENKNVN TNSENKNATK PQLSEKVLSQ KEEVITDNQE EIKIADEVKK SNKEESKQLL EVLKTKEEH QKEVQYEILQ KTIPTFEPKE SILKKLEDIK PEQVKKQTKL FRIFEPRQLP VYRANGEKEL RNRWYWKLKR D TLPDGDYD VREYFLNLYD QVLTEMPDYL LLKDMAVENK NSRDAGKVVD SETAAICDAI FQDEETEGVV RRFIAEMRQR VQ ADRNVVN YPSILHPIDH AFNEYFLQHQ LVEPLNNDII FNYIPERIRN DVNYILNMDR NLPSTARYIR PNLLQDRLNL HDN FESLWD TITTSNYILA RSVVPDLKEL VSTEAQIQKM SQDLQLEALT IQSETQFLTG INSQAANDCF KTLIAAMLSQ RTMS LDFVT TNYMSLISGM WLLTVVPNDM FIRESLVACQ LAIINTIIYP AFGMQRMHYR NGDPQTPFQI AEQQIQNFQV ANWLH FVNN NQFRQVVIDG VLNQVLNDNI RNGHVVNQLM EALMQLSRQQ FPTMPVDYKR SIQRGILLLS NRLGQLVDLT RLLAYN YET LMACITMNMQ HVQTLTTEKL QLTSVTSLCM LIGNATVIPS PQTLFHYYNV NVNFHSNYNE RINDAVAIIT AANRLNL YQ KKMKSIVEDF LKRLQIFDIS RVPDDQMYRL RDRLRLLPVE IRRLDIFNLI LMNMEQIERA SDKIAQGVII AYRDMQLE R DEMYGYVNIA RNLDGFQQIN LEELMRTGDY AQITNMLLNN QPVALVGALP FITDSSVISL VAKLDATVFA QIVKLRKVD TLKPILYKIN SDSNDFYLVA NYDWVPTSTT KVYKQIPQQF DFRASMHMLT SNLTFTVYSD LLAFVSADTV EPINAVAFDN MRIMNEL UniProtKB: Inner capsid protein VP2 |
-分子 #2: RNA-directed RNA polymerase
| 分子 | 名称: RNA-directed RNA polymerase / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス) Rotavirus A (strain RVA/Monkey/United States/RRV/1975/G3P5B[3]) (ウイルス)株: RVA/Monkey/United States/RRV/1975/G3P5B[3] |
| 分子量 | 理論値: 125.276305 KDa |
| 配列 | 文字列: MGKYNLILSE YLSFIYNSQS AVQIPIYYSS NSELENRCIE FHSKCLENSK NGLSLKKLFV EYSDVIENAT LLSILSYSYD KYNAVERKL VKYAKGKPLE ADLTVNELDY ENNKITSELF PTAEEYTDLL MDPAILTSLS SNLNAVMFWL EKHENDVAEK L KIYKRRLD ...文字列: MGKYNLILSE YLSFIYNSQS AVQIPIYYSS NSELENRCIE FHSKCLENSK NGLSLKKLFV EYSDVIENAT LLSILSYSYD KYNAVERKL VKYAKGKPLE ADLTVNELDY ENNKITSELF PTAEEYTDLL MDPAILTSLS SNLNAVMFWL EKHENDVAEK L KIYKRRLD LFTIVASTVN KYGVPRHNAK YRYEYEVMKD KPYYLVTWAN SSIEMLMSVF SHEDYLIARE LIVLSYSNRS TL AKLVSSP MSILVALVDI NGTFITNEEL ELEFSNKYVR AIVPDQTFDE LKQMLDNMRK AGLTDIPKMI QDWLVDCSIE KFP LMAKIY SWSFHVGFRK QKMLDAALDQ LKTEYTEDVD DEMYREYTML IRDEVVKMLE EPVKHDDHLL QDSELAGLLS MSSA SNGES RQLKFGRKTI FSTKKNMHVM DDMANGRYTP GIIPPVNVDK PIPLGRRDVP GRRTRIIFIL PYEYFIAQHA VVEKM LIYA KHTREYAEFY SQSNQLLSYG DVTRFLSNNS MVLYTDVSQW DSSQHNTQPF RKGIIMGLDM LANMTNDARV IQTLNL YKQ TQINLMDSYV QIPDGNVIKK IQYGAVASGE KQTKAANSIA NLALIKTVLS RISNKYSFAT KIIRVDGDDN YAVLQFN TE VTKQMVQDVS NDVRETYARM NTKVKALVST VGIEIAKRYI AGGKIFFRAG INLLNNEKKG QSTQWDQAAV LYSNYIVN R LRGFETDREF ILTKIMQMTS VAITGSLRLF PSERVLTTNS TFKVFDSEDF IIEYGTTDDE VYIQRAFMSL SSQKSGIAD EIAASSTFKN YVSRLSEQLL FSKNNIVSRG IALTEKAKLN SYAPISLEKR RAQISALLTM LQKPVTFKSS KITINDILRD IKPFFTVNE AHLPIQYQKF MPTLPDNVQY IIQCIGSRTY QIEDDGSKSA ISRLISKYSV YKPSIEELYK VISLHENEIQ L YLISLGIP KIDADTYVGS KIYSQDKYRI LESYVYNLLS INYGCYQLFD FNSPDLEKLI RIPFKGKIPA VTFILHLYAK LE VINHAIK NGSWISLFCN YPKSEMIKLW KKMWNITSLR SPYTNANFFQ D UniProtKB: RNA-directed RNA polymerase |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| グリッド | 詳細: unspecified |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 64.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | プロトコル: AB INITIO MODEL |
|---|---|
| 得られたモデル |  PDB-6oj3: |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)