+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Type six secretion system exported effector 5 (Tse5) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Pore-forming protein / P.aeruginosa / effector / Bacterial Rearrangement hot spot protein / ion channel / type VI secretion system / TOXIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |  Pseudomonas (バクテリア) / Pseudomonas (バクテリア) /  | |||||||||
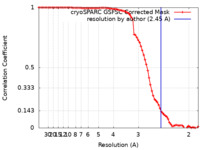
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.45 Å | |||||||||
 データ登録者 データ登録者 | Gonzalez-Magana A / Tascon I / Ubarretxena-Belandia I / Albesa-Jove D | |||||||||
| 資金援助 |  スペイン, 2件 スペイン, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Structural and functional insights into the delivery of a bacterial Rhs pore-forming toxin to the membrane. 著者: Amaia González-Magaña / Igor Tascón / Jon Altuna-Alvarez / María Queralt-Martín / Jake Colautti / Carmen Velázquez / Maialen Zabala / Jessica Rojas-Palomino / Marité Cárdenas / ...著者: Amaia González-Magaña / Igor Tascón / Jon Altuna-Alvarez / María Queralt-Martín / Jake Colautti / Carmen Velázquez / Maialen Zabala / Jessica Rojas-Palomino / Marité Cárdenas / Antonio Alcaraz / John C Whitney / Iban Ubarretxena-Belandia / David Albesa-Jové /   要旨: Bacterial competition is a significant driver of toxin polymorphism, which allows continual compensatory evolution between toxins and the resistance developed to overcome their activity. Bacterial ...Bacterial competition is a significant driver of toxin polymorphism, which allows continual compensatory evolution between toxins and the resistance developed to overcome their activity. Bacterial Rearrangement hot spot (Rhs) proteins represent a widespread example of toxin polymorphism. Here, we present the 2.45 Å cryo-electron microscopy structure of Tse5, an Rhs protein central to Pseudomonas aeruginosa type VI secretion system-mediated bacterial competition. This structural insight, coupled with an extensive array of biophysical and genetic investigations, unravels the multifaceted functional mechanisms of Tse5. The data suggest that interfacial Tse5-membrane binding delivers its encapsulated pore-forming toxin fragment to the target bacterial membrane, where it assembles pores that cause cell depolarisation and, ultimately, bacterial death. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_16778.map.gz emd_16778.map.gz | 26.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-16778-v30.xml emd-16778-v30.xml emd-16778.xml emd-16778.xml | 21.5 KB 21.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_16778_fsc.xml emd_16778_fsc.xml | 7.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_16778.png emd_16778.png | 84.7 KB | ||
| マスクデータ |  emd_16778_msk_1.map emd_16778_msk_1.map | 52.7 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-16778.cif.gz emd-16778.cif.gz | 7.1 KB | ||
| その他 |  emd_16778_half_map_1.map.gz emd_16778_half_map_1.map.gz emd_16778_half_map_2.map.gz emd_16778_half_map_2.map.gz | 48.9 MB 48.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-16778 http://ftp.pdbj.org/pub/emdb/structures/EMD-16778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-16778 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_16778_validation.pdf.gz emd_16778_validation.pdf.gz | 949 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_16778_full_validation.pdf.gz emd_16778_full_validation.pdf.gz | 948.6 KB | 表示 | |
| XML形式データ |  emd_16778_validation.xml.gz emd_16778_validation.xml.gz | 15.8 KB | 表示 | |
| CIF形式データ |  emd_16778_validation.cif.gz emd_16778_validation.cif.gz | 20.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16778 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16778 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16778 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-16778 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8cp6MC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_16778.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_16778.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.921 Å | ||||||||||||||||||||||||||||||||||||
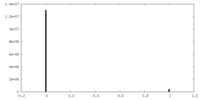
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_16778_msk_1.map emd_16778_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
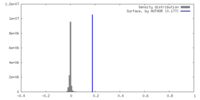
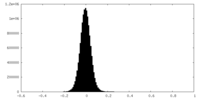
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_16778_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
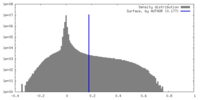
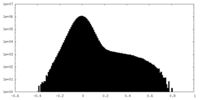
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_16778_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
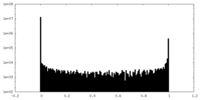
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Tse5
| 全体 | 名称: Tse5 |
|---|---|
| 要素 |
|
-超分子 #1: Tse5
| 超分子 | 名称: Tse5 / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: Pseudomonas aeruginosa type VI secretion system (T6SS) exported effector Tse5. The three chains result from the auto-cleavage of Tse5 |
|---|---|
| 由来(天然) | 生物種:  Pseudomonas (バクテリア) Pseudomonas (バクテリア) |
| 分子量 | 理論値: 146 KDa |
-分子 #1: Toxin protein Tse5
| 分子 | 名称: Toxin protein Tse5 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 7.456322 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MMGSSHHHHH HHHHSSGENL YFQGGSMSGL PVSHVGEKVS GGVISTGSPT VHVGSSAVGL ADRVSACVPL VGK UniProtKB: Toxin protein Tse5 |
-分子 #2: Toxin protein Tse5
| 分子 | 名称: Toxin protein Tse5 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 125.970461 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: PVNPMLGSKL LPEEVDFALA APDTFTFARG YLSSNPRIGR LGRGWWLPGE SMHLELSEDA CVLVDAQGRR IGFPALAPGA QHYSGSEEL WLRRGGSSGG EAQAWRGRWA AVPAELQTQE GSVLVLSGHS YLHFQRCPDG IWRLQASFGR AGYRTEFRWS G RGLLTGVR ...文字列: PVNPMLGSKL LPEEVDFALA APDTFTFARG YLSSNPRIGR LGRGWWLPGE SMHLELSEDA CVLVDAQGRR IGFPALAPGA QHYSGSEEL WLRRGGSSGG EAQAWRGRWA AVPAELQTQE GSVLVLSGHS YLHFQRCPDG IWRLQASFGR AGYRTEFRWS G RGLLTGVR DSAGRSYALV YQQACEPSEG DDGLRLFGVI LASHDGPPPD YIDPQSPGLD WLVRYQFSDS GDLIAVRDRL GQ VVRVFAW REHMLVAHGE PGGLEVRYEW DVHAPHGRVV KQIEAGGLTR TFRYLRDATE VSDSLGRVER YEFAGEGGQR RWT ALVRAD GSRSEFDYDL FGRLVAMRDP LGRETRRRRD GQGRMLEEES PGKARYRKRV DEETGLLVEL EDAMQRRWTF ERDE RGNAT TVRGPAGSTR YAYEDPRLPD RPTRIVDPRG GERRLEWNRF GLLAALTDCS GQVWRYDYDN EGRLVASSDP LGQLT RRRY DPLGQLIGLE LADGSALSYE YDALGRQTRI ADAEGHATLF SWGHGDLLAR VSDAGGGELS YLHDEAGRLV ALTNEN GVQ AQFRYDLLDR LVEETGFDGR RQRYRYNAAD ELIAREDADG RETTYAYDRD GRLASIRVPA TEHAPALVER YRWLADG RL ASAGGADCEV RYTYDEVGNL RLESQVHADG WVYSVEHSHD ALGVRQTSRY GDAPPVAWLT YGPGHLHGAL VGAVELAF E RDALHREVRR DARRDGQDDA LFTQERQHAP LGRLQRSRLR LAGGFDWQRG YRYDGLGQLV GIDDNQYPSV RYEYDLGGR LLASRRAGAA ASTYRYDAAG NRLEGVGEHA REDARQAFAE NELYRSGFSR SETRASQAGE GPARWAGNRV ERIAGNRYRF DALGNLVER IGADGERLRL AYDGAQRLVH LTRDYADGTR LEARYRYDAL SRRIAKVVLR DGVEQQVRFG WDGDRQCAEA F ARELRTTV HEPGGFVPLL RLEQACEPDP PELLQLRQAF AAEGQPLPAQ CVPALGEARI AFFHTDHLGT PLQLSDERGQ LR WQGVPDD WRAVAPERQP GAQPIRFQGQ YHDEESGLYY NRYRYYLPEA GRYASQDPLG LGGGPNPYAY ALNAPTLAYD PTG L UniProtKB: Toxin protein Tse5 |
-分子 #3: Toxin protein Tse5
| 分子 | 名称: Toxin protein Tse5 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 15.592012 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: IIPLVVIGAF AARAAIGAAL GAGIELGMQT GKQVLGQMKD NWDSDRDLTD IKWKCIDINW KHVGASAAIG TVAPGMLSTG KTVVQSAKA IRTLSGQAAN TANRAAKLAA RKAAHADTIK KAVATQAAWQ TGKQIVKCPL KDEEEECPPQ UniProtKB: Toxin protein Tse5 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| グリッド | モデル: Quantifoil / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: CARBON / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 120 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 3.6 kPa | ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 94 % / チャンバー内温度: 289 K / 装置: LEICA EM GP |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: TFS FALCON 4i (4k x 4k) 撮影したグリッド数: 1 / 実像数: 10244 / 平均露光時間: 10.84 sec. / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | Chain - Source name: Other / Chain - Initial model type: in silico model / 詳細: Buccanner |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT |
| 得られたモデル |  PDB-8cp6: |
 ムービー
ムービー コントローラー
コントローラー



 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)