+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Amyloid fibril from the antimicrobial peptide uperin 3.5 | ||||||||||||||||||
 マップデータ マップデータ | |||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
| 機能・相同性 | Uperin / Uperin family / cytolysis in another organism / other organism cell membrane / defense response to Gram-positive bacterium / protein homodimerization activity / extracellular region / membrane / Uperin-3.5 機能・相同性情報 機能・相同性情報 | ||||||||||||||||||
| 生物種 | Uperoleia mjobergii (カエル) | ||||||||||||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 3.0 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Buecker R / Seuring C / Cazey C / Veith K / Garcia-Alai M / Gruenewald K / Landau M | ||||||||||||||||||
| 資金援助 | 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: The Cryo-EM structures of two amphibian antimicrobial cross-β amyloid fibrils. 著者: Robert Bücker / Carolin Seuring / Cornelia Cazey / Katharina Veith / Maria García-Alai / Kay Grünewald / Meytal Landau /    要旨: The amyloid-antimicrobial link hypothesis is based on antimicrobial properties found in human amyloids involved in neurodegenerative and systemic diseases, along with amyloidal structural properties ...The amyloid-antimicrobial link hypothesis is based on antimicrobial properties found in human amyloids involved in neurodegenerative and systemic diseases, along with amyloidal structural properties found in antimicrobial peptides (AMPs). Supporting this hypothesis, we here determined the fibril structure of two AMPs from amphibians, uperin 3.5 and aurein 3.3, by cryogenic electron microscopy (cryo-EM), revealing amyloid cross-β fibrils of mated β-sheets at atomic resolution. Uperin 3.5 formed a 3-blade symmetrical propeller of nine peptides per fibril layer including tight β-sheet interfaces. This cross-β cryo-EM structure complements the cross-α fibril conformation previously determined by crystallography, substantiating a secondary structure switch mechanism of uperin 3.5. The aurein 3.3 arrangement consisted of six peptides per fibril layer, all showing kinked β-sheets allowing a rounded compactness of the fibril. The kinked β-sheets are similar to LARKS (Low-complexity, Amyloid-like, Reversible, Kinked Segments) found in human functional amyloids. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_14167.map.gz emd_14167.map.gz | 125.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-14167-v30.xml emd-14167-v30.xml emd-14167.xml emd-14167.xml | 18.8 KB 18.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_14167_fsc.xml emd_14167_fsc.xml | 11.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_14167.png emd_14167.png | 161.4 KB | ||
| マスクデータ |  emd_14167_msk_1.map emd_14167_msk_1.map | 134.6 MB |  マスクマップ マスクマップ | |
| その他 |  emd_14167_half_map_1.map.gz emd_14167_half_map_1.map.gz emd_14167_half_map_2.map.gz emd_14167_half_map_2.map.gz | 105.7 MB 105.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-14167 http://ftp.pdbj.org/pub/emdb/structures/EMD-14167 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14167 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-14167 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_14167_validation.pdf.gz emd_14167_validation.pdf.gz | 715.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_14167_full_validation.pdf.gz emd_14167_full_validation.pdf.gz | 715.2 KB | 表示 | |
| XML形式データ |  emd_14167_validation.xml.gz emd_14167_validation.xml.gz | 19.4 KB | 表示 | |
| CIF形式データ |  emd_14167_validation.cif.gz emd_14167_validation.cif.gz | 25.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14167 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14167 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14167 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-14167 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7qv5MC  7qv6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_14167.map.gz / 形式: CCP4 / 大きさ: 134.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_14167.map.gz / 形式: CCP4 / 大きさ: 134.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.85 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_14167_msk_1.map emd_14167_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
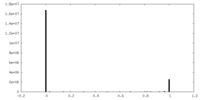
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_14167_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
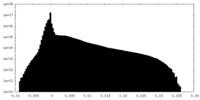
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_14167_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
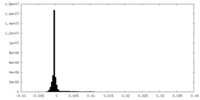
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : uperin 3.5
| 全体 | 名称: uperin 3.5 |
|---|---|
| 要素 |
|
-超分子 #1: uperin 3.5
| 超分子 | 名称: uperin 3.5 / タイプ: complex / キメラ: Yes / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種: Uperoleia mjobergii (カエル) |
| 分子量 | 理論値: 33.0 kDa/nm |
-分子 #1: Uperin-3.5
| 分子 | 名称: Uperin-3.5 / タイプ: protein_or_peptide / ID: 1 / コピー数: 27 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種: Uperoleia mjobergii (カエル) |
| 分子量 | 理論値: 1.782181 KDa |
| 配列 | 文字列: GVGDLIRKAV SVIKNIV(NH2) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 濃度 | 5 mg/mL |
|---|---|
| 緩衝液 | pH: 7 |
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / メッシュ: 300 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE-PROPANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV / 詳細: wait time 15s after application, blot time 4s. |
| 詳細 | Concentration refers to peptide monomer before fibrillation |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 11857 / 平均露光時間: 3.0 sec. / 平均電子線量: 40.0 e/Å2 / 詳細: Collected in movie-mode; 45 frames per exposure. |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 最大 デフォーカス(補正後): 3.1 µm 最小 デフォーカス(補正後): 0.35000000000000003 µm 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 105000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 詳細 | - Initial model building of a single helical layer using ChimeraX and Coot - Expansion to three layers, refinement in ISOLDE - Truncation of outer layers, re-expansion to three layers, refinement using phenix.real_space_refine |
|---|---|
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 59.34 / 当てはまり具合の基準: CC |
| 得られたモデル |  PDB-7qv5: |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X