+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EPty SPA at CSA of 1.03 mrad | |||||||||||||||
 マップデータ マップデータ | Cryo-EPty SPA 3D map reconstructed from 232 particles at convergence angle of 1.03 mrad | |||||||||||||||
 試料 試料 | Rotavirus A != Rotavirus Rotavirus A
| |||||||||||||||
 キーワード キーワード | Complex / VIRUS | |||||||||||||||
| 生物種 |  Rotavirus (ウイルス) Rotavirus (ウイルス) | |||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 37.2 Å | |||||||||||||||
 データ登録者 データ登録者 | Pei X / Wang P | |||||||||||||||
| 資金援助 |  中国, 中国,  英国, European Union, 4件 英国, European Union, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: Cryogenic electron ptychographic single particle analysis with wide bandwidth information transfer. 著者: Xudong Pei / Liqi Zhou / Chen Huang / Mark Boyce / Judy S Kim / Emanuela Liberti / Yiming Hu / Takeo Sasaki / Peter D Nellist / Peijun Zhang / David I Stuart / Angus I Kirkland / Peng Wang /    要旨: Advances in cryogenic transmission electron microscopy have revolutionised the determination of many macromolecular structures at atomic or near-atomic resolution. This method is based on ...Advances in cryogenic transmission electron microscopy have revolutionised the determination of many macromolecular structures at atomic or near-atomic resolution. This method is based on conventional defocused phase contrast imaging. However, it has limitations of weaker contrast for small biological molecules embedded in vitreous ice, in comparison with cryo-ptychography, which shows increased contrast. Here we report a single-particle analysis based on the use of ptychographic reconstruction data, demonstrating that three dimensional reconstructions with a wide information transfer bandwidth can be recovered by Fourier domain synthesis. Our work suggests future applications in otherwise challenging single particle analyses, including small macromolecules and heterogeneous or flexible particles. In addition structure determination in situ within cells without the requirement for protein purification and expression may be possible. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_35828.map.gz emd_35828.map.gz | 42.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-35828-v30.xml emd-35828-v30.xml emd-35828.xml emd-35828.xml | 14.7 KB 14.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_35828_fsc.xml emd_35828_fsc.xml | 11.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_35828.png emd_35828.png | 106.6 KB | ||
| その他 |  emd_35828_half_map_1.map.gz emd_35828_half_map_1.map.gz emd_35828_half_map_2.map.gz emd_35828_half_map_2.map.gz | 44.7 MB 44.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-35828 http://ftp.pdbj.org/pub/emdb/structures/EMD-35828 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35828 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-35828 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_35828_validation.pdf.gz emd_35828_validation.pdf.gz | 875.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_35828_full_validation.pdf.gz emd_35828_full_validation.pdf.gz | 875.2 KB | 表示 | |
| XML形式データ |  emd_35828_validation.xml.gz emd_35828_validation.xml.gz | 14 KB | 表示 | |
| CIF形式データ |  emd_35828_validation.cif.gz emd_35828_validation.cif.gz | 20.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35828 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35828 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35828 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-35828 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_35828.map.gz / 形式: CCP4 / 大きさ: 58.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_35828.map.gz / 形式: CCP4 / 大きさ: 58.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EPty SPA 3D map reconstructed from 232 particles at convergence angle of 1.03 mrad | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 4.65 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_35828_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
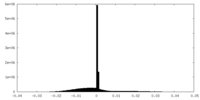
| 投影像・断面図 |
| ||||||||||||
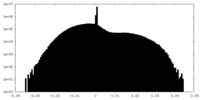
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_35828_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
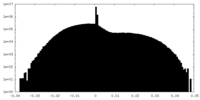
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Rotavirus A
| 全体 | 名称:  Rotavirus A (ロタウイルス A) Rotavirus A (ロタウイルス A) |
|---|---|
| 要素 |
|
-超分子 #1: Rotavirus
| 超分子 | 名称: Rotavirus / タイプ: virus / ID: 1 / 親要素: 0 / NCBI-ID: 10912 / 生物種: Rotavirus / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: STRAIN / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No |
|---|
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 8 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| グリッド | モデル: Quantifoil |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 80 % / チャンバー内温度: 298 K / 装置: GATAN CRYOPLUNGE 3 |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL CRYO ARM 300 |
|---|---|
| 撮影 | フィルム・検出器のモデル: OTHER / 平均電子線量: 22.6 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER / 最大 デフォーカス(公称値): 14.0 µm / 最小 デフォーカス(公称値): 13.5 µm |
 ムービー
ムービー コントローラー
コントローラー






 Z
Z Y
Y X
X