[日本語] English
 万見
万見- EMDB-15214: Endogenous yeast L-A helper virus identified from native cell extracts -
+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Endogenous yeast L-A helper virus identified from native cell extracts | ||||||||||||||||||
 マップデータ マップデータ | Icosahedrally averaged capsid of the L-A helper virus from native Saccharomyces cerevisiae cell extract | ||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | Capsid structure ScVLA / viral particle / wildtype / endogenous / VIRUS | ||||||||||||||||||
| 生物種 |  Saccharomyces cerevisiae virus L-A (ウイルス) Saccharomyces cerevisiae virus L-A (ウイルス) | ||||||||||||||||||
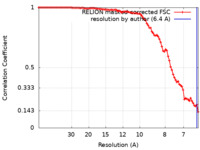
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.4 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Schmidt L / Kyrilis F / Hamdi F / Semchonok DA / Kastritis PL | ||||||||||||||||||
| 資金援助 |  ドイツ, European Union, 5件 ドイツ, European Union, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Commun Biol / 年: 2024 ジャーナル: Commun Biol / 年: 2024タイトル: Delineating organizational principles of the endogenous L-A virus by cryo-EM and computational analysis of native cell extracts. 著者: Lisa Schmidt / Christian Tüting / Fotis L Kyrilis / Farzad Hamdi / Dmitry A Semchonok / Gerd Hause / Annette Meister / Christian Ihling / Milton T Stubbs / Andrea Sinz / Panagiotis L Kastritis /   要旨: The high abundance of most viruses in infected host cells benefits their structural characterization. However, endogenous viruses are present in low copy numbers and are therefore challenging to ...The high abundance of most viruses in infected host cells benefits their structural characterization. However, endogenous viruses are present in low copy numbers and are therefore challenging to investigate. Here, we retrieve cell extracts enriched with an endogenous virus, the yeast L-A virus. The determined cryo-EM structure discloses capsid-stabilizing cation-π stacking, widespread across viruses and within the Totiviridae, and an interplay of non-covalent interactions from ten distinct capsomere interfaces. The capsid-embedded mRNA decapping active site trench is supported by a constricting movement of two flexible opposite-facing loops. tRNA-loaded polysomes and other biomacromolecules, presumably mRNA, are found in virus proximity within the cell extract. Mature viruses participate in larger viral communities resembling their rare in-cell equivalents in terms of size, composition, and inter-virus distances. Our results collectively describe a 3D-architecture of a viral milieu, opening the door to cell-extract-based high-resolution structural virology. #1:  ジャーナル: Biorxiv / 年: 2022 ジャーナル: Biorxiv / 年: 2022タイトル: Delineating organizational principles of the endogenous L-A virus by cryo-EM and computational analysis of native cell extracts 著者: Schmidt L / Tuting C / Kyrilis FL / Hamdi F / Semchonok DA / Hause G / Meister A / Ihling C / Shah PNM / Stubbs MT / Sinz A / Stuart DI / Kastritis PL | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_15214.map.gz emd_15214.map.gz | 59.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-15214-v30.xml emd-15214-v30.xml emd-15214.xml emd-15214.xml | 21.1 KB 21.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_15214_fsc.xml emd_15214_fsc.xml | 9.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_15214.png emd_15214.png | 77.5 KB | ||
| マスクデータ |  emd_15214_msk_1.map emd_15214_msk_1.map | 64 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-15214.cif.gz emd-15214.cif.gz | 5 KB | ||
| その他 |  emd_15214_additional_1.map.gz emd_15214_additional_1.map.gz emd_15214_half_map_1.map.gz emd_15214_half_map_1.map.gz emd_15214_half_map_2.map.gz emd_15214_half_map_2.map.gz | 40.3 MB 48.5 MB 48.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-15214 http://ftp.pdbj.org/pub/emdb/structures/EMD-15214 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15214 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-15214 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_15214_validation.pdf.gz emd_15214_validation.pdf.gz | 648.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_15214_full_validation.pdf.gz emd_15214_full_validation.pdf.gz | 648.2 KB | 表示 | |
| XML形式データ |  emd_15214_validation.xml.gz emd_15214_validation.xml.gz | 15.9 KB | 表示 | |
| CIF形式データ |  emd_15214_validation.cif.gz emd_15214_validation.cif.gz | 21.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15214 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15214 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15214 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-15214 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_15214.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_15214.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Icosahedrally averaged capsid of the L-A helper virus from native Saccharomyces cerevisiae cell extract | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 3.177 Å | ||||||||||||||||||||||||||||||||||||
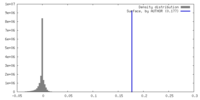
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_15214_msk_1.map emd_15214_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
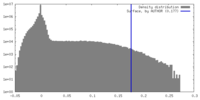
| 密度ヒストグラム |
-追加マップ: Asymmetrically reconstructed inner density of the L-A helper...
| ファイル | emd_15214_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Asymmetrically reconstructed inner density of the L-A helper virus revealing location of viral RNA | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
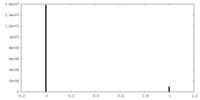
| 密度ヒストグラム |
-ハーフマップ: Icosahedrally averaged capsid of the L-A helper virus...
| ファイル | emd_15214_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Icosahedrally averaged capsid of the L-A helper virus from native Saccharomyces cerevisiae cell extract - Half Map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: Icosahedrally averaged capsid of the L-A helper virus...
| ファイル | emd_15214_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Icosahedrally averaged capsid of the L-A helper virus from native Saccharomyces cerevisiae cell extract - Half Map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
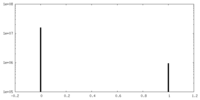
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Saccharomyces cerevisiae virus L-A
| 全体 | 名称:  Saccharomyces cerevisiae virus L-A (ウイルス) Saccharomyces cerevisiae virus L-A (ウイルス) |
|---|---|
| 要素 |
|
-超分子 #1: Saccharomyces cerevisiae virus L-A
| 超分子 | 名称: Saccharomyces cerevisiae virus L-A / タイプ: virus / ID: 1 / 親要素: 0 / 含まれる分子: #1 / NCBI-ID: 11008 / 生物種: Saccharomyces cerevisiae virus L-A / ウイルスタイプ: VIRUS-LIKE PARTICLE / ウイルス・単離状態: SPECIES / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 / 構成要素 - 濃度: 200.0 mM / 構成要素 - 式: CH3COONH4 / 構成要素 - 名称: Ammoniumacetate 詳細: pH of the buffer was adjusted with NaOH buffer was filtered and sonicated |
| グリッド | モデル: Quantifoil R2/1 / 材質: COPPER / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 15 sec. / 前処理 - 雰囲気: AIR / 前処理 - 気圧: 0.04 kPa |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277.15 K / 装置: FEI VITROBOT MARK IV / 詳細: blot force 2 and blot time 6 before plunging. |
| 詳細 | heterogenous cell extract |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS GLACIOS |
|---|---|
| 温度 | 最低: 77.0 K / 最高: 118.0 K |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / デジタル化 - サイズ - 横: 4096 pixel / デジタル化 - サイズ - 縦: 4096 pixel / 撮影したグリッド数: 7 / 実像数: 10067 / 平均露光時間: 3.61 sec. / 平均電子線量: 30.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 倍率(補正後): 44067 / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 45000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)