| 登録情報 | データベース: PDB / ID: 8b43
|
|---|
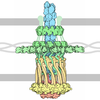
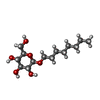
| タイトル | Crystal structure of ferrioxamine transporter |
|---|
 要素 要素 | Metal-pseudopaline receptor CntO |
|---|
 キーワード キーワード | MEMBRANE PROTEIN / Siderophore TonB-dependent transporter Pseudomonas aeruginosa Iron |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
nickel cation transport / siderophore-iron import into cell / zinc ion transport / siderophore uptake transmembrane transporter activity / siderophore transport / outer membrane / cell outer membrane / signaling receptor activity / cell surface receptor signaling pathway類似検索 - 分子機能 Secretin/TonB, short N-terminal domain / Secretin and TonB N terminus short domain / TonB-dependent siderophore receptor / TonB-dependent receptor-like, beta-barrel / TonB dependent receptor-like, beta-barrel / TonB-dependent receptor (TBDR) proteins profile. / Vitamin B12 transporter BtuB-like / TonB-dependent receptor, plug domain superfamily / TonB-dependent receptor, plug domain / TonB-dependent Receptor Plug Domain / TonB-dependent receptor-like, beta-barrel domain superfamily類似検索 - ドメイン・相同性 : / Chem-OX8 / Metal-pseudopaline receptor CntO類似検索 - 構成要素 |
|---|
| 生物種 |   Pseudomonas aeruginosa (緑膿菌) Pseudomonas aeruginosa (緑膿菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.49 Å 分子置換 / 解像度: 2.49 Å |
|---|
 データ登録者 データ登録者 | Josts, I. / Tidow, H. |
|---|
| 資金援助 |  ドイツ, 1件 ドイツ, 1件 | 組織 | 認可番号 | 国 |
|---|
| German Research Foundation (DFG) | |  ドイツ ドイツ |
|
|---|
 引用 引用 |  ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2023 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2023
タイトル: Interactions of TonB-dependent transporter FoxA with siderophores and antibiotics that affect binding, uptake, and signal transduction.
著者: Chan, D.C.K. / Josts, I. / Koteva, K. / Wright, G.D. / Tidow, H. / Burrows, L.L. |
|---|
| 履歴 | | 登録 | 2022年9月19日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2023年4月26日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2024年2月7日 | Group: Data collection / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond / pdbx_initial_refinement_model |
|---|
| 改定 1.2 | 2024年11月13日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature
Item: _pdbx_entry_details.has_protein_modification |
|---|
| 改定 1.3 | 2026年1月21日 | Group: Database references / Source and taxonomy / Structure summary
カテゴリ: entity / entity_name_com ...entity / entity_name_com / entity_src_gen / struct_ref / struct_ref_seq
Item: _entity.pdbx_description / _entity_src_gen.pdbx_gene_src_gene ..._entity.pdbx_description / _entity_src_gen.pdbx_gene_src_gene / _struct_ref.db_code / _struct_ref.pdbx_db_accession / _struct_ref_seq.pdbx_db_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.49 Å
分子置換 / 解像度: 2.49 Å  データ登録者
データ登録者 ドイツ, 1件
ドイツ, 1件  引用
引用 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2023
ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2023 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 8b43.cif.gz
8b43.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb8b43.ent.gz
pdb8b43.ent.gz PDB形式
PDB形式 8b43.json.gz
8b43.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/b4/8b43
https://data.pdbj.org/pub/pdb/validation_reports/b4/8b43 ftp://data.pdbj.org/pub/pdb/validation_reports/b4/8b43
ftp://data.pdbj.org/pub/pdb/validation_reports/b4/8b43
 F&H 検索
F&H 検索 リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  PETRA III, EMBL c/o DESY
PETRA III, EMBL c/o DESY  / ビームライン: P13 (MX1) / 波長: 0.976 Å
/ ビームライン: P13 (MX1) / 波長: 0.976 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



 PDBj
PDBj