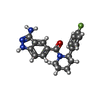
登録情報 データベース : PDB / ID : 5idpタイトル CDK8-CYCC IN COMPLEX WITH (3-Amino-1H-indazol-5-yl)-[(S)-2-(4-fluoro-phenyl)-piperidin-1-yl]-methanone Cyclin-C Cyclin-dependent kinase 8 キーワード / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト)手法 / / / 解像度 : 2.65 Å データ登録者 Musil, D. / Blagg, J. / Mallinger, A. / Czodrowski, P. / Schiemann, K. ジャーナル : J. Med. Chem. / 年 : 2016タイトル : Structure-Based Optimization of Potent, Selective, and Orally Bioavailable CDK8 Inhibitors Discovered by High-Throughput Screening.著者: Czodrowski, P. / Mallinger, A. / Wienke, D. / Esdar, C. / Poschke, O. / Busch, M. / Rohdich, F. / Eccles, S.A. / Ortiz-Ruiz, M.J. / Schneider, R. / Raynaud, F.I. / Clarke, P.A. / Musil, D. / ... 著者 : Czodrowski, P. / Mallinger, A. / Wienke, D. / Esdar, C. / Poschke, O. / Busch, M. / Rohdich, F. / Eccles, S.A. / Ortiz-Ruiz, M.J. / Schneider, R. / Raynaud, F.I. / Clarke, P.A. / Musil, D. / Schwarz, D. / Dale, T. / Urbahns, K. / Blagg, J. / Schiemann, K. 履歴 登録 2016年2月24日 登録サイト / 処理サイト 改定 1.0 2016年12月21日 Provider / タイプ 改定 1.1 2024年1月10日 Group / Database references / Refinement descriptionカテゴリ chem_comp_atom / chem_comp_bond ... chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model Item / _database_2.pdbx_database_accession
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  フーリエ合成 / 解像度: 2.65 Å
フーリエ合成 / 解像度: 2.65 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J. Med. Chem. / 年: 2016
ジャーナル: J. Med. Chem. / 年: 2016 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5idp.cif.gz
5idp.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5idp.ent.gz
pdb5idp.ent.gz PDB形式
PDB形式 5idp.json.gz
5idp.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/id/5idp
https://data.pdbj.org/pub/pdb/validation_reports/id/5idp ftp://data.pdbj.org/pub/pdb/validation_reports/id/5idp
ftp://data.pdbj.org/pub/pdb/validation_reports/id/5idp リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: CDK8
Homo sapiens (ヒト) / 遺伝子: CDK8
 Homo sapiens (ヒト) / 遺伝子: CCNC
Homo sapiens (ヒト) / 遺伝子: CCNC
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SLS
SLS  / ビームライン: X06SA / 波長: 1 Å
/ ビームライン: X06SA / 波長: 1 Å 解析
解析 フーリエ合成
フーリエ合成 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj