| 登録情報 | データベース: PDB / ID: 5cc3
|
|---|
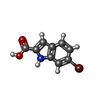
| タイトル | Crystal structure of Mycobacterium tuberculosis malate synthase in complex with 6-bromo-1H-indole-2-carboxylic acid |
|---|
 要素 要素 | Malate synthase G |
|---|
 キーワード キーワード | TRANSFERASE / Complex / Fragment |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
host cell extracellular matrix binding / capsule / malate synthase / malate synthase activity / glyoxylate catabolic process / coenzyme A binding / adhesion of symbiont to host / coenzyme A metabolic process / glyoxylate cycle / fibronectin binding ...host cell extracellular matrix binding / capsule / malate synthase / malate synthase activity / glyoxylate catabolic process / coenzyme A binding / adhesion of symbiont to host / coenzyme A metabolic process / glyoxylate cycle / fibronectin binding / laminin binding / tricarboxylic acid cycle / peptidoglycan-based cell wall / magnesium ion binding / cell surface / protein homodimerization activity / extracellular region / plasma membrane / cytosol / cytoplasm類似検索 - 分子機能 Malate synthase G / : / Malate synthase G, alpha-beta insertion domain / Malate synthase, domain III / Malate synthase, domain 3 / Malate Synthase G; Chain: A; Domain 4 / Malate synthase / Malate synthase superfamily / Malate synthase, C-terminal superfamily / Malate synthase, N-terminal and TIM-barrel domains ...Malate synthase G / : / Malate synthase G, alpha-beta insertion domain / Malate synthase, domain III / Malate synthase, domain 3 / Malate Synthase G; Chain: A; Domain 4 / Malate synthase / Malate synthase superfamily / Malate synthase, C-terminal superfamily / Malate synthase, N-terminal and TIM-barrel domains / : / : / Malate synthase, TIM barrel domain / Malate synthase, N-terminal domain / Malate synthase, C-terminal / TIM Barrel / Alpha-Beta Barrel / Up-down Bundle / Mainly Alpha / Alpha Beta類似検索 - ドメイン・相同性 6-bromanyl-1H-indole-2-carboxylic acid / Malate synthase G類似検索 - 構成要素 |
|---|
| 生物種 |   Mycobacterium tuberculosis (結核菌) Mycobacterium tuberculosis (結核菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.204 Å 分子置換 / 解像度: 2.204 Å |
|---|
 データ登録者 データ登録者 | Huang, H.-L. / Sacchettini, J.C. |
|---|
| 資金援助 |  米国, 1件 米国, 1件 | 組織 | 認可番号 | 国 |
|---|
| Bill & Melinda Gates Foundation | OPP1024055 |  米国 米国 |
|
|---|
 引用 引用 | #2:  ジャーナル: Chem.Biol. / 年: 2012タイトル ジャーナル: Chem.Biol. / 年: 2012タイトル: Structure-guided discovery of phenyl-diketo acids as potent inhibitors of M. tuberculosis malate synthase. 著者: Krieger, I.V. / Freundlich, J.S. / Gawandi, V.B. / Roberts, J.P. / Gawandi, V.B. / Sun, Q. / Owen, J.L. / Fraile, M.T. / Huss, S.I. / Lavandera, J.L. / Ioerger, T.R. / Sacchettini, J.C. |
|---|
| 履歴 | | 登録 | 2015年7月1日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2016年8月10日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年9月27日 | Group: Author supporting evidence / Derived calculations / カテゴリ: pdbx_audit_support / pdbx_struct_oper_list
Item: _pdbx_audit_support.funding_organization / _pdbx_struct_oper_list.symmetry_operation |
|---|
| 改定 1.2 | 2023年9月27日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.204 Å
分子置換 / 解像度: 2.204 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: To Be Published
ジャーナル: To Be Published ジャーナル: J.Biol.Chem. / 年: 2003
ジャーナル: J.Biol.Chem. / 年: 2003 ジャーナル: Chem.Biol. / 年: 2012
ジャーナル: Chem.Biol. / 年: 2012 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5cc3.cif.gz
5cc3.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5cc3.ent.gz
pdb5cc3.ent.gz PDB形式
PDB形式 5cc3.json.gz
5cc3.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5cc3_validation.pdf.gz
5cc3_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5cc3_full_validation.pdf.gz
5cc3_full_validation.pdf.gz 5cc3_validation.xml.gz
5cc3_validation.xml.gz 5cc3_validation.cif.gz
5cc3_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/cc/5cc3
https://data.pdbj.org/pub/pdb/validation_reports/cc/5cc3 ftp://data.pdbj.org/pub/pdb/validation_reports/cc/5cc3
ftp://data.pdbj.org/pub/pdb/validation_reports/cc/5cc3 リンク
リンク 集合体
集合体
 要素
要素 Mycobacterium tuberculosis (strain ATCC 25618 / H37Rv) (結核菌)
Mycobacterium tuberculosis (strain ATCC 25618 / H37Rv) (結核菌)
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 23-ID-B / 波長: 0.987 Å
/ ビームライン: 23-ID-B / 波長: 0.987 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



















 PDBj
PDBj