+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of GATA4 in complex with ALBN1 nucleosome | |||||||||
 マップデータ マップデータ | main map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | nucleosome / pioneer transcription factors / DNA binding proteins / transcription / chromatin / NUCLEAR PROTEIN / NUCLEAR PROTEIN-DNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報atrial septum secundum morphogenesis / atrioventricular valve formation / transdifferentiation / embryonic heart tube anterior/posterior pattern specification / Formation of lateral plate mesoderm / intestinal epithelial cell differentiation / cardiac right ventricle morphogenesis / atrioventricular node development / co-SMAD binding / cell growth involved in cardiac muscle cell development ...atrial septum secundum morphogenesis / atrioventricular valve formation / transdifferentiation / embryonic heart tube anterior/posterior pattern specification / Formation of lateral plate mesoderm / intestinal epithelial cell differentiation / cardiac right ventricle morphogenesis / atrioventricular node development / co-SMAD binding / cell growth involved in cardiac muscle cell development / atrial septum morphogenesis / cardiac muscle tissue regeneration / endocardial cushion development / Transcriptional regulation of testis differentiation / cardiac ventricle morphogenesis / Physiological factors / atrial septum primum morphogenesis / embryonic foregut morphogenesis / atrioventricular canal development / YAP1- and WWTR1 (TAZ)-stimulated gene expression / Synthesis, secretion, and inactivation of Glucose-dependent Insulinotropic Polypeptide (GIP) / endoderm development / Formation of definitive endoderm / positive regulation of BMP signaling pathway / response to vitamin A / regulation of cardiac muscle cell contraction / aortic valve morphogenesis / Cardiogenesis / ventricular septum development / negative regulation of cardiac muscle cell apoptotic process / DNA-binding transcription activator activity / cell fate commitment / detection of maltose stimulus / maltose transport complex / NFAT protein binding / heart looping / carbohydrate transport / protein localization to CENP-A containing chromatin / CENP-A containing nucleosome / negative regulation of apoptotic signaling pathway / carbohydrate transmembrane transporter activity / maltose binding / maltose transport / maltodextrin transmembrane transport / negative regulation of tumor necrosis factor-mediated signaling pathway / positive regulation of vascular endothelial growth factor production / Replacement of protamines by nucleosomes in the male pronucleus / arachidonate 15-lipoxygenase / arachidonate 15-lipoxygenase activity / Packaging Of Telomere Ends / lipoxygenase pathway / Recognition and association of DNA glycosylase with site containing an affected purine / Cleavage of the damaged purine / telomere organization / arachidonate metabolic process / Chromatin modifying enzymes / lipid oxidation / Deposition of new CENPA-containing nucleosomes at the centromere / ATP-binding cassette (ABC) transporter complex, substrate-binding subunit-containing / negative regulation of oxidative stress-induced intrinsic apoptotic signaling pathway / hepoxilin biosynthetic process / Recognition and association of DNA glycosylase with site containing an affected pyrimidine / Cleavage of the damaged pyrimidine / response to mechanical stimulus / linoleic acid metabolic process / Meiotic synapsis / Inhibition of DNA recombination at telomere / nucleosomal DNA binding / RNA Polymerase I Promoter Opening / Assembly of the ORC complex at the origin of replication / Interleukin-7 signaling / epigenetic regulation of gene expression / ATP-binding cassette (ABC) transporter complex / DNA methylation / negative regulation of autophagy / Condensation of Prophase Chromosomes / HCMV Late Events / SIRT1 negatively regulates rRNA expression / Chromatin modifications during the maternal to zygotic transition (MZT) / ERCC6 (CSB) and EHMT2 (G9a) positively regulate rRNA expression / cell chemotaxis / PRC2 methylates histones and DNA / Defective pyroptosis / Meiotic recombination / innate immune response in mucosa / DNA Damage/Telomere Stress Induced Senescence / HDACs deacetylate histones / Nonhomologous End-Joining (NHEJ) / RNA Polymerase I Promoter Escape / Transcriptional regulation by small RNAs / lipopolysaccharide binding / Transcriptional regulation of granulopoiesis / cellular response to glucose stimulus / RNA polymerase II transcription regulatory region sequence-specific DNA binding / HDMs demethylate histones / Formation of the beta-catenin:TCF transactivating complex / HCMV Early Events / RUNX1 regulates genes involved in megakaryocyte differentiation and platelet function / G2/M DNA damage checkpoint / wound healing 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / synthetic construct (人工物) Homo sapiens (ヒト) / synthetic construct (人工物) | |||||||||
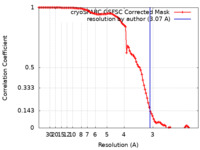
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.07 Å | |||||||||
 データ登録者 データ登録者 | Zhou BR / Bai Y | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol.Cell / 年: 2024 ジャーナル: Mol.Cell / 年: 2024タイトル: Cryo-EM structure of GATA4 in complex with ALBN1 nucleosome 著者: Zhou BR / Bai Y | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_43196.map.gz emd_43196.map.gz | 53.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-43196-v30.xml emd-43196-v30.xml emd-43196.xml emd-43196.xml | 21.5 KB 21.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_43196_fsc.xml emd_43196_fsc.xml | 9.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_43196.png emd_43196.png | 156.4 KB | ||
| Filedesc metadata |  emd-43196.cif.gz emd-43196.cif.gz | 6.8 KB | ||
| その他 |  emd_43196_half_map_1.map.gz emd_43196_half_map_1.map.gz emd_43196_half_map_2.map.gz emd_43196_half_map_2.map.gz | 95.6 MB 95.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-43196 http://ftp.pdbj.org/pub/emdb/structures/EMD-43196 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43196 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43196 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_43196_validation.pdf.gz emd_43196_validation.pdf.gz | 926 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_43196_full_validation.pdf.gz emd_43196_full_validation.pdf.gz | 925.6 KB | 表示 | |
| XML形式データ |  emd_43196_validation.xml.gz emd_43196_validation.xml.gz | 18.4 KB | 表示 | |
| CIF形式データ |  emd_43196_validation.cif.gz emd_43196_validation.cif.gz | 23.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43196 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43196 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43196 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-43196 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8vg0MC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_43196.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_43196.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | main map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.056 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: half map 1
| ファイル | emd_43196_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: half map 2
| ファイル | emd_43196_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : GATA4 in complex with 186bp ALBN1 nucleosome
| 全体 | 名称: GATA4 in complex with 186bp ALBN1 nucleosome |
|---|---|
| 要素 |
|
-超分子 #1: GATA4 in complex with 186bp ALBN1 nucleosome
| 超分子 | 名称: GATA4 in complex with 186bp ALBN1 nucleosome / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#7 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: DNA (159-MER)
| 分子 | 名称: DNA (159-MER) / タイプ: dna / ID: 1 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 57.399637 KDa |
| 配列 | 文字列: (DA)(DT)(DC)(DC)(DG)(DA)(DG)(DA)(DT)(DG) (DG)(DT)(DA)(DC)(DT)(DT)(DT)(DG)(DT)(DG) (DT)(DC)(DT)(DC)(DC)(DT)(DG)(DC)(DT) (DC)(DT)(DG)(DT)(DC)(DA)(DG)(DC)(DA)(DG) (DG) (DG)(DC)(DA)(DC)(DT) ...文字列: (DA)(DT)(DC)(DC)(DG)(DA)(DG)(DA)(DT)(DG) (DG)(DT)(DA)(DC)(DT)(DT)(DT)(DG)(DT)(DG) (DT)(DC)(DT)(DC)(DC)(DT)(DG)(DC)(DT) (DC)(DT)(DG)(DT)(DC)(DA)(DG)(DC)(DA)(DG) (DG) (DG)(DC)(DA)(DC)(DT)(DG)(DT)(DA) (DC)(DT)(DT)(DG)(DC)(DT)(DG)(DA)(DT)(DA) (DC)(DC) (DA)(DG)(DG)(DG)(DA)(DA)(DT) (DG)(DT)(DT)(DT)(DG)(DT)(DT)(DC)(DT)(DT) (DA)(DA)(DA) (DT)(DA)(DC)(DC)(DA)(DT) (DC)(DA)(DT)(DT)(DC)(DC)(DG)(DG)(DA)(DC) (DG)(DT)(DG)(DT) (DT)(DT)(DG)(DC)(DC) (DT)(DT)(DG)(DG)(DC)(DC)(DA)(DG)(DT)(DT) (DT)(DT)(DC)(DC)(DA) (DT)(DG)(DT)(DA) (DC)(DA)(DT)(DG)(DC)(DA)(DG)(DA)(DA)(DA) (DG)(DA)(DA)(DG)(DT)(DT) (DT)(DG)(DG) (DA)(DC)(DT)(DG)(DA)(DT)(DC)(DA)(DA)(DT) (DA)(DC)(DA)(DG)(DT)(DC)(DC) (DT)(DC) (DT)(DG)(DC)(DC)(DT)(DT)(DT)(DA)(DA)(DA) (DG)(DC)(DA)(DA)(DT)(DA)(DG)(DG) (DA) (DA)(DA)(DG)(DA)(DT) |
-分子 #2: DNA (159-MER)
| 分子 | 名称: DNA (159-MER) / タイプ: dna / ID: 2 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 57.42777 KDa |
| 配列 | 文字列: (DA)(DT)(DC)(DT)(DT)(DT)(DC)(DC)(DT)(DA) (DT)(DT)(DG)(DC)(DT)(DT)(DT)(DA)(DA)(DA) (DG)(DG)(DC)(DA)(DG)(DA)(DG)(DG)(DA) (DC)(DT)(DG)(DT)(DA)(DT)(DT)(DG)(DA)(DT) (DC) (DA)(DG)(DT)(DC)(DC) ...文字列: (DA)(DT)(DC)(DT)(DT)(DT)(DC)(DC)(DT)(DA) (DT)(DT)(DG)(DC)(DT)(DT)(DT)(DA)(DA)(DA) (DG)(DG)(DC)(DA)(DG)(DA)(DG)(DG)(DA) (DC)(DT)(DG)(DT)(DA)(DT)(DT)(DG)(DA)(DT) (DC) (DA)(DG)(DT)(DC)(DC)(DA)(DA)(DA) (DC)(DT)(DT)(DC)(DT)(DT)(DT)(DC)(DT)(DG) (DC)(DA) (DT)(DG)(DT)(DA)(DC)(DA)(DT) (DG)(DG)(DA)(DA)(DA)(DA)(DC)(DT)(DG)(DG) (DC)(DC)(DA) (DA)(DG)(DG)(DC)(DA)(DA) (DA)(DC)(DA)(DC)(DG)(DT)(DC)(DC)(DG)(DG) (DA)(DA)(DT)(DG) (DA)(DT)(DG)(DG)(DT) (DA)(DT)(DT)(DT)(DA)(DA)(DG)(DA)(DA)(DC) (DA)(DA)(DA)(DC)(DA) (DT)(DT)(DC)(DC) (DC)(DT)(DG)(DG)(DT)(DA)(DT)(DC)(DA)(DG) (DC)(DA)(DA)(DG)(DT)(DA) (DC)(DA)(DG) (DT)(DG)(DC)(DC)(DC)(DT)(DG)(DC)(DT)(DG) (DA)(DC)(DA)(DG)(DA)(DG)(DC) (DA)(DG) (DG)(DA)(DG)(DA)(DC)(DA)(DC)(DA)(DA)(DA) (DG)(DT)(DA)(DC)(DC)(DA)(DT)(DC) (DT) (DC)(DG)(DG)(DA)(DT) |
-分子 #3: Histone H3.1
| 分子 | 名称: Histone H3.1 / タイプ: protein_or_peptide / ID: 3 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 15.437167 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MARTKQTARK STGGKAPRKQ LATKAARKSA PATGGVKKPH RYRPGTVALR EIRRYQKSTE LLIRKLPFQR LVREIAQDFK TDLRFQSSA VMALQEACEA YLVGLFEDTN LCAIHAKRVT IMPKDIQLAR RIRGERA UniProtKB: Histone H3.1 |
-分子 #4: Histone H4
| 分子 | 名称: Histone H4 / タイプ: protein_or_peptide / ID: 4 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 11.394426 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSGRGKGGKG LGKGGAKRHR KVLRDNIQGI TKPAIRRLAR RGGVKRISGL IYEETRGVLK VFLENVIRDA VTYTEHAKRK TVTAMDVVY ALKRQGRTLY GFGG UniProtKB: Arachidonate 15-lipoxygenase |
-分子 #5: Histone H2A type 1-B/E
| 分子 | 名称: Histone H2A type 1-B/E / タイプ: protein_or_peptide / ID: 5 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 14.165551 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSGRGKQGGK ARAKAKTRSS RAGLQFPVGR VHRLLRKGNY SERVGAGAPV YLAAVLEYLT AEILELAGNA ARDNKKTRII PRHLQLAIR NDEELNKLLG RVTIAQGGVL PNIQAVLLPK KTESHHKAKG K UniProtKB: Histone H2A type 1-B/E |
-分子 #6: Histone H2B type 1-J
| 分子 | 名称: Histone H2B type 1-J / タイプ: protein_or_peptide / ID: 6 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 13.935239 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MPEPAKSAPA PKKGSKKAVT KAQKKDGKKR KRSRKESYSI YVYKVLKQVH PDTGISSKAM GIMNSFVNDI FERIAGEASR LAHYNKRST ITSREIQTAV RLLLPGELAK HAVSEGTKAV TKYTSAK UniProtKB: Histone H2B type 1-J |
-分子 #7: Maltose/maltodextrin-binding periplasmic protein,Transcription fa...
| 分子 | 名称: Maltose/maltodextrin-binding periplasmic protein,Transcription factor GATA-4 タイプ: protein_or_peptide / ID: 7 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 87.880258 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGSSHHHHHH GSSMKIEEGK LVIWINGDKG YNGLAEVGKK FEKDTGIKVT VEHPDKLEEK FPQVAATGDG PDIIFWAHDR FGGYAQSGL LAEITPDKAF QDKLYPFTWD AVRYNGKLIA YPIAVEALSL IYNKDLLPNP PKTWEEIPAL DKELKAKGKS A LMFNLQEP ...文字列: MGSSHHHHHH GSSMKIEEGK LVIWINGDKG YNGLAEVGKK FEKDTGIKVT VEHPDKLEEK FPQVAATGDG PDIIFWAHDR FGGYAQSGL LAEITPDKAF QDKLYPFTWD AVRYNGKLIA YPIAVEALSL IYNKDLLPNP PKTWEEIPAL DKELKAKGKS A LMFNLQEP YFTWPLIAAD GGYAFKYENG KYDIKDVGVD NAGAKAGLTF LVDLIKNKHM NADTDYSIAE AAFNKGETAM TI NGPWAWS NIDTSKVNYG VTVLPTFKGQ PSKPFVGVLS AGINAASPNK ELAKEFLENY LLTDEGLEAV NKDKPLGAVA LKS YEEELA KDPRIAATME NAQKGEIMPN IPQMSAFWYA VRTAVINAAS GRQTVDEALK DAQTNGIEEN LYFQSNAMYQ SLAM AANHG PPPGAYEAGG PGAFMHGAGA ASSPVYVPTP RVPSSVLGLS YLQGGGAGSA SGGASGGSSG GAASGAGPGT QQGSP GWSQ AGADGAAYTP PPVSPRFSFP GTTGSLAAAA AAAAAREAAA YSSGGGAAGA GLAGREQYGR AGFAGSYSSP YPAYMA DVG ASWAAAAAAS AGPFDSPVLH SLPGRANPAA RHPNLDMFDD FSEGRECVNC GAMSTPLWRR DGTGHYLCNA CGLYHKM NG INRPLIKPQR RLSASRRVGL SCANCQTTTT TLWRRNAEGE PVCNACGLYM KLHGVPRPLA MRKEGIQTRK RKPKNLNK S KTPAAPSGSE SLPPASGASS NSSNATTSSS EEMRPIKTEP GLSSHYGHSS SVSQTFSVSA MSGHGPSIHP VLSALKLSP QGYASPVSQS PQTSSKQDSW NSLVLADSHG DIITA UniProtKB: Maltose/maltodextrin-binding periplasmic protein, Transcription factor GATA-4 |
-分子 #8: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 8 / コピー数: 1 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 1.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: OTHER / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z
Z Y
Y X
X