+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of E3 ubiquitin ligase Doa10 from Saccharomyces cerevisiae | |||||||||
 マップデータ マップデータ | Sharpened map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | ubiquitin / ERAD / protein quality control / membrane protein / LIGASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Doa10p ubiquitin ligase complex / nuclear inner membrane / retrograde protein transport, ER to cytosol / ERAD pathway / RING-type E3 ubiquitin transferase / ubiquitin-protein transferase activity / nuclear envelope / ubiquitin protein ligase activity / protein ubiquitination / endoplasmic reticulum membrane ...Doa10p ubiquitin ligase complex / nuclear inner membrane / retrograde protein transport, ER to cytosol / ERAD pathway / RING-type E3 ubiquitin transferase / ubiquitin-protein transferase activity / nuclear envelope / ubiquitin protein ligase activity / protein ubiquitination / endoplasmic reticulum membrane / endoplasmic reticulum / zinc ion binding / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
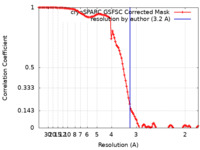
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Park E / Itskanov SI | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Substrate recognition mechanism of the endoplasmic reticulum-associated ubiquitin ligase Doa10. 著者: Kevin Wu / Samuel Itskanov / Diane L Lynch / Yuanyuan Chen / Aasha Turner / James C Gumbart / Eunyong Park /  要旨: Doa10 (MARCHF6 in metazoans) is a large polytopic membrane-embedded E3 ubiquitin ligase in the endoplasmic reticulum (ER) that plays an important role in quality control of cytosolic and ER proteins. ...Doa10 (MARCHF6 in metazoans) is a large polytopic membrane-embedded E3 ubiquitin ligase in the endoplasmic reticulum (ER) that plays an important role in quality control of cytosolic and ER proteins. Although Doa10 is highly conserved across eukaryotes, it is not understood how Doa10 recognizes its substrates. Here, we define the substrate recognition mechanism of Doa10 by structural and functional analyses on Saccharomyces cerevisiae Doa10 and its model substrates. Cryo-EM analysis shows that Doa10 has unusual architecture with a large lipid-filled central cavity, and its conserved middle domain forms an additional water-filled lateral tunnel open to the cytosol. Our biochemical data and molecular dynamics simulations suggest that the entrance of the substrate's degron peptide into the lateral tunnel is required for efficient polyubiquitination. The N- and C-terminal membrane domains of Doa10 seem to form fence-like features to restrict polyubiquitination to those proteins that can access the central cavity and lateral tunnel. Our study reveals how extended hydrophobic sequences at the termini of substrate proteins are recognized by Doa10 as a signal for quality control. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_41508.map.gz emd_41508.map.gz | 118.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-41508-v30.xml emd-41508-v30.xml emd-41508.xml emd-41508.xml | 20.4 KB 20.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_41508_fsc.xml emd_41508_fsc.xml | 11.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_41508.png emd_41508.png | 138.2 KB | ||
| Filedesc metadata |  emd-41508.cif.gz emd-41508.cif.gz | 6.6 KB | ||
| その他 |  emd_41508_additional_1.map.gz emd_41508_additional_1.map.gz emd_41508_half_map_1.map.gz emd_41508_half_map_1.map.gz emd_41508_half_map_2.map.gz emd_41508_half_map_2.map.gz | 62.3 MB 115.9 MB 115.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-41508 http://ftp.pdbj.org/pub/emdb/structures/EMD-41508 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41508 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-41508 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_41508_validation.pdf.gz emd_41508_validation.pdf.gz | 810.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_41508_full_validation.pdf.gz emd_41508_full_validation.pdf.gz | 810.3 KB | 表示 | |
| XML形式データ |  emd_41508_validation.xml.gz emd_41508_validation.xml.gz | 19 KB | 表示 | |
| CIF形式データ |  emd_41508_validation.cif.gz emd_41508_validation.cif.gz | 24.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41508 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41508 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41508 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-41508 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8tqmMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_41508.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_41508.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.91 Å | ||||||||||||||||||||
| 密度 |
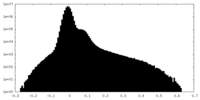
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Unsharpened map
| ファイル | emd_41508_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
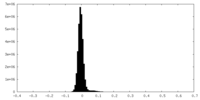
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_41508_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
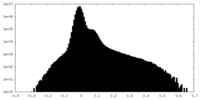
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_41508_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
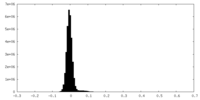
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : E3 ubiquitin ligase Doa10
| 全体 | 名称: E3 ubiquitin ligase Doa10 |
|---|---|
| 要素 |
|
-超分子 #1: E3 ubiquitin ligase Doa10
| 超分子 | 名称: E3 ubiquitin ligase Doa10 / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 151 KDa |
-分子 #1: ERAD-associated E3 ubiquitin-protein ligase DOA10
| 分子 | 名称: ERAD-associated E3 ubiquitin-protein ligase DOA10 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 151.608109 KDa |
| 配列 | 文字列: MDVDSDVNVS RLRDELHKVA NEETDTATFN DDAPSGATCR ICRGEATEDN PLFHPCKCRG SIKYMHESCL LEWVASKNID ISKPGADVK CDICHYPIQF KTIYAENMPE KIPFSLLLSK SILTFFEKAR LALTIGLAAV LYIIGVPLVW NMFGKLYTMM L DGSSPYPG ...文字列: MDVDSDVNVS RLRDELHKVA NEETDTATFN DDAPSGATCR ICRGEATEDN PLFHPCKCRG SIKYMHESCL LEWVASKNID ISKPGADVK CDICHYPIQF KTIYAENMPE KIPFSLLLSK SILTFFEKAR LALTIGLAAV LYIIGVPLVW NMFGKLYTMM L DGSSPYPG DFLKSLIYGY DQSATPELTT RAIFYQLLQN HSFTSLQFIM IVILHIALYF QYDMIVREDV FSKMVFHKIG PR LSPKDLK SRLKERFPMM DDRMVEYLAR EMRAHDENRQ EQGHDRLNMP AAAADNNNNV INPRNDNVPP QDPNDHRNFE NLR HVDELD HDEATEEHEN NDSDNSLPSG DDSSRILPGS SSDNEEDEEA EGQQQQQQPE EEADYRDHIE PNPIDMWANR RAQN EFDDL IAAQQNAINR PNAPVFIPPP AQNRAGNVDQ DEQDFGAAVG VPPAQANPDD QGQGPLVINL KLKLLNVIAY FIIAV VFTA IYLAISYLFP TFIGFGLLKI YFGIFKVILR GLCHLYYLSG AHIAYNGLTK LVPKVDVAMS WISDHLIHDI IYLYNG YTE NTMKHSIFIR ALPALTTYLT SVSIVCASSN LVSRGYGREN GMSNPTRRLI FQILFALKCT FKVFTLFFIE LAGFPIL AG VMLDFSLFCP ILASNSRMLW VPSICAIWPP FSLFVYWTIG TLYMYWFAKY IGMIRKNIIR PGVLFFIRSP EDPNIKIL H DSLIHPMSIQ LSRLCLSMFI YAIFIVLGFG FHTRIFFPFM LKSNLLSVPE AYKPTSIISW KFNTILLTLY FTKRILESS SYVKPLLERY WKTIFKLCSR KLRLSSFILG KDTPTERGHI VYRNLFYKYI AAKNAEWSNQ ELFTKPKTLE QAEELFGQVR DVHAYFVPD GVLMRVPSSD IVSRNYVQTM FVPVTKDDKL LKPLDLERIK ERNKRAAGEF GYLDEQNTEY DQYYIVYVPP D FRLRYMTL LGLVWLFASI LMLGVTFISQ ALINFVCSFG FLPVVKLLLG ERNKVYVAWK ELSDISYSYL NIYYVCVGSV CL SKIAKDI LHFTEGQNTL DEHAVDENEV EEVEHDIPER DINNAPVNNI NNVEEGQGIF MAIFNSIFDS MLVKYNLMVF IAI MIAVIR TMVSWVVLTD GILACYNYLT IRVFGNSSYT IGNSKWFKYD ESLLFVVWII SSMVNFGTGY KSLKLFFRNR NTSK LNFLK TMALELFKQG FLHMVIYVLP IIILSLVFLR DVSTKQIIDI SHGSRSFTLS LNESFPTWTR MQDIYFGLLI ALESF TFFF QATVLFIQWF KSTVQNVKDE VYTKGRALEN LPDES UniProtKB: ERAD-associated E3 ubiquitin-protein ligase DOA10 |
-分子 #2: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE
| 分子 | 名称: 1,2-DIACYL-SN-GLYCERO-3-PHOSPHOCHOLINE / タイプ: ligand / ID: 2 / コピー数: 4 / 式: PC1 |
|---|---|
| 分子量 | 理論値: 790.145 Da |
| Chemical component information |  ChemComp-PC1: |
-分子 #3: TRISTEAROYLGLYCEROL
| 分子 | 名称: TRISTEAROYLGLYCEROL / タイプ: ligand / ID: 3 / コピー数: 1 / 式: TGL |
|---|---|
| 分子量 | 理論値: 891.48 Da |
| Chemical component information |  ChemComp-TGL: |
-分子 #4: CHOLESTEROL HEMISUCCINATE
| 分子 | 名称: CHOLESTEROL HEMISUCCINATE / タイプ: ligand / ID: 4 / コピー数: 1 / 式: Y01 |
|---|---|
| 分子量 | 理論値: 486.726 Da |
| Chemical component information |  ChemComp-Y01: |
-分子 #5: ERGOSTEROL
| 分子 | 名称: ERGOSTEROL / タイプ: ligand / ID: 5 / コピー数: 1 / 式: ERG |
|---|---|
| 分子量 | 理論値: 396.648 Da |
| Chemical component information |  ChemComp-ERG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7.5 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY ARRAY / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
| 詳細 | 20 mM Tris-HCl, pH 7.5, 100 mM NaCl, 1 mM EDTA, 2 mM DTT, 0.02% GDN |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.4 µm 最小 デフォーカス(公称値): 0.7000000000000001 µm 倍率(公称値): 64000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | Chain - Source name: Other / Chain - Initial model type: other / 詳細: de novo |
|---|---|
| 精密化 | プロトコル: AB INITIO MODEL |
| 得られたモデル |  PDB-8tqm: |
 ムービー
ムービー コントローラー
コントローラー




 Z
Z Y
Y X
X