+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, focused refinement of RBD region | ||||||||||||
 マップデータ マップデータ | |||||||||||||
 試料 試料 |
| ||||||||||||
 キーワード キーワード | Spike protein / Antibody Fab fragment / Complex / VIRAL PROTEIN/IMMUNE SYSTEM / VIRAL PROTEIN-IMMUNE SYSTEM complex | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / entry receptor-mediated virion attachment to host cell ...Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / entry receptor-mediated virion attachment to host cell / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / receptor-mediated endocytosis of virus by host cell / Attachment and Entry / membrane fusion / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / receptor ligand activity / symbiont-mediated suppression of host innate immune response / host cell surface receptor binding / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / SARS-CoV-2 activates/modulates innate and adaptive immune responses / host cell plasma membrane / virion membrane / identical protein binding / membrane / plasma membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.17 Å | ||||||||||||
 データ登録者 データ登録者 | Liu B / Gao X / Li Z / Chen Q / He J / Xiong X | ||||||||||||
| 資金援助 | 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2024 ジャーナル: Cell Rep / 年: 2024タイトル: An unconventional VH1-2 antibody tolerates escape mutations and shows an antigenic hotspot on SARS-CoV-2 spike. 著者: Banghui Liu / Xuefeng Niu / Yijun Deng / Zhaoyong Zhang / Yanqun Wang / Xijie Gao / Huan Liang / Zimu Li / Qian Wang / Yuanyi Cheng / Qiuluan Chen / Shuangshuang Huang / Yingxian Pan / ...著者: Banghui Liu / Xuefeng Niu / Yijun Deng / Zhaoyong Zhang / Yanqun Wang / Xijie Gao / Huan Liang / Zimu Li / Qian Wang / Yuanyi Cheng / Qiuluan Chen / Shuangshuang Huang / Yingxian Pan / Mengzhen Su / Xiancheng Lin / Chuanying Niu / Yinglin Chen / Wenyi Yang / Yudi Zhang / Qihong Yan / Jun He / Jincun Zhao / Ling Chen / Xiaoli Xiong /  要旨: The severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) spike (S) protein continues to evolve antigenically, impacting antibody immunity. D1F6, an affinity-matured non-stereotypic VH1-2 ...The severe acute respiratory syndrome coronavirus 2 (SARS-CoV-2) spike (S) protein continues to evolve antigenically, impacting antibody immunity. D1F6, an affinity-matured non-stereotypic VH1-2 antibody isolated from a patient infected with the SARS-CoV-2 ancestral strain, effectively neutralizes most Omicron variants tested, including XBB.1.5. We identify that D1F6 in the immunoglobulin G (IgG) form is able to overcome the effect of most Omicron mutations through its avidity-enhanced multivalent S-trimer binding. Cryo-electron microscopy (cryo-EM) and biochemical analyses show that three simultaneous epitope mutations are generally needed to substantially disrupt the multivalent S-trimer binding by D1F6 IgG. Antigenic mutations at spike positions 346, 444, and 445, which appeared in the latest variants, have little effect on D1F6 binding individually. However, these mutations are able to act synergistically with earlier Omicron mutations to impair neutralization by affecting the interaction between D1F6 IgG and the S-trimer. These results provide insight into the mechanism by which accumulated antigenic mutations facilitate evasion of affinity-matured antibodies. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_39919.map.gz emd_39919.map.gz | 95.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-39919-v30.xml emd-39919-v30.xml emd-39919.xml emd-39919.xml | 17.1 KB 17.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_39919.png emd_39919.png | 15.4 KB | ||
| Filedesc metadata |  emd-39919.cif.gz emd-39919.cif.gz | 5.7 KB | ||
| その他 |  emd_39919_half_map_1.map.gz emd_39919_half_map_1.map.gz emd_39919_half_map_2.map.gz emd_39919_half_map_2.map.gz | 95.6 MB 95.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-39919 http://ftp.pdbj.org/pub/emdb/structures/EMD-39919 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-39919 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-39919 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_39919_validation.pdf.gz emd_39919_validation.pdf.gz | 870.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_39919_full_validation.pdf.gz emd_39919_full_validation.pdf.gz | 869.9 KB | 表示 | |
| XML形式データ |  emd_39919_validation.xml.gz emd_39919_validation.xml.gz | 13 KB | 表示 | |
| CIF形式データ |  emd_39919_validation.cif.gz emd_39919_validation.cif.gz | 15.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-39919 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-39919 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-39919 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-39919 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8zc1MC  8zbyC  8zbzC  8zc0C  8zc2C  8zc3C  8zc4C  8zc5C  8zc6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_39919.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_39919.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.32 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_39919_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
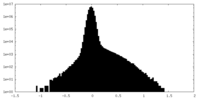
| 投影像・断面図 |
| ||||||||||||
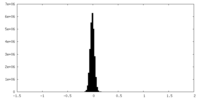
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_39919_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
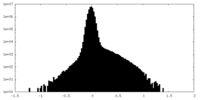
| 投影像・断面図 |
| ||||||||||||
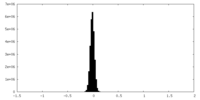
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fa...
| 全体 | 名称: SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, focused refinement of RBD region |
|---|---|
| 要素 |
|
-超分子 #1: SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fa...
| 超分子 | 名称: SARS-CoV-2 Omicron BA.2 spike trimer (6P) in complex with D1F6 Fab, focused refinement of RBD region タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Spike protein S1
| 分子 | 名称: Spike protein S1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  株: Omicron/BA.2 |
| 分子量 | 理論値: 22.153029 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ITNLCPFDEV FNATRFASVY AWNRKRISNC VADYSVLYNF APFFAFKCYG VSPTKLNDLC FTNVYADSFV IRGNEVSQIA PGQTGNIAD YNYKLPDDFT GCVIAWNSNK LDSKVGGNYN YLYRLFRKSN LKPFERDIST EIYQAGNKPC NGVAGFNCYF P LRSYGFRP ...文字列: ITNLCPFDEV FNATRFASVY AWNRKRISNC VADYSVLYNF APFFAFKCYG VSPTKLNDLC FTNVYADSFV IRGNEVSQIA PGQTGNIAD YNYKLPDDFT GCVIAWNSNK LDSKVGGNYN YLYRLFRKSN LKPFERDIST EIYQAGNKPC NGVAGFNCYF P LRSYGFRP TYGVGHQPYR VVVLSFELLH APATVCGP UniProtKB: Spike glycoprotein |
-分子 #2: Light chain of D1F6 Fab
| 分子 | 名称: Light chain of D1F6 Fab / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.62327 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QPVLTQPPSA SGPPGQSVSI SCSGSRSNIG TNFVYWYQQL PGAAPKLLIY KNDQRPSGVP ERFFGSKSGT SASLAISGLR SEDEVDYYC AAWDDSLSGH VFGAGTKVTV LGTKLTVLGQ PKAAPSVTLF PPSSEELQAN KATLVCLISD FYPGAVTVAW K ADSSPVKA ...文字列: QPVLTQPPSA SGPPGQSVSI SCSGSRSNIG TNFVYWYQQL PGAAPKLLIY KNDQRPSGVP ERFFGSKSGT SASLAISGLR SEDEVDYYC AAWDDSLSGH VFGAGTKVTV LGTKLTVLGQ PKAAPSVTLF PPSSEELQAN KATLVCLISD FYPGAVTVAW K ADSSPVKA GVETTTPSKQ SNNKYAASSY LSLTPEQWKS HRSYSCQVTH EGSTVEKTVA PTECS |
-分子 #3: Heavy chain of D1F6 Fab
| 分子 | 名称: Heavy chain of D1F6 Fab / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.752727 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVQSGAE VKKPGASVKV SCKASGYIFS DYNIHWVRQA PGQGLEWMGW ISPDSDDTNY AQSFQGRVTM TRDTSITTVY MELSSLRSD DTAVYFCARS VGYCSLNSCQ RWMWFDTWGQ GALVTVSSAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW ...文字列: EVQLVQSGAE VKKPGASVKV SCKASGYIFS DYNIHWVRQA PGQGLEWMGW ISPDSDDTNY AQSFQGRVTM TRDTSITTVY MELSSLRSD DTAVYFCARS VGYCSLNSCQ RWMWFDTWGQ GALVTVSSAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW NSGALTSGVH TFPAVLQSSG LYSLSSVVTV PSSSLGTQTY ICNVNHKPSN TKVDKKVEPK SC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 295 K |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.17 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 239007 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー
















 Z
Z Y
Y X
X