+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human urea transporter A2. | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Urea transporter / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報urea transport / Transport of bile salts and organic acids, metal ions and amine compounds / urea transmembrane transport / urea transmembrane transporter activity / cell adhesion molecule binding / transmembrane transport / apical plasma membrane / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /  Homo sapien (ヒト) Homo sapien (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.0 Å | |||||||||
 データ登録者 データ登録者 | Huang S / Liu L / Sun J | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Structural insights into the mechanisms of urea permeation and distinct inhibition modes of urea transporters. 著者: Shen-Ming Huang / Zhi-Zhen Huang / Lei Liu / Meng-Yao Xiong / Chao Zhang / Bo-Yang Cai / Ming-Wei Wang / Kui Cai / Ying-Li Jia / Jia-Le Wang / Ming-Hui Zhang / Yi-He Xie / Min Li / Hang Zhang ...著者: Shen-Ming Huang / Zhi-Zhen Huang / Lei Liu / Meng-Yao Xiong / Chao Zhang / Bo-Yang Cai / Ming-Wei Wang / Kui Cai / Ying-Li Jia / Jia-Le Wang / Ming-Hui Zhang / Yi-He Xie / Min Li / Hang Zhang / Cheng-Hao Weng / Xin Wen / Zhi Li / Ying Sun / Fan Yi / Zhao Yang / Peng Xiao / Fan Yang / Xiao Yu / Lu Tie / Bao-Xue Yang / Jin-Peng Sun /  要旨: Urea's transmembrane transport through urea transporters (UT) is a fundamental physiological behavior for life activities. Here, we present 11 cryo-EM structures of four UT members in resting states, ...Urea's transmembrane transport through urea transporters (UT) is a fundamental physiological behavior for life activities. Here, we present 11 cryo-EM structures of four UT members in resting states, urea transport states, or inactive states bound with synthetic competitive, uncompetitive or noncompetitive inhibitor. Our results indicate that the binding of urea via a conserved urea recognition motif (URM) and the urea transport via H-bond transfer along the Q-T-T-Q motif among different UT members. Moreover, distinct binding modes of the competitive inhibitors 25a and ATB3, the uncompetitive inhibitor CF11 and the noncompetitive inhibitor HQA2 provide different mechanisms for blocking urea transport and achieved selectivity through L-P pocket, UCBP region and SCG pocket, respectively. In summary, our study not only allows structural understanding of urea transport via UTs but also afforded a structural landscape of hUT-A2 inhibition by competitive, uncompetitive and noncompetitive inhibitors, which may facilitate developing selective human UT-A inhibitors as a new class of salt-sparing diuretics. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_38274.map.gz emd_38274.map.gz | 46.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-38274-v30.xml emd-38274-v30.xml emd-38274.xml emd-38274.xml | 15.1 KB 15.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_38274.png emd_38274.png | 227.4 KB | ||
| Filedesc metadata |  emd-38274.cif.gz emd-38274.cif.gz | 5.6 KB | ||
| その他 |  emd_38274_half_map_1.map.gz emd_38274_half_map_1.map.gz emd_38274_half_map_2.map.gz emd_38274_half_map_2.map.gz | 84.6 MB 84.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-38274 http://ftp.pdbj.org/pub/emdb/structures/EMD-38274 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38274 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38274 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_38274_validation.pdf.gz emd_38274_validation.pdf.gz | 915.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_38274_full_validation.pdf.gz emd_38274_full_validation.pdf.gz | 915.1 KB | 表示 | |
| XML形式データ |  emd_38274_validation.xml.gz emd_38274_validation.xml.gz | 13.3 KB | 表示 | |
| CIF形式データ |  emd_38274_validation.cif.gz emd_38274_validation.cif.gz | 15.6 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38274 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38274 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38274 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38274 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8xddMC  8xd7C  8xd9C  8xdaC  8xdbC  8xdcC  8xdeC  8xdfC  8xdgC  8xdhC  8xdiC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_38274.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_38274.map.gz / 形式: CCP4 / 大きさ: 91.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_38274_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_38274_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Homotrimer complex of human urea transporter
| 全体 | 名称: Homotrimer complex of human urea transporter |
|---|---|
| 要素 |
|
-超分子 #1: Homotrimer complex of human urea transporter
| 超分子 | 名称: Homotrimer complex of human urea transporter / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-分子 #1: Urea transporter 2
| 分子 | 名称: Urea transporter 2 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapien (ヒト) Homo sapien (ヒト) |
| 分子量 | 理論値: 43.419789 KDa |
| 組換発現 | 生物種:  Spodoptera (蝶・蛾) Spodoptera (蝶・蛾) |
| 配列 | 文字列: MEESSEIKVE TNISKTSWIR SSMAASGKRV SKALSYITGE MKECGEGLKD KSPVFQFFDW VLRGTSQVMF VNNPLSGILI ILGLFIQNP WWAISGCLGT IMSTLTALIL SQDKSAIAAG FHGYNGVLVG LLMAVFSDKG DYYWWLLLPV IIMSMSCPIL S SALGTIFS ...文字列: MEESSEIKVE TNISKTSWIR SSMAASGKRV SKALSYITGE MKECGEGLKD KSPVFQFFDW VLRGTSQVMF VNNPLSGILI ILGLFIQNP WWAISGCLGT IMSTLTALIL SQDKSAIAAG FHGYNGVLVG LLMAVFSDKG DYYWWLLLPV IIMSMSCPIL S SALGTIFS KWDLPVFTLP FNITVTLYLA ATGHYNLFFP TTLLQPASAM PNITWSEVQV PLLLRAIPVG IGQVYGCDNP WT GGIFLIA LFISSPLICL HAAIGSTMGM LAALTIATPF DSIYFGLCGF NSTLACIAIG GMFYVITWQT HLLAIACALF AAY LGAALA NMLSVFGLPP CTWPFCLSAL TFLLLTTNNP AIYKLPLSKV TYPEANRIYY LSQERNRRAS IITKYQAYDV S UniProtKB: Urea transporter 2 |
-分子 #2: 8-hydroxyquinoline-2-carboxylic acid
| 分子 | 名称: 8-hydroxyquinoline-2-carboxylic acid / タイプ: ligand / ID: 2 / コピー数: 3 / 式: 8HC |
|---|---|
| 分子量 | 理論値: 189.167 Da |
| Chemical component information | 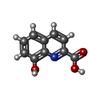 ChemComp-8HC: |
-分子 #3: 1-(3-methoxyphenyl)methanamine
| 分子 | 名称: 1-(3-methoxyphenyl)methanamine / タイプ: ligand / ID: 3 / コピー数: 3 / 式: SZ4 |
|---|---|
| 分子量 | 理論値: 137.179 Da |
| Chemical component information | 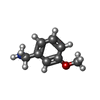 ChemComp-SZ4: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | cell |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: FREON 12 |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源: OTHER |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: OTHER / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: PDB ENTRY PDBモデル - PDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.0 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 92767 |
| 初期 角度割当 | タイプ: ANGULAR RECONSTITUTION |
| 最終 角度割当 | タイプ: OTHER |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)