+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
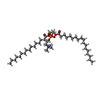
| タイトル | C. elegans SID1 in complex with dsRNA | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | dsRNA recognition / MEMBRANE PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報RNA transmembrane transporter activity / dsRNA transport / RNA transport / regulatory ncRNA-mediated post-transcriptional gene silencing / double-stranded RNA binding / lysosome / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   | |||||||||
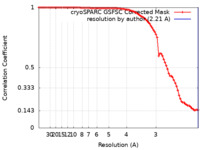
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.21 Å | |||||||||
 データ登録者 データ登録者 | Gong DS | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nucleic Acids Res / 年: 2024 ジャーナル: Nucleic Acids Res / 年: 2024タイトル: Structural basis for double-stranded RNA recognition by SID1. 著者: Runhao Wang / Ye Cong / Dandan Qian / Chuangye Yan / Deshun Gong /  要旨: The nucleic acid transport properties of the systemic RNAi-defective (SID) 1 family make them attractive targets for developing RNA-based therapeutics and drugs. However, the molecular basis for ...The nucleic acid transport properties of the systemic RNAi-defective (SID) 1 family make them attractive targets for developing RNA-based therapeutics and drugs. However, the molecular basis for double-stranded (ds) RNA recognition by SID1 family remains elusive. Here, we report the cryo-EM structures of Caenorhabditis elegans (c) SID1 alone and in complex with dsRNA, both at a resolution of 2.2 Å. The dimeric cSID1 interacts with two dsRNA molecules simultaneously. The dsRNA is located at the interface between β-strand rich domain (BRD)1 and BRD2 and nearly parallel to the membrane plane. In addition to extensive ionic interactions between basic residues and phosphate backbone, several hydrogen bonds are formed between 2'-hydroxyl group of dsRNA and the contact residues. Additionally, the electrostatic potential surface shows three basic regions are fitted perfectly into three major grooves of dsRNA. These structural characteristics enable cSID1 to bind dsRNA in a sequence-independent manner and to distinguish between DNA and RNA. The cSID1 exhibits no conformational changes upon binding dsRNA, with the exception of a few binding surfaces. Structural mapping of dozens of loss-of-function mutations allows potential interpretation of their diverse functional mechanisms. Our study marks an important step toward mechanistic understanding of the SID1 family-mediated dsRNA uptake. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_38236.map.gz emd_38236.map.gz | 59.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-38236-v30.xml emd-38236-v30.xml emd-38236.xml emd-38236.xml | 17.3 KB 17.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_38236_fsc.xml emd_38236_fsc.xml | 8.3 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_38236.png emd_38236.png | 140.8 KB | ||
| Filedesc metadata |  emd-38236.cif.gz emd-38236.cif.gz | 6.3 KB | ||
| その他 |  emd_38236_half_map_1.map.gz emd_38236_half_map_1.map.gz emd_38236_half_map_2.map.gz emd_38236_half_map_2.map.gz | 59.3 MB 59.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-38236 http://ftp.pdbj.org/pub/emdb/structures/EMD-38236 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38236 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-38236 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_38236_validation.pdf.gz emd_38236_validation.pdf.gz | 857.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_38236_full_validation.pdf.gz emd_38236_full_validation.pdf.gz | 857.5 KB | 表示 | |
| XML形式データ |  emd_38236_validation.xml.gz emd_38236_validation.xml.gz | 16.4 KB | 表示 | |
| CIF形式データ |  emd_38236_validation.cif.gz emd_38236_validation.cif.gz | 21.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38236 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38236 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38236 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-38236 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8xc1MC  8xbsC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_38236.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_38236.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.0825 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_38236_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
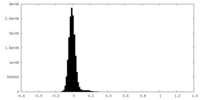
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_38236_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
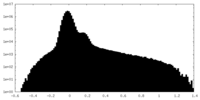
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : complex of SID1 and dsRNA
+超分子 #1: complex of SID1 and dsRNA
+超分子 #2: SID1
+超分子 #3: RNA
+分子 #1: Systemic RNA interference defective protein 1
+分子 #2: RNA (50-MER)
+分子 #3: RNA (50-MER)
+分子 #5: ZINC ION
+分子 #6: CHOLESTEROL
+分子 #7: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(tri...
+分子 #8: 2-acetamido-2-deoxy-beta-D-glucopyranose
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.4 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 1.3 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





 Z
Z Y
Y X
X













 Homo sapiens (ヒト)
Homo sapiens (ヒト)