+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of SARS-CoV-2 BA.2 RBD in complex with BA7535 fab (local refinement) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | VIRAL PROTEIN-IMMUNE SYSTEM complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / entry receptor-mediated virion attachment to host cell ...Maturation of spike protein / viral translation / Translation of Structural Proteins / Virion Assembly and Release / host cell surface / host extracellular space / suppression by virus of host tetherin activity / Induction of Cell-Cell Fusion / structural constituent of virion / entry receptor-mediated virion attachment to host cell / host cell endoplasmic reticulum-Golgi intermediate compartment membrane / receptor-mediated endocytosis of virus by host cell / Attachment and Entry / membrane fusion / positive regulation of viral entry into host cell / receptor-mediated virion attachment to host cell / receptor ligand activity / host cell surface receptor binding / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / SARS-CoV-2 activates/modulates innate and adaptive immune responses / host cell plasma membrane / virion membrane / identical protein binding / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
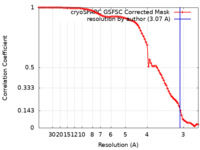
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.07 Å | |||||||||
 データ登録者 データ登録者 | Liu Z / Yan A / Gao Y | |||||||||
| 資金援助 |  中国, 1件 中国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Identification of a highly conserved neutralizing epitope within the RBD region of diverse SARS-CoV-2 variants. 著者: Yanqun Wang / An Yan / Deyong Song / Maoqin Duan / Chuangchuang Dong / Jiantao Chen / Zihe Jiang / Yuanzhu Gao / Muding Rao / Jianxia Feng / Zhaoyong Zhang / Ruxi Qi / Xiaomin Ma / Hong Liu / ...著者: Yanqun Wang / An Yan / Deyong Song / Maoqin Duan / Chuangchuang Dong / Jiantao Chen / Zihe Jiang / Yuanzhu Gao / Muding Rao / Jianxia Feng / Zhaoyong Zhang / Ruxi Qi / Xiaomin Ma / Hong Liu / Beibei Yu / Qiaoping Wang / Mengqi Zong / Jie Jiao / Pingping Xing / Rongrong Pan / Dan Li / Juxue Xiao / Junbo Sun / Ying Li / Linfeng Zhang / Zhenduo Shen / Baiping Sun / Yanyan Zhao / Lu Zhang / Jun Dai / Jingxian Zhao / Lan Wang / Changlin Dou / Zheng Liu / Jincun Zhao /  要旨: The constant emergence of SARS-CoV-2 variants continues to impair the efficacy of existing neutralizing antibodies, especially XBB.1.5 and EG.5, which showed exceptional immune evasion properties. ...The constant emergence of SARS-CoV-2 variants continues to impair the efficacy of existing neutralizing antibodies, especially XBB.1.5 and EG.5, which showed exceptional immune evasion properties. Here, we identify a highly conserved neutralizing epitope targeted by a broad-spectrum neutralizing antibody BA7535, which demonstrates high neutralization potency against not only previous variants, such as Alpha, Beta, Gamma, Delta and Omicron BA.1-BA.5, but also more recently emerged Omicron subvariants, including BF.7, CH.1.1, XBB.1, XBB.1.5, XBB.1.9.1, EG.5. Structural analysis of the Omicron Spike trimer with BA7535-Fab using cryo-EM indicates that BA7535 recognizes a highly conserved cryptic receptor-binding domain (RBD) epitope, avoiding most of the mutational hot spots in RBD. Furthermore, structural simulation based on the interaction of BA7535-Fab/RBD complexes dissects the broadly neutralizing effect of BA7535 against latest variants. Therapeutic and prophylactic treatment with BA7535 alone or in combination with BA7208 protected female mice from the circulating Omicron BA.5 and XBB.1 variant infection, suggesting the highly conserved neutralizing epitope serves as a potential target for developing highly potent therapeutic antibodies and vaccines. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_34526.map.gz emd_34526.map.gz | 59.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-34526-v30.xml emd-34526-v30.xml emd-34526.xml emd-34526.xml | 17.2 KB 17.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_34526_fsc.xml emd_34526_fsc.xml | 8.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_34526.png emd_34526.png | 76.4 KB | ||
| Filedesc metadata |  emd-34526.cif.gz emd-34526.cif.gz | 6 KB | ||
| その他 |  emd_34526_half_map_1.map.gz emd_34526_half_map_1.map.gz emd_34526_half_map_2.map.gz emd_34526_half_map_2.map.gz | 59.3 MB 59.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-34526 http://ftp.pdbj.org/pub/emdb/structures/EMD-34526 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34526 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-34526 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_34526_validation.pdf.gz emd_34526_validation.pdf.gz | 809.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_34526_full_validation.pdf.gz emd_34526_full_validation.pdf.gz | 808.8 KB | 表示 | |
| XML形式データ |  emd_34526_validation.xml.gz emd_34526_validation.xml.gz | 16.2 KB | 表示 | |
| CIF形式データ |  emd_34526_validation.cif.gz emd_34526_validation.cif.gz | 21 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34526 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34526 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34526 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-34526 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8h7zMC  8h7lC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_34526.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_34526.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.336 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #2
| ファイル | emd_34526_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_34526_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cryo-EM structure of SARS-CoV-2 BA.2 RBD in complex with BA7535 f...
| 全体 | 名称: Cryo-EM structure of SARS-CoV-2 BA.2 RBD in complex with BA7535 fab (local refinement) |
|---|---|
| 要素 |
|
-超分子 #1: Cryo-EM structure of SARS-CoV-2 BA.2 RBD in complex with BA7535 f...
| 超分子 | 名称: Cryo-EM structure of SARS-CoV-2 BA.2 RBD in complex with BA7535 fab (local refinement) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Spike glycoprotein
| 分子 | 名称: Spike glycoprotein / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 22.282211 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: ITNLCPFDEV FNATRFASVY AWNRKRISNC VADYSVLYNF APFFAFKCYG VSPTKLNDLC FTNVYADSFV IRGNEVSQIA PGQTGNIAD YNYKLPDDFT GCVIAWNSNK LDSKVGGNYN YLYRLFRKSN LKPFERDIST EIYQAGNKPC NGVAGFNCYF P LRSYGFRP ...文字列: ITNLCPFDEV FNATRFASVY AWNRKRISNC VADYSVLYNF APFFAFKCYG VSPTKLNDLC FTNVYADSFV IRGNEVSQIA PGQTGNIAD YNYKLPDDFT GCVIAWNSNK LDSKVGGNYN YLYRLFRKSN LKPFERDIST EIYQAGNKPC NGVAGFNCYF P LRSYGFRP TYGVGHQPYR VVVLSFELLH APATVCGPK UniProtKB: Spike glycoprotein |
-分子 #2: BA7535 fab
| 分子 | 名称: BA7535 fab / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 49.838086 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVESGGG VVQPGRSLRL SCAASEFTFS SFAMHWVRQA PGKGLEWVAL ISYDGSNKYY ADSVKGRFTI SRDNSKNTLY LQMNSLRAE DTAVYYCARV SYPLTKYYYG MDVWGQGTTV TVSSASTKGP SVFPLAPSSK STSGGTAALG CLVKDYFPEP V TVSWNSGA ...文字列: EVQLVESGGG VVQPGRSLRL SCAASEFTFS SFAMHWVRQA PGKGLEWVAL ISYDGSNKYY ADSVKGRFTI SRDNSKNTLY LQMNSLRAE DTAVYYCARV SYPLTKYYYG MDVWGQGTTV TVSSASTKGP SVFPLAPSSK STSGGTAALG CLVKDYFPEP V TVSWNSGA LTSGVHTFPA VLQSSGLYSL SSVVTVPSSS LGTQTYICNV NHKPSNTKVD KKVEPKSCDK THTCPPCPAP EL LGGPSVF LFPPKPKDTL MISRTPEVTC VVVDVSHEDP EVKFNWYVDG VEVHNAKTKP REEQYNSTYR VVSVLTVLHQ DWL NGKEYK CKVSNKALPA PIEKTISKAK GQPREPQVYT LPPSRDELTK NQVSLTCLVK GFYPSDIAVE WESNGQPENN YKTT PPVLD SDGSFFLYSK LTVDKSRWQQ GNVFSCSVMH EALHNHYTQK SLSLSPGK |
-分子 #3: BA7535 fab
| 分子 | 名称: BA7535 fab / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.431002 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EIVMTQSPAF MSATPGDKVN ISCKASQDIA DDMNWYQQKP GEAAIFIIQE ATTLVPGISP RFSGSGYGTD FTLTINNIES EDAAYYFCL QHDNFPLTFG GGTKVEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS ...文字列: EIVMTQSPAF MSATPGDKVN ISCKASQDIA DDMNWYQQKP GEAAIFIIQE ATTLVPGISP RFSGSGYGTD FTLTINNIES EDAAYYFCL QHDNFPLTFG GGTKVEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS KDSTYSLSST LTLSKADYEK HKVYACEVTH QGLSSPVTKS FNRGEC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 1.39 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 5.0 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー









 Z
Z Y
Y X
X