+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | CryoEM structure of yeast Arginyltransferase 1 (ATE1) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Arginyltransferase / post-translational modification / enzyme / TRANSFERASE-RNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Huang W / Zhang Y / Taylor DJ | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2023 ジャーナル: Nat Commun / 年: 2023タイトル: The structural basis of tRNA recognition by arginyl-tRNA-protein transferase. 著者: Thilini Abeywansha / Wei Huang / Xuan Ye / Allison Nawrocki / Xin Lan / Eckhard Jankowsky / Derek J Taylor / Yi Zhang /  要旨: Arginyl-tRNA-protein transferase 1 (ATE1) is a master regulator of protein homeostasis, stress response, cytoskeleton maintenance, and cell migration. The diverse functions of ATE1 arise from its ...Arginyl-tRNA-protein transferase 1 (ATE1) is a master regulator of protein homeostasis, stress response, cytoskeleton maintenance, and cell migration. The diverse functions of ATE1 arise from its unique enzymatic activity to covalently attach an arginine onto its protein substrates in a tRNA-dependent manner. However, how ATE1 (and other aminoacyl-tRNA transferases) hijacks tRNA from the highly efficient ribosomal protein synthesis pathways and catalyzes the arginylation reaction remains a mystery. Here, we describe the three-dimensional structures of Saccharomyces cerevisiae ATE1 with and without its tRNA cofactor. Importantly, the putative substrate binding domain of ATE1 adopts a previously uncharacterized fold that contains an atypical zinc-binding site critical for ATE1 stability and function. The unique recognition of tRNA by ATE1 is coordinated through interactions with the major groove of the acceptor arm of tRNA. Binding of tRNA induces conformational changes in ATE1 that helps explain the mechanism of substrate arginylation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_29638.map.gz emd_29638.map.gz | 58.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-29638-v30.xml emd-29638-v30.xml emd-29638.xml emd-29638.xml | 17.1 KB 17.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_29638.png emd_29638.png | 56.9 KB | ||
| Filedesc metadata |  emd-29638.cif.gz emd-29638.cif.gz | 5.8 KB | ||
| その他 |  emd_29638_additional_1.map.gz emd_29638_additional_1.map.gz emd_29638_half_map_1.map.gz emd_29638_half_map_1.map.gz emd_29638_half_map_2.map.gz emd_29638_half_map_2.map.gz | 53.5 MB 2.3 MB 2.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-29638 http://ftp.pdbj.org/pub/emdb/structures/EMD-29638 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29638 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-29638 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_29638_validation.pdf.gz emd_29638_validation.pdf.gz | 491.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_29638_full_validation.pdf.gz emd_29638_full_validation.pdf.gz | 491.2 KB | 表示 | |
| XML形式データ |  emd_29638_validation.xml.gz emd_29638_validation.xml.gz | 12.1 KB | 表示 | |
| CIF形式データ |  emd_29638_validation.cif.gz emd_29638_validation.cif.gz | 14.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29638 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29638 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29638 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-29638 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8fzrMC  8e3sC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_29638.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_29638.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.8726 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: Phenix auto-sharpen map
| ファイル | emd_29638_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Phenix auto-sharpen map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
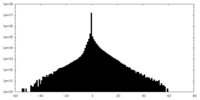
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_29638_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
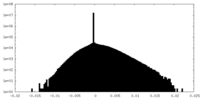
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_29638_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : yeast Arginyltransferase 1 bound to Arg tRNA
| 全体 | 名称: yeast Arginyltransferase 1 bound to Arg tRNA |
|---|---|
| 要素 |
|
-超分子 #1: yeast Arginyltransferase 1 bound to Arg tRNA
| 超分子 | 名称: yeast Arginyltransferase 1 bound to Arg tRNA / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  |
-分子 #1: Arginyl-tRNA--protein transferase 1
| 分子 | 名称: Arginyl-tRNA--protein transferase 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: arginyltransferase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 58.001277 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSDRFVIWAP SMHNEPAAKC GYCHGNKGGN MDQLFALDSW AHRYMNKMDV VKIENCTIGS FVEHMDVATY DRMCNMGFRR SGKFLYKVD PLRNCCRLYT IRTAPQELNM TKELKKCISR FATRITSEDY CPAAVASSDF VGKIVNAEMN SKTFYTRFEP A LYSEEKYH ...文字列: MSDRFVIWAP SMHNEPAAKC GYCHGNKGGN MDQLFALDSW AHRYMNKMDV VKIENCTIGS FVEHMDVATY DRMCNMGFRR SGKFLYKVD PLRNCCRLYT IRTAPQELNM TKELKKCISR FATRITSEDY CPAAVASSDF VGKIVNAEMN SKTFYTRFEP A LYSEEKYH LFVKYQEKVH QDYNNSPKSF KRFLCDTPFG PEAVLGTQES WEQLNNWQRM KPGEKLKHMG PVHECYYYEG KL IAITVSD ILPSGISSVY FIWDPDYSKW SLGKLSALRD LAIIQRTNLQ YYYLGYYIED CPKMNYKANY GAEVLDVCHS KYI PLKPIQ DMISRGKLFV IGEEETKVTK ELYLVDSETG RGEGFPTDNV VKYKNIAEEI YGVGGCAFKS ANESALELKE LYGI PYEEE DLDTIYHLKE HNGHAPNGIP NVVPGLLPLW ELLDIMQSGK ITDLEGRLFL FEIETEGIRP LINFYSEPPN VKKRI CDVI RLFGFETCMK AVILYSEQM UniProtKB: Arginyl-tRNA--protein transferase 1 |
-分子 #2: Arg tRNA
| 分子 | 名称: Arg tRNA / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 24.789736 KDa |
| 配列 | 文字列: GCGCCCUUAG CUCAGUUGGA UAGAGCAACG ACCUUCUAAG UCGUGGGCCG CAGGUUCGAA UCCUGCAGGG CGCGCCA GENBANK: GENBANK: CP026935.2 |
-分子 #3: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 3 / コピー数: 1 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.1 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 40.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 25.0 µm / 最小 デフォーカス(公称値): 5.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL / 詳細: AlphaFold II predicted mode AF-P16639-F1 |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.6 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 208051 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー







 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)