+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-2858 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of yeast 80S ribosome calculated on Amazon's elastic cloud computing network | |||||||||
 マップデータ マップデータ | 80S yeast ribosome reconstructed using Relion from published dataset EMPIAR ID 10002. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Ribosome / yeast / Relion / Amazon | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.6 Å | |||||||||
 データ登録者 データ登録者 | Cianfrocco MA / Leschziner AE | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2015 ジャーナル: Elife / 年: 2015タイトル: Low cost, high performance processing of single particle cryo-electron microscopy data in the cloud. 著者: Michael A Cianfrocco / Andres E Leschziner /  要旨: The advent of a new generation of electron microscopes and direct electron detectors has realized the potential of single particle cryo-electron microscopy (cryo-EM) as a technique to generate high- ...The advent of a new generation of electron microscopes and direct electron detectors has realized the potential of single particle cryo-electron microscopy (cryo-EM) as a technique to generate high-resolution structures. Calculating these structures requires high performance computing clusters, a resource that may be limiting to many likely cryo-EM users. To address this limitation and facilitate the spread of cryo-EM, we developed a publicly available 'off-the-shelf' computing environment on Amazon's elastic cloud computing infrastructure. This environment provides users with single particle cryo-EM software packages and the ability to create computing clusters with 16-480+ CPUs. We tested our computing environment using a publicly available 80S yeast ribosome dataset and estimate that laboratories could determine high-resolution cryo-EM structures for $50 to $1500 per structure within a timeframe comparable to local clusters. Our analysis shows that Amazon's cloud computing environment may offer a viable computing environment for cryo-EM. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_2858.map.gz emd_2858.map.gz | 49.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-2858-v30.xml emd-2858-v30.xml emd-2858.xml emd-2858.xml | 11.4 KB 11.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_2858_fsc.xml emd_2858_fsc.xml | 8.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_2858.png emd_2858.png | 516.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-2858 http://ftp.pdbj.org/pub/emdb/structures/EMD-2858 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2858 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-2858 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_2858_validation.pdf.gz emd_2858_validation.pdf.gz | 340.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_2858_full_validation.pdf.gz emd_2858_full_validation.pdf.gz | 339.3 KB | 表示 | |
| XML形式データ |  emd_2858_validation.xml.gz emd_2858_validation.xml.gz | 10.7 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2858 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2858 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2858 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-2858 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_2858.map.gz / 形式: CCP4 / 大きさ: 51.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_2858.map.gz / 形式: CCP4 / 大きさ: 51.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | 80S yeast ribosome reconstructed using Relion from published dataset EMPIAR ID 10002. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.77 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : 80S yeast ribosome
| 全体 | 名称: 80S yeast ribosome |
|---|---|
| 要素 |
|
-超分子 #1000: 80S yeast ribosome
| 超分子 | 名称: 80S yeast ribosome / タイプ: sample / ID: 1000 詳細: Micrographs were downloaded from EMPIAR dataset 10002, associated with the publication Bai et al. eLife (2013) 集合状態: ribosome-eukaryote / Number unique components: 1 |
|---|---|
| 分子量 | 実験値: 4.2 MDa / 理論値: 4.2 MDa |
-超分子 #1: 80S ribosome
| 超分子 | 名称: 80S ribosome / タイプ: complex / ID: 1 詳細: Micrographs were downloaded from EMPAIR database 10002, associated with Bai et al. eLife (2013) 組換発現: No / Ribosome-details: ribosome-eukaryote: ALL |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 実験値: 4.2 MDa / 理論値: 4.2 MDa |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL |
|---|---|
| 緩衝液 | pH: 7.45 詳細: 3mM Hepes-KOH, 6.6 mM Tris-acetate pH 7.2, 3 mM NH4Cl, 6.6 mM NH4-acetate, 48 mM K-acetate, 4 mM Mg-acetate, 2.4 mM DTT |
| グリッド | 詳細: Quantifoil grids (2/2) with 3 nm thin carbon on top |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 90 K / 装置: FEI VITROBOT MARK II 詳細: Micrographs were downloaded from EMPIAR database 10002, associated with Bai et al. eLife (2013) 手法: Blot 2.5 seconds before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI POLARA 300 |
|---|---|
| 温度 | 最低: 80 K / 最高: 90 K / 平均: 85 K |
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism was corrected at 59,000 times magnification |
| 詳細 | Micrographs were downloaded from EMPIAR 10002 |
| 日付 | 2012年7月15日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: FEI FALCON I (4k x 4k) デジタル化 - サンプリング間隔: 14 µm / 実像数: 200 / 平均電子線量: 16 e/Å2 詳細: Every image is the average of sixteen frames recorded by the direct electron detector |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 79096 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2 mm / 最大 デフォーカス(公称値): 3.44 µm / 最小 デフォーカス(公称値): 1.191 µm |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Tecnai Polara / 画像提供: FEI Company |
- 画像解析
画像解析
| 詳細 | Particles were extracted and processed using Relion |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: C1 (非対称) / 解像度のタイプ: BY AUTHOR / 解像度: 4.6 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Relion / 使用した粒子像数: 32533 |
| FSC曲線 (解像度の算出) | 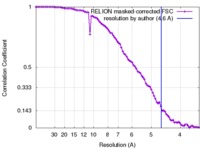 |
-原子モデル構築 1
| 初期モデル | PDB ID:  3u5b |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Each PDB model was docked using "Fit in map" in Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
-原子モデル構築 2
| 初期モデル | PDB ID:  3u5c |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Each PDB model was docked using "Fit in map" in Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
-原子モデル構築 3
| 初期モデル | PDB ID:  3u5d |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Each PDB model was docked using "Fit in map" in Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
-原子モデル構築 4
| 初期モデル | PDB ID:  3u5e |
|---|---|
| ソフトウェア | 名称:  Chimera Chimera |
| 詳細 | Each PDB model was docked using "Fit in map" in Chimera |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)