+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cereblon~DDB1 bound to Iberdomide and Ikaros ZF1-2-3 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Ubiquitin / CRL4 / Adaptor / Cereblon / LIGASE | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of monoatomic ion transmembrane transport / lymphocyte differentiation / positive regulation by virus of viral protein levels in host cell / epigenetic programming in the zygotic pronuclei / spindle assembly involved in female meiosis / Cul4-RING E3 ubiquitin ligase complex / UV-damage excision repair / biological process involved in interaction with symbiont / regulation of mitotic cell cycle phase transition / NOTCH3 Intracellular Domain Regulates Transcription ...negative regulation of monoatomic ion transmembrane transport / lymphocyte differentiation / positive regulation by virus of viral protein levels in host cell / epigenetic programming in the zygotic pronuclei / spindle assembly involved in female meiosis / Cul4-RING E3 ubiquitin ligase complex / UV-damage excision repair / biological process involved in interaction with symbiont / regulation of mitotic cell cycle phase transition / NOTCH3 Intracellular Domain Regulates Transcription / WD40-repeat domain binding / Cul4A-RING E3 ubiquitin ligase complex / Cul4B-RING E3 ubiquitin ligase complex / ubiquitin ligase complex scaffold activity / negative regulation of reproductive process / negative regulation of developmental process / locomotory exploration behavior / mesoderm development / viral release from host cell / cullin family protein binding / positive regulation of Wnt signaling pathway / ectopic germ cell programmed cell death / negative regulation of protein-containing complex assembly / proteasomal protein catabolic process / positive regulation of viral genome replication / pericentric heterochromatin / positive regulation of gluconeogenesis / erythrocyte differentiation / nucleotide-excision repair / Recognition of DNA damage by PCNA-containing replication complex / DNA Damage Recognition in GG-NER / positive regulation of protein-containing complex assembly / regulation of circadian rhythm / Transcription-Coupled Nucleotide Excision Repair (TC-NER) / Formation of TC-NER Pre-Incision Complex / Dual Incision in GG-NER / Wnt signaling pathway / Formation of Incision Complex in GG-NER / Dual incision in TC-NER / Gap-filling DNA repair synthesis and ligation in TC-NER / positive regulation of protein catabolic process / cellular response to UV / rhythmic process / chromatin organization / Neddylation / site of double-strand break / protein-macromolecule adaptor activity / ubiquitin-dependent protein catabolic process / proteasome-mediated ubiquitin-dependent protein catabolic process / transmembrane transporter binding / Potential therapeutics for SARS / damaged DNA binding / chromosome, telomeric region / protein ubiquitination / DNA-binding transcription factor activity / RNA polymerase II cis-regulatory region sequence-specific DNA binding / protein domain specific binding / DNA repair / negative regulation of DNA-templated transcription / DNA damage response / protein-containing complex binding / regulation of transcription by RNA polymerase II / negative regulation of apoptotic process / nucleolus / apoptotic process / perinuclear region of cytoplasm / protein-containing complex / DNA binding / extracellular space / extracellular exosome / nucleoplasm / identical protein binding / membrane / nucleus / metal ion binding / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.6 Å | |||||||||
 データ登録者 データ登録者 | Watson ER / Lander GC | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2022 ジャーナル: Science / 年: 2022タイトル: Molecular glue CELMoD compounds are regulators of cereblon conformation. 著者: Edmond R Watson / Scott Novick / Mary E Matyskiela / Philip P Chamberlain / Andres H de la Peña / Jinyi Zhu / Eileen Tran / Patrick R Griffin / Ingrid E Wertz / Gabriel C Lander /  要旨: Cereblon (CRBN) is a ubiquitin ligase (E3) substrate receptor protein co-opted by CRBN E3 ligase modulatory drug (CELMoD) agents that target therapeutically relevant proteins for degradation. Prior ...Cereblon (CRBN) is a ubiquitin ligase (E3) substrate receptor protein co-opted by CRBN E3 ligase modulatory drug (CELMoD) agents that target therapeutically relevant proteins for degradation. Prior crystallographic studies defined the drug-binding site within CRBN's thalidomide-binding domain (TBD), but the allostery of drug-induced neosubstrate binding remains unclear. We performed cryo-electron microscopy analyses of the DNA damage-binding protein 1 (DDB1)-CRBN apo complex and compared these structures with DDB1-CRBN in the presence of CELMoD compounds alone and complexed with neosubstrates. Association of CELMoD compounds to the TBD is necessary and sufficient for triggering CRBN allosteric rearrangement from an open conformation to the canonical closed conformation. The neosubstrate Ikaros only stably associates with the closed CRBN conformation, illustrating the importance of allostery for CELMoD compound efficacy and informing structure-guided design strategies to improve therapeutic efficacy. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_27241.map.gz emd_27241.map.gz | 21.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-27241-v30.xml emd-27241-v30.xml emd-27241.xml emd-27241.xml | 23.1 KB 23.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_27241_fsc.xml emd_27241_fsc.xml | 7.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_27241.png emd_27241.png | 117 KB | ||
| Filedesc metadata |  emd-27241.cif.gz emd-27241.cif.gz | 7.1 KB | ||
| その他 |  emd_27241_additional_1.map.gz emd_27241_additional_1.map.gz emd_27241_half_map_1.map.gz emd_27241_half_map_1.map.gz emd_27241_half_map_2.map.gz emd_27241_half_map_2.map.gz | 22.2 MB 39.8 MB 39.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27241 http://ftp.pdbj.org/pub/emdb/structures/EMD-27241 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27241 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27241 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_27241_validation.pdf.gz emd_27241_validation.pdf.gz | 875.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_27241_full_validation.pdf.gz emd_27241_full_validation.pdf.gz | 874.8 KB | 表示 | |
| XML形式データ |  emd_27241_validation.xml.gz emd_27241_validation.xml.gz | 15.1 KB | 表示 | |
| CIF形式データ |  emd_27241_validation.cif.gz emd_27241_validation.cif.gz | 19.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27241 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27241 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27241 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27241 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8d80MC  8cvpC  8d7uC  8d7vC  8d7wC  8d7xC  8d7yC  8d7zC  8d81C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_27241.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_27241.map.gz / 形式: CCP4 / 大きさ: 42.9 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.15 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_27241_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_27241_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_27241_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Cereblon~DDB1 bound to Iberdomide and Ikaros ZF1-2-3
| 全体 | 名称: Cereblon~DDB1 bound to Iberdomide and Ikaros ZF1-2-3 |
|---|---|
| 要素 |
|
-超分子 #1: Cereblon~DDB1 bound to Iberdomide and Ikaros ZF1-2-3
| 超分子 | 名称: Cereblon~DDB1 bound to Iberdomide and Ikaros ZF1-2-3 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 177 KDa |
-分子 #1: DNA damage-binding protein 1
| 分子 | 名称: DNA damage-binding protein 1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 127.097469 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSYNYVVTAQ KPTAVNGCVT GHFTSAEDLN LLIAKNTRLE IYVVTAEGLR PVKEVGMYGK IAVMELFRPK GESKDLLFIL TAKYNACIL EYKQSGESID IITRAHGNVQ DRIGRPSETG IIGIIDPECR MIGLRLYDGL FKVIPLDRDN KELKAFNIRL E ELHVIDVK ...文字列: MSYNYVVTAQ KPTAVNGCVT GHFTSAEDLN LLIAKNTRLE IYVVTAEGLR PVKEVGMYGK IAVMELFRPK GESKDLLFIL TAKYNACIL EYKQSGESID IITRAHGNVQ DRIGRPSETG IIGIIDPECR MIGLRLYDGL FKVIPLDRDN KELKAFNIRL E ELHVIDVK FLYGCQAPTI CFVYQDPQGR HVKTYEVSLR EKEFNKGPWK QENVEAEASM VIAVPEPFGG AIIIGQESIT YH NGDKYLA IAPPIIKQST IVCHNRVDPN GSRYLLGDME GRLFMLLLEK EEQMDGTVTL KDLRVELLGE TSIAECLTYL DNG VVFVGS RLGDSQLVKL NVDSNEQGSY VVAMETFTNL GPIVDMCVVD LERQGQGQLV TCSGAFKEGS LRIIRNGIGI HEHA SIDLP GIKGLWPLRS DPNRETDDTL VLSFVGQTRV LMLNGEEVEE TELMGFVDDQ QTFFCGNVAH QQLIQITSAS VRLVS QEPK ALVSEWKEPQ AKNISVASCN SSQVVVAVGR ALYYLQIHPQ ELRQISHTEM EHEVACLDIT PLGDSNGLSP LCAIGL WTD ISARILKLPS FELLHKEMLG GEIIPRSILM TTFESSHYLL CALGDGALFY FGLNIETGLL SDRKKVTLGT QPTVLRT FR SLSTTNVFAC SDRPTVIYSS NHKLVFSNVN LKEVNYMCPL NSDGYPDSLA LANNSTLTIG TIDEIQKLHI RTVPLYES P RKICYQEVSQ CFGVLSSRIE VQDTSGGTTA LRPSASTQAL SSSVSSSKLF SSSTAPHETS FGEEVEVHNL LIIDQHTFE VLHAHQFLQN EYALSLVSCK LGKDPNTYFI VGTAMVYPEE AEPKQGRIVV FQYSDGKLQT VAEKEVKGAV YSMVEFNGKL LASINSTVR LYEWTTEKEL RTECNHYNNI MALYLKTKGD FILVGDLMRS VLLLAYKPME GNFEEIARDF NPNWMSAVEI L DDDNFLGA ENAFNLFVCQ KDSAATTDEE RQHLQEVGLF HLGEFVNVFC HGSLVMQNLG ETSTPTQGSV LFGTVNGMIG LV TSLSESW YNLLLDMQNR LNKVIKSVGK IEHSFWRSFH TERKTEPATG FIDGDLIESF LDISRPKMQE VVANLQYDDG SGM KREATA DDLIKVVEEL TRIH UniProtKB: DNA damage-binding protein 1 |
-分子 #2: Protein cereblon
| 分子 | 名称: Protein cereblon / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 50.603676 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MAGEGDQQDA AHNMGNHLPL LPAESEEEDE MEVEDQDSKE AKKPNIINFD TSLPTSHTYL GADMEEFHGR TLHDDDSCQV IPVLPQVMM ILIPGQTLPL QLFHPQEVSM VRNLIQKDRT FAVLAYSNVQ EREAQFGTTA EIYAYREEQD FGIEIVKVKA I GRQRFKVL ...文字列: MAGEGDQQDA AHNMGNHLPL LPAESEEEDE MEVEDQDSKE AKKPNIINFD TSLPTSHTYL GADMEEFHGR TLHDDDSCQV IPVLPQVMM ILIPGQTLPL QLFHPQEVSM VRNLIQKDRT FAVLAYSNVQ EREAQFGTTA EIYAYREEQD FGIEIVKVKA I GRQRFKVL ELRTQSDGIQ QAKVQILPEC VLPSTMSAVQ LESLNKCQIF PSKPVSREDQ CSYKWWQKYQ KRKFHCANLT SW PRWLYSL YDAETLMDRI KKQLREWDEN LKDDSLPSNP IDFSYRVAAC LPIDDVLRIQ LLKIGSAIQR LRCELDIMNK CTS LCCKQC QETEITTKNE IFSLSLCGPM AAYVNPHGYV HETLTVYKAC NLNLIGRPST EHSWFPGYAW TVAQCKICAS HIGW KFTAT KKDMSPQKFW GLTRSALLPT IPDTEDEISP DKVILCL UniProtKB: Protein cereblon |
-分子 #3: DNA-binding protein Ikaros
| 分子 | 名称: DNA-binding protein Ikaros / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 9.731428 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: GSLPNGKLKC DICGIICIGP NVLMVHKRSH TGERPFQCNQ CGASFTQKGN LLRHIKLHSG EKPFKCHLCN YACRRRDALT GHLRTHS UniProtKB: DNA-binding protein Ikaros |
-分子 #4: ZINC ION
| 分子 | 名称: ZINC ION / タイプ: ligand / ID: 4 / コピー数: 2 / 式: ZN |
|---|---|
| 分子量 | 理論値: 65.409 Da |
-分子 #5: (3S)-3-[4-({4-[(morpholin-4-yl)methyl]phenyl}methoxy)-1-oxo-1,3-d...
| 分子 | 名称: (3S)-3-[4-({4-[(morpholin-4-yl)methyl]phenyl}methoxy)-1-oxo-1,3-dihydro-2H-isoindol-2-yl]piperidine-2,6-dione タイプ: ligand / ID: 5 / コピー数: 1 / 式: 8W7 |
|---|---|
| 分子量 | 理論値: 449.499 Da |
| Chemical component information | 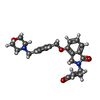 ChemComp-8W7: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 20 mg/mL |
|---|---|
| 緩衝液 | pH: 7 / 詳細: 20mM HEPES pH 7.0, 240mM NaCl, 3mM TCEP |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 25 sec. / 前処理 - 雰囲気: OTHER |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 277 K / 装置: HOMEMADE PLUNGER / 詳細: Manual plunge in 4 degree C cold room. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 62.5 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 43478 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 1.2 µm 最小 デフォーカス(公称値): 0.7000000000000001 µm 倍率(公称値): 36000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー






















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)