+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of Acidothermus cellulolyticus Cas9 ternary complex (Target bound) | |||||||||
 マップデータ マップデータ | Accas9 ternary complex (Target bound) | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Cas9 / AceCas9 / Crispr / Target bound / RNA BINDING PROTEIN / RNA BINDING PROTEIN-DNA-RNA complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報defense response to virus / endonuclease activity / DNA binding / RNA binding / zinc ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Acidothermus cellulolyticus 11B (バクテリア) / synthetic construct (人工物) Acidothermus cellulolyticus 11B (バクテリア) / synthetic construct (人工物) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.78 Å | |||||||||
 データ登録者 データ登録者 | Rai J / Das A / Li H | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Catal / 年: 2023 ジャーナル: Nat Catal / 年: 2023タイトル: Coupled catalytic states and the role of metal coordination in Cas9. 著者: Anuska Das / Jay Rai / Mitchell O Roth / Yuerong Shu / Megan L Medina / Mackenzie R Barakat / Hong Li /  要旨: Controlling the activity of the CRISPR-Cas9 system is essential to its safe adoption for clinical and research applications. Although the conformational dynamics of Cas9 are known to control its ...Controlling the activity of the CRISPR-Cas9 system is essential to its safe adoption for clinical and research applications. Although the conformational dynamics of Cas9 are known to control its enzymatic activity, details of how Cas9 influences the catalytic processes at both nuclease domains remain elusive. Here we report five cryo-electron microscopy structures of the active Cas9 complex along the reaction path at 2.2-2.9 Å resolution. We observed that a large movement in one nuclease domain, triggered by the cognate DNA, results in noticeable changes in the active site of the other domain that is required for metal coordination and catalysis. Furthermore, the conformations synchronize the reaction intermediates, enabling coupled cutting of the two DNA strands. Consistent with the roles of conformations in organizing the active sites, adjustments to the metal-coordination residues lead to altered metal specificity of Cas9 and commonly used Cas9 in cells. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_27145.map.gz emd_27145.map.gz | 100.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-27145-v30.xml emd-27145-v30.xml emd-27145.xml emd-27145.xml | 18.8 KB 18.8 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_27145.png emd_27145.png | 73.8 KB | ||
| Filedesc metadata |  emd-27145.cif.gz emd-27145.cif.gz | 6.8 KB | ||
| その他 |  emd_27145_half_map_1.map.gz emd_27145_half_map_1.map.gz emd_27145_half_map_2.map.gz emd_27145_half_map_2.map.gz | 84.2 MB 84.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-27145 http://ftp.pdbj.org/pub/emdb/structures/EMD-27145 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27145 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-27145 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_27145_validation.pdf.gz emd_27145_validation.pdf.gz | 1 MB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_27145_full_validation.pdf.gz emd_27145_full_validation.pdf.gz | 1 MB | 表示 | |
| XML形式データ |  emd_27145_validation.xml.gz emd_27145_validation.xml.gz | 13 KB | 表示 | |
| CIF形式データ |  emd_27145_validation.cif.gz emd_27145_validation.cif.gz | 15.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27145 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27145 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27145 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-27145 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_27145.map.gz / 形式: CCP4 / 大きさ: 107.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_27145.map.gz / 形式: CCP4 / 大きさ: 107.2 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Accas9 ternary complex (Target bound) | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.825 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: Cas9 ternary complex (Target bound)
| ファイル | emd_27145_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cas9 ternary complex (Target bound) | ||||||||||||
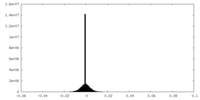
| 投影像・断面図 |
| ||||||||||||
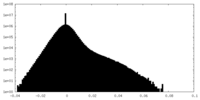
| 密度ヒストグラム |
-ハーフマップ: Halfmap2
| ファイル | emd_27145_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Halfmap2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
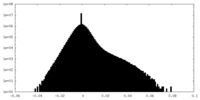
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : CryoEM Structure of AceCas9 (Target bound)
| 全体 | 名称: CryoEM Structure of AceCas9 (Target bound) |
|---|---|
| 要素 |
|
-超分子 #1: CryoEM Structure of AceCas9 (Target bound)
| 超分子 | 名称: CryoEM Structure of AceCas9 (Target bound) / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#3 |
|---|
-超分子 #2: CRISPR-associated endonuclease, Csn1 family/RNA
| 超分子 | 名称: CRISPR-associated endonuclease, Csn1 family/RNA / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Acidothermus cellulolyticus 11B (バクテリア) Acidothermus cellulolyticus 11B (バクテリア) |
-超分子 #3: DNA
| 超分子 | 名称: DNA / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #3 |
|---|
-分子 #1: CRISPR-associated endonuclease, Csn1 family
| 分子 | 名称: CRISPR-associated endonuclease, Csn1 family / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Acidothermus cellulolyticus 11B (バクテリア) Acidothermus cellulolyticus 11B (バクテリア)株: ATCC 43068 / DSM 8971 / 11B |
| 分子量 | 理論値: 127.498094 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MGGSEVGTVP VTWRLGVDVG ERSIGLAAVS YEEDKPKEIL AAVSWIHDGG VGDERSGASR LALRGMARRA RRLRRFRRAR LRDLDMLLS ELGWTPLPDK NVSPVDAWLA RKRLAEEYVV DETERRRLLG YAVSHMARHR GWRNPWTTIK DLKNLPQPSD S WERTRESL ...文字列: MGGSEVGTVP VTWRLGVDVG ERSIGLAAVS YEEDKPKEIL AAVSWIHDGG VGDERSGASR LALRGMARRA RRLRRFRRAR LRDLDMLLS ELGWTPLPDK NVSPVDAWLA RKRLAEEYVV DETERRRLLG YAVSHMARHR GWRNPWTTIK DLKNLPQPSD S WERTRESL EARYSVSLEP GTVGQWAGYL LQRAPGIRLN PTQQSAGRRA ELSNATAFET RLRQEDVLWE LRCIADVQGL PE DVVSNVI DAVFCQKRPS VPAERIGRDP LDPSQLRASR ACLEFQEYRI VAAVANLRIR DGSGSRPLSL EERNAVIEAL LAQ TERSLT WSDIALEILK LPNESDLTSV PEEDGPSSLA YSQFAPFDET SARIAEFIAK NRRKIPTFAQ WWQEQDRTSR SDLV AALAD NSIAGEEEQE LLVHLPDAEL EALEGLALPS GRVAYSRLTL SGLTRVMRDD GVDVHNARKT CFGVDDNWRP PLPAL HEAT GHPVVDRNLA ILRKFLSSAT MRWGPPQSIV VELARGASES RERQAEEEAA RRAHRKANDR IRAELRASGL SDPSPA DLV RARLLELYDC HCMYCGAPIS WENSELDHIV PRTDGGSNRH ENLAITCGAC NKEKGRRPFA SWAETSNRVQ LRDVIDR VQ KLKYSGNMYW TRDEFSRYKK SVVARLKRRT SDPEVIQSIE STGYAAVALR DRLLSYGEKN GVAQVAVFRG GVTAEARR W LDISIERLFS RVAIFAQSTS TKRLDRRHHA VDAVVLTTLT PGVAKTLADA RSRRVSAEFW RRPSDVNRHS TEEPQSPAY RQWKESCSGL GDLLISTAAR DSIAVAAPLR LRPTGALHEE TLRAFSEHTV GAAWKGAELR RIVEPEVYAA FLALTDPGGR FLKVSPSED VLPADENRHI VLSDRVLGPR DRVKLFPDDR GSIRVRGGAA YIASFHHARV FRWGSSHSPS FALLRVSLAD L AVAGLLRD GVDVFTAELP PWTPAWRYAS IALVKAVESG DAKQVGWLVP GDELDFGPEG VTTAAGDLSM FLKYFPERHW VV TGFEDDK RINLKPAFLS AEQAEVLRTE RSDRPDTLTE AGEILAQFFP RCWRATVAKV LCHPGLTVIR RTALGQPRWR RGH LPYSWR PWSADPWSGG TP UniProtKB: CRISPR-associated endonuclease, Csn1 family |
-分子 #2: Single guide RNA (102-MER)
| 分子 | 名称: Single guide RNA (102-MER) / タイプ: rna / ID: 2 / コピー数: 1 |
|---|---|
| 由来(天然) | 生物種:  Acidothermus cellulolyticus 11B (バクテリア) Acidothermus cellulolyticus 11B (バクテリア)株: ATCC 43068 / DSM 8971 / 11B |
| 分子量 | 理論値: 34.390289 KDa |
| 配列 | 文字列: (GTP)GUAGGAUGG CAAGAUCCUG GUAUGCUGGG GAGCCUGAAA AGGCUACCUA GCAAGACCCC UUCGUGGGGU CGCAUU CUU CACCCCCUCG CAGCAGCGAG GGGGUUC |
-分子 #3: DNA target strand (5'-D(P*CP*CP*AP*GP*GP*AP*TP*CP*TP*TP*GP*CP*CP*...
| 分子 | 名称: DNA target strand (5'-D(P*CP*CP*AP*GP*GP*AP*TP*CP*TP*TP*GP*CP*CP*AP*TP*CP*CP*TP*AP*CP*CP*TP*CP*T)-3') タイプ: dna / ID: 3 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 7.216654 KDa |
| 配列 | 文字列: (DC)(DC)(DA)(DG)(DG)(DA)(DT)(DC)(DT)(DT) (DG)(DC)(DC)(DA)(DT)(DC)(DC)(DT)(DA)(DC) (DC)(DT)(DC)(DT) |
-分子 #4: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 4 / コピー数: 10 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #5: water
| 分子 | 名称: water / タイプ: ligand / ID: 5 / コピー数: 36 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 60.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: OTHER |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 2.78 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 91324 |
| 初期 角度割当 | タイプ: OTHER |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 4) |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)