+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Tertiary structure of an individual particle of self-folding RNA polymer (particle #099) | ||||||||||||||||||
 マップデータ マップデータ | |||||||||||||||||||
 試料 試料 |
| ||||||||||||||||||
 キーワード キーワード | Single molecule structure / Individual Particle cryo-Electron Tomography / IPET / Cryo-ET / tertiary structure / Structural Flexibility / Self-folding mechanism / RNA origami / RNA | ||||||||||||||||||
| 生物種 | synthetic construct (人工物) | ||||||||||||||||||
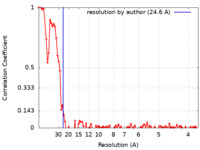
| 手法 | 電子線トモグラフィー法 / クライオ電子顕微鏡法 / 解像度: 25.0 Å | ||||||||||||||||||
 データ登録者 データ登録者 | Liu J / Ren G | ||||||||||||||||||
| 資金援助 |  米国, 5件 米国, 5件
| ||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024タイトル: Non-averaged single-molecule tertiary structures reveal RNA self-folding through individual-particle cryo-electron tomography. 著者: Jianfang Liu / Ewan K S McRae / Meng Zhang / Cody Geary / Ebbe Sloth Andersen / Gang Ren /    要旨: Large-scale and continuous conformational changes in the RNA self-folding process present significant challenges for structural studies, often requiring trade-offs between resolution and ...Large-scale and continuous conformational changes in the RNA self-folding process present significant challenges for structural studies, often requiring trade-offs between resolution and observational scope. Here, we utilize individual-particle cryo-electron tomography (IPET) to examine the post-transcriptional self-folding process of designed RNA origami 6-helix bundle with a clasp helix (6HBC). By avoiding selection, classification, averaging, or chemical fixation and optimizing cryo-ET data acquisition parameters, we reconstruct 120 three-dimensional (3D) density maps from 120 individual particles at an electron dose of no more than 168 eÅ, achieving averaged resolutions ranging from 23 to 35 Å, as estimated by Fourier shell correlation (FSC) at 0.5. Each map allows us to identify distinct RNA helices and determine a unique tertiary structure. Statistical analysis of these 120 structures confirms two reported conformations and reveals a range of kinetically trapped, intermediate, and highly compacted states, demonstrating a maturation folding landscape likely driven by helix-helix compaction interactions. | ||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_25332.map.gz emd_25332.map.gz | 6.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-25332-v30.xml emd-25332-v30.xml emd-25332.xml emd-25332.xml | 12.3 KB 12.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_25332_fsc.xml emd_25332_fsc.xml | 10.8 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_25332.png emd_25332.png | 65.4 KB | ||
| Filedesc metadata |  emd-25332.cif.gz emd-25332.cif.gz | 5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-25332 http://ftp.pdbj.org/pub/emdb/structures/EMD-25332 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25332 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25332 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_25332_validation.pdf.gz emd_25332_validation.pdf.gz | 301.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_25332_full_validation.pdf.gz emd_25332_full_validation.pdf.gz | 301.1 KB | 表示 | |
| XML形式データ |  emd_25332_validation.xml.gz emd_25332_validation.xml.gz | 10.1 KB | 表示 | |
| CIF形式データ |  emd_25332_validation.cif.gz emd_25332_validation.cif.gz | 13.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25332 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25332 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25332 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-25332 | HTTPS FTP |
-関連構造データ
| 関連構造データ | C: 同じ文献を引用 ( |
|---|
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_25332.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_25332.map.gz / 形式: CCP4 / 大きさ: 8 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.88 Å | ||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : RNA Origami 6 Helix Bundle with Clasp (6HBC)
| 全体 | 名称: RNA Origami 6 Helix Bundle with Clasp (6HBC) |
|---|---|
| 要素 |
|
-超分子 #1: RNA Origami 6 Helix Bundle with Clasp (6HBC)
| 超分子 | 名称: RNA Origami 6 Helix Bundle with Clasp (6HBC) / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all 詳細: The RNA was transcribed from linearized DNA template using T7 RNA polymerase purified in house. |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 230 KDa |
-分子 #1: RNA Origami 6 Helix Bundle with Clasp (6HBC)
| 分子 | 名称: RNA Origami 6 Helix Bundle with Clasp (6HBC) / タイプ: rna / ID: 1 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 配列 | 文字列: GGGAGAGUAC UAUUCAGAUG CAGACCGCAA GUUCAGAGCG GUUUGCAUCU AGGGUACGUU UUCGAACGUA UCCUCCGACU AAGUGUAUUC GUAUACUUAG UGCCUUGUGC CUGCUUCGGC AGGCAUGACC CAAAUGUGCC UUUCGGGGCA CAUUUCCGGU CAUCCAAGUU ...文字列: GGGAGAGUAC UAUUCAGAUG CAGACCGCAA GUUCAGAGCG GUUUGCAUCU AGGGUACGUU UUCGAACGUA UCCUCCGACU AAGUGUAUUC GUAUACUUAG UGCCUUGUGC CUGCUUCGGC AGGCAUGACC CAAAUGUGCC UUUCGGGGCA CAUUUCCGGU CAUCCAAGUU CGCUUGGGUG AUGCGGGCGU AUAGGUUCGU CUAUACGUCC GCGUUUUCCG AGAAGAGGUA ACUCGGGAAA CCGGUCCACG UGACAAAGGU AGAGUUACGU GGAGGGAGCA GCUGCAAAGG GAUAAUGCAG UUGCUGGCUG GAUGCCAGAA CUCACGACUG GCAUCUACGG GGAUGGUGCU CUCCCAAUUC UCCAUUUACC GCCGAAUCGA CCCCAACGUG AGAGGGGUCG GUUCCCCGAG CAUAGACCAA UAUCCCAGGU UUAUGCUCCC CAACGCUGGA CGAACUACCU ACGUCUAGCG UUCCGGCAAA UGAGUCAAUA CCUCAGACUU AUUUGCGGUG CCUGAGCCUA AACUGAACAU GGGUUCAGGC AUCUUGGCUC CAGUUCGCUG GAGCCGACGG UAGCGCUGCG UUCGCGCAGU GCUAGGGAGC AUCCGUUUUC GAGCGGAUGC UGGGCGGUUG CCUGUUCGCA GGCAAUCGGG CCUACUCAUG AUUCGUCAUG AGUGGUGACA GCGUGAUGUU CGCAUUACGC UGUCGGGUAG AUGGAGAAUU |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 電子線トモグラフィー法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.3 mg/mL | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| ||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 90 % / チャンバー内温度: 277 K / 装置: LEICA EM GP | ||||||||||||
| 詳細 | In vitro transcribed RNA was purified by size exclusion chromatography and spin concentrated in amicon spin columns. | ||||||||||||
| 切片作成 | その他: NO SECTIONING |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 21 / 平均露光時間: 0.88 sec. / 平均電子線量: 8.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー





































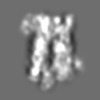
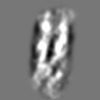




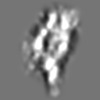
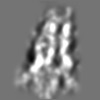





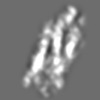






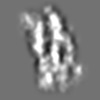


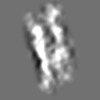
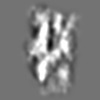


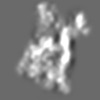

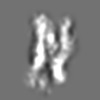
















































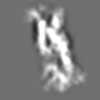



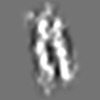


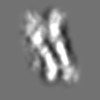

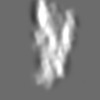



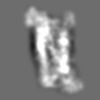
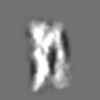





















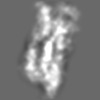


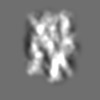





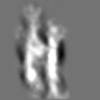



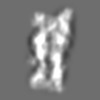




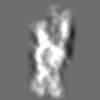

 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)