+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24852 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Extended conformation of daytime state KaiC | |||||||||
 マップデータ マップデータ | Sharpened map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | AAA ATPase / Circadian Oscillator / Kinase / Phosphatase / CIRCADIAN CLOCK PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報regulation of phosphorelay signal transduction system / negative regulation of circadian rhythm / entrainment of circadian clock / protein serine/threonine/tyrosine kinase activity / circadian rhythm / 加水分解酵素; 酸無水物に作用; 酸無水物に作用・細胞または細胞小器官の運動に関与 / non-specific serine/threonine protein kinase / protein serine kinase activity / protein serine/threonine kinase activity / regulation of DNA-templated transcription ...regulation of phosphorelay signal transduction system / negative regulation of circadian rhythm / entrainment of circadian clock / protein serine/threonine/tyrosine kinase activity / circadian rhythm / 加水分解酵素; 酸無水物に作用; 酸無水物に作用・細胞または細胞小器官の運動に関与 / non-specific serine/threonine protein kinase / protein serine kinase activity / protein serine/threonine kinase activity / regulation of DNA-templated transcription / magnesium ion binding / ATP hydrolysis activity / DNA binding / ATP binding / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.8 Å | |||||||||
 データ登録者 データ登録者 | Sandate CR / Swan JA | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2022 ジャーナル: Nat Struct Mol Biol / 年: 2022タイトル: Coupling of distant ATPase domains in the circadian clock protein KaiC. 著者: Jeffrey A Swan / Colby R Sandate / Archana G Chavan / Alfred M Freeberg / Diana Etwaru / Dustin C Ernst / Joseph G Palacios / Susan S Golden / Andy LiWang / Gabriel C Lander / Carrie L Partch /  要旨: The AAA family member KaiC is the central pacemaker for circadian rhythms in the cyanobacterium Synechococcus elongatus. Composed of two hexameric rings of adenosine triphosphatase (ATPase) domains ...The AAA family member KaiC is the central pacemaker for circadian rhythms in the cyanobacterium Synechococcus elongatus. Composed of two hexameric rings of adenosine triphosphatase (ATPase) domains with tightly coupled activities, KaiC undergoes a cycle of autophosphorylation and autodephosphorylation on its C-terminal (CII) domain that restricts binding of clock proteins on its N-terminal (CI) domain to the evening. Here, we use cryogenic-electron microscopy to investigate how daytime and nighttime states of CII regulate KaiB binding on CI. We find that the CII hexamer is destabilized during the day but takes on a rigidified C-symmetric state at night, concomitant with ring-ring compression. Residues at the CI-CII interface are required for phospho-dependent KaiB association, coupling ATPase activity on CI to cooperative KaiB recruitment. Together, these studies clarify a key step in the regulation of cyanobacterial circadian rhythms by KaiC phosphorylation. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24852.map.gz emd_24852.map.gz | 25.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24852-v30.xml emd-24852-v30.xml emd-24852.xml emd-24852.xml | 23.9 KB 23.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_24852_fsc.xml emd_24852_fsc.xml | 8.1 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_24852.png emd_24852.png | 76.3 KB | ||
| Filedesc metadata |  emd-24852.cif.gz emd-24852.cif.gz | 6.8 KB | ||
| その他 |  emd_24852_additional_1.map.gz emd_24852_additional_1.map.gz emd_24852_half_map_1.map.gz emd_24852_half_map_1.map.gz emd_24852_half_map_2.map.gz emd_24852_half_map_2.map.gz | 24.8 MB 24.9 MB 24.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24852 http://ftp.pdbj.org/pub/emdb/structures/EMD-24852 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24852 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24852 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24852.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24852.map.gz / 形式: CCP4 / 大きさ: 27 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Sharpened map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.15 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
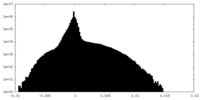
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Unsharpened map
| ファイル | emd_24852_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unsharpened map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
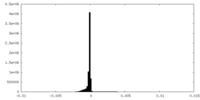
| 密度ヒストグラム |
-ハーフマップ: Half map 2
| ファイル | emd_24852_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
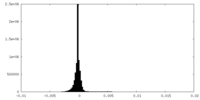
| 密度ヒストグラム |
-ハーフマップ: Half map 1
| ファイル | emd_24852_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map 1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
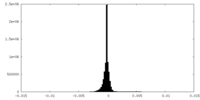
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Compressed state hexamer of nighttime state phosphomutant KaiC (K...
| 全体 | 名称: Compressed state hexamer of nighttime state phosphomutant KaiC (KaiC-EA) |
|---|---|
| 要素 |
|
-超分子 #1: Compressed state hexamer of nighttime state phosphomutant KaiC (K...
| 超分子 | 名称: Compressed state hexamer of nighttime state phosphomutant KaiC (KaiC-EA) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア) |
| 分子量 | 理論値: 350 KDa |
-分子 #1: Circadian clock protein kinase KaiC
| 分子 | 名称: Circadian clock protein kinase KaiC / タイプ: protein_or_peptide / ID: 1 / コピー数: 6 / 光学異性体: LEVO / EC番号: non-specific serine/threonine protein kinase |
|---|---|
| 由来(天然) | 生物種:  Synechococcus elongatus (バクテリア) Synechococcus elongatus (バクテリア) |
| 分子量 | 理論値: 58.084781 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MTSAEMTSPN NNSEHQAIAK MRTMIEGFDD ISHGGLPIGR STLVSGTSGT GKTLFSIQFL YNGIIEFDEP GVFVTFEETP QDIIKNARS FGWDLAKLVD EGKLFILDAS PDPEGQEVVG GFDLSALIER INYAIQKYRA RRVSIDSVTS VFQQYDASSV V RRELFRLV ...文字列: MTSAEMTSPN NNSEHQAIAK MRTMIEGFDD ISHGGLPIGR STLVSGTSGT GKTLFSIQFL YNGIIEFDEP GVFVTFEETP QDIIKNARS FGWDLAKLVD EGKLFILDAS PDPEGQEVVG GFDLSALIER INYAIQKYRA RRVSIDSVTS VFQQYDASSV V RRELFRLV ARLKQIGATT VMTTERIEEY GPIARYGVEE FVSDNVVILR NVLEGERRRR TLEILKLRGT SHMKGEYPFT IT DHGINIF PLGAMRLTQR SSNVRVSSGV VRLDEMCGGG FFKDSIILAT GATGTGKTLL VSRFVENACA NKERAILFAY EES RAQLLR NAYSWGMDFE EMERQNLLKI VCAYPESAGL EDHLQIIKSE INDFKPARIA IDSLSALARG VSNNAFRQFV IGVT GYAKQ EEITGLFTNT SDQFMGAHSI TDSHIAEITD TIILLQYVEI RGEMSRAINV FKMRGSWHDK AIREFMISDK GPDIK DSFR NFERIISGSP TRITVDEKSE LSRIVRGVQE KGPES UniProtKB: Circadian clock oscillator protein KaiC |
-分子 #2: ADENOSINE-5'-TRIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-TRIPHOSPHATE / タイプ: ligand / ID: 2 / コピー数: 6 / 式: ATP |
|---|---|
| 分子量 | 理論値: 507.181 Da |
| Chemical component information |  ChemComp-ATP: |
-分子 #3: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 3 / コピー数: 12 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #4: ADENOSINE-5'-DIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-DIPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 6 / 式: ADP |
|---|---|
| 分子量 | 理論値: 427.201 Da |
| Chemical component information |  ChemComp-ADP: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 6 mg/mL | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 構成要素:
| |||||||||||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / メッシュ: 300 / 支持フィルム - 材質: GRAPHENE / 支持フィルム - トポロジー: CONTINUOUS 詳細: Graphene-coated grids were made hydrophilic via treatment by UV/ozone cleaner. | |||||||||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 95 % / チャンバー内温度: 277.15 K / 装置: HOMEMADE PLUNGER 詳細: Grids with applied sample were manually blotted with filter paper (Whatman No.1) for 3 seconds in a 4 C cold room before plunge freezing in liquid ethane cooled by liquid nitrogen.. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TALOS ARCTICA |
|---|---|
| 温度 | 最低: 70.0 K / 最高: 70.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3710 pixel / デジタル化 - サイズ - 縦: 3838 pixel / デジタル化 - 画像ごとのフレーム数: 1-62 / 撮影したグリッド数: 1 / 実像数: 1541 / 平均露光時間: 6.2 sec. / 平均電子線量: 40.3 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 70.0 µm / 最大 デフォーカス(補正後): -2.0 µm / 最小 デフォーカス(補正後): -0.5 µm / 倍率(補正後): 43478 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.0 µm / 最小 デフォーカス(公称値): -0.5 µm / 倍率(公称値): 36000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Talos Arctica / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)