+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-24610 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of RNA-dependent RNA polymerase 2 (RDR2) from Arabidopsis thaliana | |||||||||
 マップデータ マップデータ | EM map for RNA dependent RNA polymerase 2 from Arabidopsis | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | siRNA / epigenetics / plants / RNA polymerase / gene silencing / TRANSCRIPTION | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報siRNA-mediated long-distance post-transcriptional gene silencing / siRNA transcription / DNA/RNA hybrid binding / siRNA processing / defense response to fungus / single-stranded RNA binding / RNA-directed RNA polymerase / RNA-dependent RNA polymerase activity / nucleolus / nucleoplasm ...siRNA-mediated long-distance post-transcriptional gene silencing / siRNA transcription / DNA/RNA hybrid binding / siRNA processing / defense response to fungus / single-stranded RNA binding / RNA-directed RNA polymerase / RNA-dependent RNA polymerase activity / nucleolus / nucleoplasm / nucleus / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.1 Å | |||||||||
 データ登録者 データ登録者 | Fukudome A / Pikaard CS | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Proc Natl Acad Sci U S A / 年: 2021 ジャーナル: Proc Natl Acad Sci U S A / 年: 2021タイトル: Structure and RNA template requirements of RNA-DEPENDENT RNA POLYMERASE 2. 著者: Akihito Fukudome / Jasleen Singh / Vibhor Mishra / Eswar Reddem / Francisco Martinez-Marquez / Sabine Wenzel / Rui Yan / Momoko Shiozaki / Zhiheng Yu / Joseph Che-Yen Wang / Yuichiro Takagi / Craig S Pikaard /  要旨: RNA-dependent RNA polymerases play essential roles in RNA-mediated gene silencing in eukaryotes. In , RNA-DEPENDENT RNA POLYMERASE 2 (RDR2) physically interacts with DNA-dependent NUCLEAR RNA ...RNA-dependent RNA polymerases play essential roles in RNA-mediated gene silencing in eukaryotes. In , RNA-DEPENDENT RNA POLYMERASE 2 (RDR2) physically interacts with DNA-dependent NUCLEAR RNA POLYMERASE IV (Pol IV) and their activities are tightly coupled, with Pol IV transcriptional arrest, induced by the nontemplate DNA strand, somehow enabling RDR2 to engage Pol IV transcripts and generate double-stranded RNAs. The double-stranded RNAs are then released from the Pol IV-RDR2 complex and diced into short-interfering RNAs that guide RNA-directed DNA methylation and silencing. Here we report the structure of full-length RDR2, at an overall resolution of 3.1 Å, determined by cryoelectron microscopy. The N-terminal region contains an RNA-recognition motif adjacent to a positively charged channel that leads to a catalytic center with striking structural homology to the catalytic centers of multisubunit DNA-dependent RNA polymerases. We show that RDR2 initiates 1 to 2 nt internal to the 3' ends of its templates and can transcribe the RNA of an RNA/DNA hybrid, provided that 9 or more nucleotides are unpaired at the RNA's 3' end. Using a nucleic acid configuration that mimics the arrangement of RNA and DNA strands upon Pol IV transcriptional arrest, we show that displacement of the RNA 3' end occurs as the DNA template and nontemplate strands reanneal, enabling RDR2 transcription. These results suggest a model in which Pol IV arrest and backtracking displaces the RNA 3' end as the DNA strands reanneal, allowing RDR2 to engage the RNA and synthesize the complementary strand. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_24610.map.gz emd_24610.map.gz | 98.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-24610-v30.xml emd-24610-v30.xml emd-24610.xml emd-24610.xml | 14.1 KB 14.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_24610_fsc.xml emd_24610_fsc.xml | 11.4 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_24610.png emd_24610.png | 99.2 KB | ||
| Filedesc metadata |  emd-24610.cif.gz emd-24610.cif.gz | 6.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-24610 http://ftp.pdbj.org/pub/emdb/structures/EMD-24610 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24610 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-24610 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_24610_validation.pdf.gz emd_24610_validation.pdf.gz | 539.3 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_24610_full_validation.pdf.gz emd_24610_full_validation.pdf.gz | 538.8 KB | 表示 | |
| XML形式データ |  emd_24610_validation.xml.gz emd_24610_validation.xml.gz | 12.3 KB | 表示 | |
| CIF形式データ |  emd_24610_validation.cif.gz emd_24610_validation.cif.gz | 16.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24610 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24610 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24610 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-24610 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_24610.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_24610.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | EM map for RNA dependent RNA polymerase 2 from Arabidopsis | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.844 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
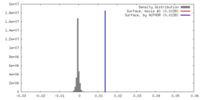
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : RNA-dependent RNA polymerase 2 (RDR2)
| 全体 | 名称: RNA-dependent RNA polymerase 2 (RDR2) |
|---|---|
| 要素 |
|
-超分子 #1: RNA-dependent RNA polymerase 2 (RDR2)
| 超分子 | 名称: RNA-dependent RNA polymerase 2 (RDR2) / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 129 KDa |
-分子 #1: RNA-dependent RNA polymerase 2
| 分子 | 名称: RNA-dependent RNA polymerase 2 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: RNA-directed RNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 133.619828 KDa |
| 組換発現 | 生物種: Insect cell expression vector pTIE1 (その他) |
| 配列 | 文字列: MVSETTTNRS TVKISNVPQT IVADELLRFL ELHLGEDTVF ALEIPTTRDN WKPRDFARVQ FTTLEVKSRA QLLSSQSKLL FKTHNLRLS EAYDDIIPRP VDPRKRLDDI VLTVGFPESD EKRFCALEKW DGVRCWILTE KRRVEFWVWE SGDCYKIEVR F EDIIETLS ...文字列: MVSETTTNRS TVKISNVPQT IVADELLRFL ELHLGEDTVF ALEIPTTRDN WKPRDFARVQ FTTLEVKSRA QLLSSQSKLL FKTHNLRLS EAYDDIIPRP VDPRKRLDDI VLTVGFPESD EKRFCALEKW DGVRCWILTE KRRVEFWVWE SGDCYKIEVR F EDIIETLS CCVNGDASEI DAFLLKLKYG PKVFKRVTVH IATKFKSDRY RFCKEDFDFM WIRTTDFSGS KSIGTSTCFC LE VHNGSTM LDIFSGLPYY REDTLSLTYV DGKTFASAAQ IVPLLNAAIL GLEFPYEILF QLNALVHAQK ISLFAASDME LIK ILRGMS LETALVILKK LHQQSSICYD PVFFVKTQMQ SVVKKMKHSP ASAYKRLTEQ NIMSCQRAYV TPSKIYLLGP ELET ANYVV KNFAEHVSDF MRVTFVEEDW SKLPANALSV NSKEGYFVKP SRTNIYNRVL SILGEGITVG PKRFEFLAFS ASQLR GNSV WMFASNEKVK AEDIREWMGC FRKIRSISKC AARMGQLFSA SRQTLIVRAQ DVEQIPDIEV TTDGADYCFS DGIGKI SLA FAKQVAQKCG LSHVPSAFQI RYGGYKGVIA VDRSSFRKLS LRDSMLKFDS NNRMLNVTRW TESMPCFLNR EIICLLS TL GIEDAMFEAM QAVHLSMLGN MLEDRDAALN VLQKLSGENS KNLLVKMLLQ GYAPSSEPYL SMMLRVHHES QLSELKSR C RILVPKGRIL IGCMDEMGIL EYGQVYVRVT LTKAELKSRD QSYFRKIDEE TSVVIGKVVV TKNPCLHPGD IRVLDAIYE VHFEEKGYLD CIIFPQKGER PHPNECSGGD LDGDQFFVSW DEKIIPSEMD PPMDYAGSRP RLMDHDVTLE EIHKFFVDYM ISDTLGVIS TAHLVHADRD PEKARSQKCL ELANLHSRAV DFAKTGAPAE MPYALKPREF PDFLERFEKP TYISESVFGK L YRAVKSSL AQRKPEAESE DTVAYDVTLE EAGFESFIET AKAHRDMYGE KLTSLMIYYG AANEEEILTG ILKTKEMYLA RD NRRYGDM KDRITLSVKD LHKEAMGWFE KSCEDEQQKK KLASAWYYVT YNPNHRDEKL TFLSFPWIVG DVLLDIKAEN AQR QSVEEK TSGLVSIKLE NLYFQGSAWS HPQFEKGGGS GGGSGGSAWS HPQFEK UniProtKB: RNA-dependent RNA polymerase 2 |
-分子 #2: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 2 / コピー数: 1 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.7 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 |
| グリッド | 前処理 - タイプ: GLOW DISCHARGE / 詳細: unspecified |
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
| 詳細 | The sample was mono disperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) #0 - 撮影したグリッド数: 1 / #0 - 実像数: 6417 / #0 - 平均露光時間: 4.0 sec. / #0 - 平均電子線量: 60.0 e/Å2 / #0 - 詳細: Non-tilted dataset / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) #1 - 撮影したグリッド数: 1 / #1 - 実像数: 4545 / #1 - 平均露光時間: 4.0 sec. / #1 - 平均電子線量: 60.0 e/Å2 / #1 - 詳細: 30 degree titled dataset |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 59242 / 照射モード: OTHER / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.0 µm / 最小 デフォーカス(公称値): -0.8 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 73.71 |
|---|---|
| 得られたモデル |  PDB-7roz: |
 ムービー
ムービー コントローラー
コントローラー













 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)