+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The structure of the human 80S ribosome at 1.9 angstrom resolution reveals the molecular role of chemical modifications and ions in RNA - Focused refinement of the of the 60S subunit | |||||||||||||||
 マップデータ マップデータ | Focused refinement of the 60S ribosome subunit using the multibody job in relion. | |||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード | ribosome / cryo-electron microscopie / post-transcriptional modifications | |||||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 1.9 Å | |||||||||||||||
 データ登録者 データ登録者 | Holvec S / Barchet C / Frechin L / Hazemann I / von Loeffelholz O / Klaholz BP | |||||||||||||||
| 資金援助 |  フランス, 4件 フランス, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2024 ジャーナル: Nat Struct Mol Biol / 年: 2024タイトル: The structure of the human 80S ribosome at 1.9 Å resolution reveals the molecular role of chemical modifications and ions in RNA. 著者: Samuel Holvec / Charles Barchet / Antony Lechner / Léo Fréchin / S Nimali T De Silva / Isabelle Hazemann / Philippe Wolff / Ottilie von Loeffelholz / Bruno P Klaholz /  要旨: The ribosomal RNA of the human protein synthesis machinery comprises numerous chemical modifications that are introduced during ribosome biogenesis. Here we present the 1.9 Å resolution cryo ...The ribosomal RNA of the human protein synthesis machinery comprises numerous chemical modifications that are introduced during ribosome biogenesis. Here we present the 1.9 Å resolution cryo electron microscopy structure of the 80S human ribosome resolving numerous new ribosomal RNA modifications and functionally important ions such as Zn, K and Mg, including their associated individual water molecules. The 2'-O-methylation, pseudo-uridine and base modifications were confirmed by mass spectrometry, resulting in a complete investigation of the >230 sites, many of which could not be addressed previously. They choreograph key interactions within the RNA and at the interface with proteins, including at the ribosomal subunit interfaces of the fully assembled 80S ribosome. Uridine isomerization turns out to be a key mechanism for U-A base pair stabilization in RNA in general. The structural environment of chemical modifications and ions is primordial for the RNA architecture of the mature human ribosome, hence providing a structural framework to address their role in healthy states and in human diseases. #1:  ジャーナル: Biorxiv / 年: 2023 ジャーナル: Biorxiv / 年: 2023タイトル: Structure of the human 80S ribosome at 1.9 angstrom resolution - the molecular role of chemical modifications and ions in RNA 著者: Holvec S / Barchet C / Lechner A / Frechin L / Silva SNTD / Hazemann I / Wolff P / Loeffelholz OV / Klaholz BP | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_18812.map.gz emd_18812.map.gz | 46.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-18812-v30.xml emd-18812-v30.xml emd-18812.xml emd-18812.xml | 16.1 KB 16.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_18812.png emd_18812.png | 55.4 KB | ||
| Filedesc metadata |  emd-18812.cif.gz emd-18812.cif.gz | 4.4 KB | ||
| その他 |  emd_18812_half_map_1.map.gz emd_18812_half_map_1.map.gz emd_18812_half_map_2.map.gz emd_18812_half_map_2.map.gz | 279.9 MB 280.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-18812 http://ftp.pdbj.org/pub/emdb/structures/EMD-18812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18812 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-18812 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_18812_validation.pdf.gz emd_18812_validation.pdf.gz | 794.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_18812_full_validation.pdf.gz emd_18812_full_validation.pdf.gz | 793.8 KB | 表示 | |
| XML形式データ |  emd_18812_validation.xml.gz emd_18812_validation.xml.gz | 18.6 KB | 表示 | |
| CIF形式データ |  emd_18812_validation.cif.gz emd_18812_validation.cif.gz | 22.1 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18812 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18812 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-18812 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_18812.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_18812.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Focused refinement of the 60S ribosome subunit using the multibody job in relion. | ||||||||||||||||||||||||||||||||||||
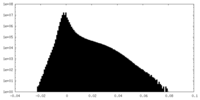
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ |
| ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: Second half-map of the 60S subunit map.
| ファイル | emd_18812_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Second half-map of the 60S subunit map. | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
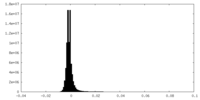
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Human 60S ribosomal subunit
| 全体 | 名称: Human 60S ribosomal subunit |
|---|---|
| 要素 |
|
-超分子 #1: Human 60S ribosomal subunit
| 超分子 | 名称: Human 60S ribosomal subunit / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 1.0 mg/mL |
|---|---|
| 緩衝液 | pH: 7.6 |
| グリッド | モデル: Quantifoil / 材質: COPPER / メッシュ: 200 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: OTHER |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 283.15 K / 装置: FEI VITROBOT MARK IV |
| 詳細 | Purified from HeLa cells. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: FEI FALCON IV (4k x 4k) デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 1 / 実像数: 6528 / 平均露光時間: 3.58 sec. / 平均電子線量: 1.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.1 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: EMDB MAP EMDB ID: |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 1.9 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 382016 |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
 ムービー
ムービー コントローラー
コントローラー








 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)